Espectrometría de masas enfoque para estudiar la estructura de la proteína y las interacciones en liofilizadas Polvos
Summary
Here, we present detailed protocols for solid-state amide hydrogen/deuterium exchange mass spectrometry (ssHDX-MS) and solid-state photolytic labeling mass spectrometry (ssPL-MS) for proteins in solid powders. The methods provide high-resolution information on protein conformation and interactions in the amorphous solid-state, which may be useful in formulation design.
Abstract
Amida de hidrógeno / intercambio de deuterio (ssHDX-MS) y fotolítica etiquetado de la cadena lateral (SSPL-MS), seguido por análisis de espectrometría de masas pueden ser valiosos para la caracterización de formulaciones liofilizadas de proteínas terapéuticas. Etiquetado seguido por la digestión proteolítica adecuada permite que la estructura de proteínas y las interacciones que se asignan con la resolución a nivel de péptido. Dado que la proteína elementos estructurales se estabilizan mediante una red de enlaces químicos de las principales cadenas y cadenas laterales de aminoácidos, un etiquetado específico de los átomos en los residuos de aminoácidos da una idea de la estructura y la conformación de la proteína. En contraste con los métodos de rutina utilizados para estudiar las proteínas en sólidos liofilizados (por ejemplo, FTIR), ssHDX-MS-MS y SSPL proporcionan información cuantitativa y específica de sitio. El grado de incorporación de deuterio y los parámetros cinéticos se puede relacionar con el intercambio rápidamente y lentamente piscinas de amida (N rápido, N lento) y refleja directamente los degree de plegamiento de proteínas y estructura en formulaciones liofilizadas. Etiquetado fotolítico Estable no sufre de respaldo de cambio, una ventaja sobre ssHDX-MS. Aquí, ofrecemos protocolos detallados para ambos ssHDX-MS y SSPL-MS, utilizando la mioglobina (Mb) como una proteína modelo en formulaciones liofilizadas que contienen trehalosa o sorbitol.
Introduction
Medicamentos de proteínas son el sector de más rápido crecimiento de la industria biofarmacéutica y ofrecen nuevos tratamientos prometedores para enfermedades hasta ahora intratables, como los trastornos hormonales, cáncer y enfermedades autoinmunes 1. En 2012, el mercado de productos bioterapéuticos global alcanzó $ 138 mil millones y se espera que llegue a $ 179 mil millones para el año 2018 2. Las proteínas son más grandes y más frágiles que los fármacos de molécula pequeña convencionales y por lo tanto son más susceptibles a muchos tipos de degradación 3. Para asegurar la vida útil y la estabilidad adecuada, fármacos de proteínas se formulan a menudo como liofilizado (es decir, liofilizado) polvos sólidos. Sin embargo, una proteína puede todavía sufrir degradación en el estado sólido, en particular si su estructura nativa no se conserva durante el proceso de liofilización 4,5. Asegurar que la estructura se ha conservado es factible sólo si hay métodos analíticos que pueden sondear conformación de la proteína en el estado sólido con suficient resolución.
Espectroscopía de RMN 6 y cristalografía de rayos X 7 son los métodos comúnmente utilizados de alta resolución para evaluar la estructura de proteínas en solución y los sólidos cristalinos 8. Debido a la naturaleza de los excipientes y los métodos de procesamiento utilizados, las formulaciones de proteínas liofilizadas son generalmente amorfa en vez de cristalina 9. La falta de homogeneidad y el orden microscópico hace que las técnicas mencionadas anteriormente poco práctico para las proteínas en sólidos amorfos. Espectroscopía infrarroja por transformada de Fourier (FTIR) 10, espectroscopia de Raman 11 y la espectroscopia de infrarrojo cercano (NIR) 12 han sido utilizados regularmente por la industria biofarmacéutica para comparar la estructura secundaria de proteínas en polvos liofilizados a la de la estructura de estado de solución nativa. Sin embargo, estos métodos son de baja resolución y sólo pueden proporcionar información sobre los cambios globales en la estructura secundaria. Caracterización estructural de estado sólido utilizando FTIRha mostrado ya sea débil o pobre 13,14 15 correlación con la estabilidad de almacenamiento a largo plazo. Estas limitaciones ponen de relieve la necesidad de métodos de alta resolución conveniente para identificar perturbaciones estructurales de proteínas en el estado sólido.
Etiquetado químico junto con la proteólisis y el análisis de espectrometría de masas ha surgido como un enfoque poderoso para el seguimiento de la estructura de proteínas y las interacciones moleculares en solución acuosa. En el desarrollo farmacéutico, HDX-MS se ha utilizado para el mapeo de epítopo en las interacciones antígeno-anticuerpo 16,17, para mapear las interacciones receptor-drogas 18, para vigilar los efectos de las modificaciones post-traduccionales en la conformación de los fármacos proteicos 19, y comparar variación de lote a lote en el desarrollo de los biosimilares 20. Del mismo modo, los ligandos fotoactivables se han utilizado para identificar dianas de fármacos y para determinar la afinidad de unión y la especificidad de las interacciones fármaco-receptor 21,22. Para enviarxtend la aplicación de estos métodos a formulaciones liofilizadas, nuestro grupo ha desarrollado la espectrometría de masas de intercambio de deuterio hidrógeno en estado sólido (ssHDX-MS) y espectrometría de masas etiquetado fotolítico de estado sólido (SSPL-MS) para el estudio de las conformaciones de proteínas y las interacciones de excipiente en muestras liofilizadas con alta resolución.
En tanto ssHDX-MS-MS y SspI, la proteína está marcada en condiciones de reacción ideales en sólidos liofilizados, y las muestras se reconstituye a continuación, y se analizó mediante espectrometría de masas con o sin digestión proteolítica. ssHDX-MS proporciona información sobre la exposición principal cadena de vapor de deuterio, mientras SSPL-MS proporciona información sobre el medio ambiente de las cadenas laterales (Figura 1). Los dos métodos de este modo pueden proporcionar información complementaria sobre la conformación de proteínas en el estado sólido. Aquí, ofrecemos un protocolo general para el estudio de las proteínas en los sólidos liofilizados utilizando ssHDX-MS y SSPL-MS (Figura 2), utilizando como Mbuna proteína modelo. Mostramos la capacidad de los dos métodos para distinguir las diferencias en las formulaciones con dos excipientes diferentes.
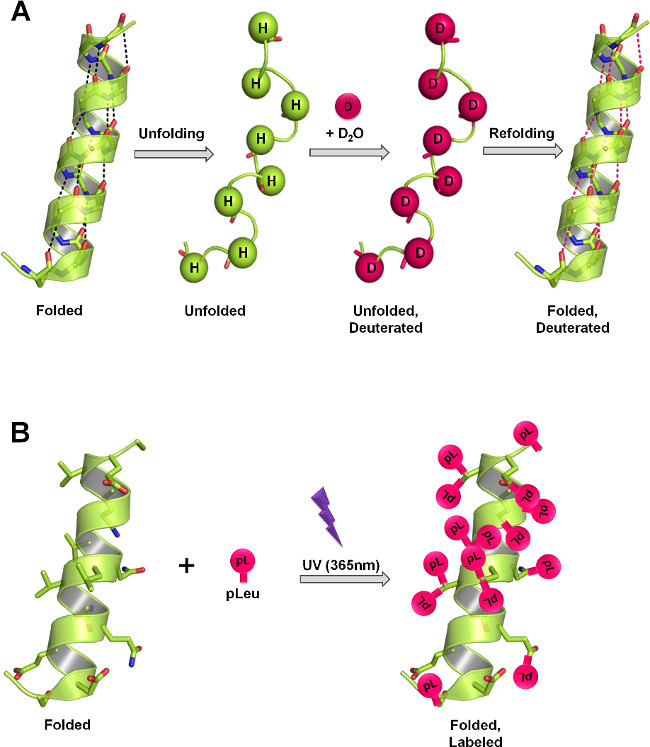
Figura 1:. SsHDX y SSPL estructura de la proteína medida en sólidos liofilizados a través de diferentes mecanismos de etiquetado (A) En HDX, la columna vertebral amida hidrógenos intercambio con deuterio como una función de la estructura de proteínas y D 2 O accesibilidad. En el estado sólido, la velocidad y el grado de intercambio de deuterio dependen del nivel de D 2 O sorción, la movilidad de proteínas (despliegue y replegamiento de eventos) y la naturaleza de los excipientes presentes en la matriz sólida. (B) En PL, la irradiación UV a 365 nm inicia la formación de un carbeno intermedio reactivo del grupo funcional diazirina de pleu del Sáhel y se inserta de forma no específica a cualquier enlace XH (X = cualquier átomo), o added a través de un enlace C = C en sus inmediaciones. En el estado sólido, la velocidad y extensión de etiquetado dependen de la concentración local del agente de marcaje, el tiempo de irradiación, la estructura de proteínas y la naturaleza de los excipientes presentes en la matriz sólida. Los paneles A y B muestran el etiquetado teórico máximo que puede ocurrir en la columna vertebral y las cadenas laterales, respectivamente, en la proteína.
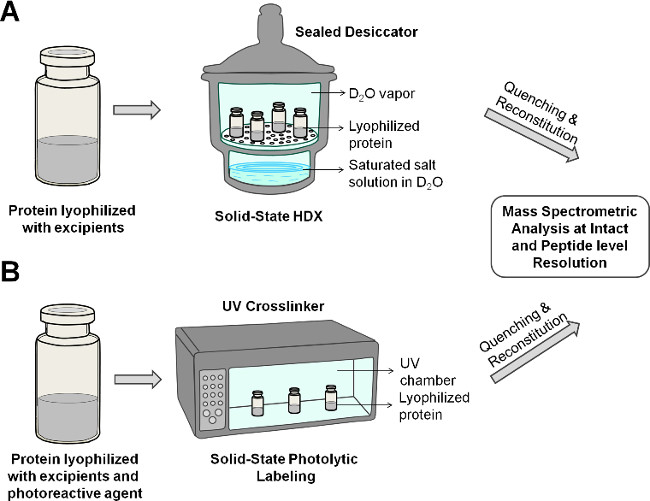
Figura 2: muestra de estado sólido esquemática HDX-MS (A) y PL-MS (B) para la proteína en la formulación liofilizada.
Protocol
Representative Results
Discussion
Varios estudios han sugerido que el entorno local en muestras liofilizadas afecta a la degradación de proteínas 5,29,30. Sin embargo, establecer una relación directa entre la estructura de la proteína y la estabilidad en el estado sólido no ha sido posible debido a la falta de métodos analíticos de alta resolución. La aplicación de métodos de alta resolución existentes, tales como HDX y PL a polvos liofilizados requiere la modificación de los protocolos de la solución y la interpretación de los datos cuidado. HDX-MS y PL-MS han sido adoptados sucesivamente para monitorear conformaciones de las proteínas en el estado sólido. Los resultados presentados aquí y en otros lugares 27,28,31-33 han demostrado la capacidad de estos métodos para controlar la conformación de proteínas con alta resolución en el entorno sólido. Aunque los pasos críticos en el análisis de los datos no varían de etiquetado en solución 34-36, se requieren consideraciones importantes durante la instalación experimental y la interpretación de datos para químico de estado sólidoetiquetado cal.
La selección del reactivo de marcaje debe basarse en el tamaño y el mecanismo de etiquetado. El pequeño tamaño de deuterio permite que el esqueleto peptídico a palpar fácilmente, mientras que el tamaño relativamente grande de pleu del Sáhel limita etiquetado a las cadenas laterales. Tanto ssHDX y SSPL no muestran ninguna preferencia por cualquier aminoácido, por lo que el etiquetado depende sólo de la columna vertebral y de la cadena lateral de la exposición a la matriz. Para sondear con eficacia conformaciones de proteínas en estado sólido, los factores externos que afectan el proceso de etiquetado deben ser cuidadosamente controlados. La cantidad total y la distribución espacial de agente de marcaje en los sólidos liofilizados es diferente de soluciones acuosas.
En ssHDX, la cantidad de D 2 O en la matriz sólida puede afectar la tasa de desplegamiento de la proteína (o despliegue parcial), el replegamiento, y el intercambio de deuterio. Este no es el caso con solución HDX, en el que la muestra de proteína normalmente se diluye con un volumen amplio de D 2 O.Detección cuidadosa de los efectos de la hidratación en la tasa de ssHDX puede informar a la selección de las condiciones ideales de SR. Para controlar la velocidad de absorción de humedad y evitar el colapso del polvo en formulaciones que contienen excipientes higroscópicos (por ejemplo, sacarosa y trehalosa), ssHDX puede llevarse a cabo bajo condiciones de refrigeración (2-8 ° C). Nuestro estudio anterior sobre los efectos de hidratación mostró velocidad y el grado de intercambio aumentó con el aumento en el contenido de humedad, como se esperaba. En gran parte de nuestro trabajo, una HR intermedio del 43% a los 5 ° C ha demostrado ser ideal para distinguir formulaciones en un tiempo razonable 24. La reacción se lleva a cabo normalmente hasta que se alcanza una meseta. Esto asegura que la sorción de humedad y la difusión en el sólido no controlan la tasa de HDX. El uso de tamaños de muestra pequeños sólidos con un volumen de pre-liofilización de ≤2 ml también ayuda a asegurar que D 2 O sorción de vapor es esencialmente completa al comienzo del período de cambio. Aunque ssHDX-MS ofreceinformación cuantitativa sobre la conformación de la proteína en estado sólido, hay ciertas condiciones en que la interpretación de los datos no puede basarse exclusivamente en el estudio ssHDX solo. Es posible que la absorción de deuterio disminución observada en una muestra (en comparación con el control) puede ser debido a la mayor retención de la estructura de la proteína o la cantidad significativa de agregados de proteínas presentes en la muestra. En tal caso, la interpretación de los datos ssHDX requiere los resultados de otros métodos complementarios. Se observó ensanchamiento de los picos en los espectros de masas deuterado para varias formulaciones Mb 27,28. Esto podría ser debido a varios factores como la presencia de la población de proteína parcialmente desplegada, la heterogeneidad espacial en la muestra, o los gradientes espaciales de la concentración de D 2 O. Sin embargo, estos factores no se distinguían en ssHDX-MS y necesita más investigación.
Como SSPL-MS es relativamente nueva en comparación con otros métodos, el aprendizaje continuo absus aplicaciones y limitaciones que se requiere. En SSPL, el foto-reticulante se liofiliza con la proteína. La falta de humedad limita la movilidad de los componentes dentro de la matriz sólida, y la relajación estructural parcial que puede ocurrir con sorción de humedad en ssHDX no es un fenómeno en SSPL. Esto limita el etiquetado en SSPL a la vecindad inmediata de la foto-reticulante. Sin embargo, a diferencia de HDX-MS, MS / MS análisis de la proteína covalentemente etiquetados puede proporcionar información estructural a nivel de residuos. Desde etiquetado SSPL es covalente e irreversible, de vuelta de cambio no se produce y se puede preparar muestras y se analizaron sin la preocupación por la pérdida de la etiqueta. Para facilitar la difusión de agente de marcaje y mejorar la eficiencia de etiquetado en matriz sólida, SSPL se puede realizar con el aumento de% de humedad relativa. pleu del Sáhel absorción también se puede mejorar mediante el aumento de la concentración de agente fotorreactivo. La relación molar de proteína para pleu del Sáhel puede variarse según se desee. En general, un exceso molar de 100x pleu del Sáhel a protein asegurará un etiquetado adecuado. Sin embargo, la alta concentración pleu del Sáhel puede resultar en la pérdida de la estructura terciaria de proteínas en la matriz sólida. Por lo tanto, además de la cinética de etiquetado y composición de la formulación, la selección de la concentración de pleu del Sáhel debe también estar basada en el mantenimiento de la integridad estructural de la proteína. Como pleu del Sáhel etiquetas no selectiva XH (donde X = C, N, O), es posible que los excipientes con sitios de etiquetado similares pueden afectar en gran medida el nivel de etiquetado de proteínas. La interferencia de excipientes en la disponibilidad de pleu del Sáhel para el etiquetado de proteínas aún no se ha caracterizado. Se sabe que el carbeno generada a partir de la activación no se diazirina residuo específico, sin embargo un estudio informa sesgo hacia Asp y Glu 36. Mientras que es bueno para aprender acerca de las interacciones de residuos específica, la información de péptido nivel también es útil y se puede utilizar para diseñar excipientes para bloquear regiones con alta exposición de la matriz en el estado sólido. SSPL-MS proporciona información cualitativa detallada, sin embargodatos cuantitativos debe ser obtenida y métricas robustas necesita ser desarrollado para analizar las diferencias de formulación a través de una variedad de sistemas liofilizados.
El uso de una etiqueta de residuo específico combinado con el análisis MS / MS se puede mejorar aún más la resolución al nivel de aminoácidos. Reactivos de etiquetado tales como 2,3-butanodiona para etiquetar Arg, N hidroxisuccinimida derivados de Lys y N derivados -alkylmaleimide para Cys se puede utilizar para mapear con precisión las interacciones moleculares en polvo liofilizado. Sin embargo, estos reactivos son dependiente del pH y las reacciones pueden no ser tan bien controlados como el etiquetado fotolítica en estado sólido. Un enfoque alternativo es incorporar el foto-reticulante en la secuencia de proteína con el uso de líneas de células auxotróficas, mutagénesis dirigida al sitio o derivatización de la cadena lateral.
Nuestros estudios previos ssHDX-MS-MS y SSPL han demostrado que el etiquetado de proteínas depende de la naturaleza y cantidad de excipientesutilizado 24,27,28,31-33,37,38. ssHDX-MS de Mb coliofilizado con clorhidrato de guanidina (Gdn.HCl) mostraron una mayor captación de deuterio que Mb coliofilizado con bajo peso molecular que no contienen azúcar 32. En un estudio SSPL-MS separada, Mb coliofilizado con Gdn.HCl mostró una mayor protección de etiquetado fotolítico de Mb con sacarosa 33. Además, las mediciones cuantitativas de ssHDX-MS han sido altamente correlacionado con la estabilidad de la proteína durante el almacenamiento a largo plazo 28. Estos estudios sugieren que ssHDX o SSPL de la proteína refleja la medida de la retención estructural de la proteína en polvo liofilizado. Creemos que la retención de la estructura secundaria en polvos liofilizados proporciona un entorno favorable para el etiquetado de cadena lateral con pleu del Sáhel y protección de hidrógeno amida de intercambio de deuterio. Sin embargo, la comparación detallada del contenido informativo de estos métodos se debe realizar en el futuro. Aunque el establecimiento de la utilidad de ssHDX-MS-MS y SSPLcomo herramienta de detección formulación finalmente exigir que se aplica a muchas proteínas, los resultados de nuestros estudios recientes apoya su adopción más amplia. Con un mayor desarrollo, se espera que estos métodos son ampliamente útil para caracterizar las formulaciones de proteínas de estado sólido en la industria biofarmacéutica.
Divulgazioni
The authors have nothing to disclose.
Acknowledgements
The authors gratefully acknowledge financial support from NIH R01 GM085293 (PI: E. M. Topp) and from the College of Pharmacy at Purdue University.
Materials
| Name of Material/ Equipment | Company | Catalog Number | Comments/Description |
| Equine myoglobin | Sigma-Aldrich | M0630-5G | |
| D-(+)-Trehalose dihydrate | Sigma Aldrich | #T9531 | |
| D-Sorbitol | Sigma Aldrich | #240850 | |
| L-Photo-leucine | Thermo Scientific | #22610 | |
| Potassium phosphate monobasic | Sigma-Aldrich | #P0662 | |
| Potassium phosphate dibasic | Sigma-Aldrich | #P3786 | |
| Deuterium Oxide | Cambridge Isotope Laboratories | #DLM-4-PK | Alternate (Cat. No.: 151882, Sigma-Aldrich) |
| Immobilized pepsin | Applied Biosystems | #2-3132-00 | |
| Trypsin | Promega | #V511A | Chymotrypsin (Cat. No.: #V1062, Promega) can be additionally used |
| Water, Optima LC/MS grade | Fisher Chemical | #7732-18-5 | |
| Acetonitrile | Sigma-Aldrich | #34998 | |
| Formic acid | Thermo Scientific | #28905 | |
| ESI-TOF Calibrant | Agilent Technologies | #G1969-85000 | Highly flammable liquid |
| Protein microtrap | Michrom Bioresources | TR1/25108/03 | |
| Peptide microtrap | Michrom Bioresources | TR1/25109/02 | |
| Analytical column | Agilent Technologies | Zorbax 300SB-C18 | |
| Freeze dryer | VirTis AdVantage Plus | ||
| Stratalinker equipped with five 365 nm lamps | Stratagene Corp. | Stratalinker 2400 | |
| HPLC | Agilent Technologies | 1200 series LC | Refrigerated LC system for HDX-MS |
| ESI-qTOF MS | Agilent Technologies | 6520 qTOF | |
| HDExaminer (HDX-MS data analysis software) | Sierra Analytics | http://www.massspec.com/HDExaminer.html |
Riferimenti
- Lawrence, S. Billion dollar babies–biotech drugs as blockbusters. Nat. Biotechnol. 25 (4), 380-382 (2007).
- . . Global Markets and Manufacturing Technologies for Protein Drugs. , BIO021D (2013).
- Lai, M. C., Topp, E. M. Solid-state chemical stability of proteins and peptides. J. Pharm. Sci. 88 (5), 489-500 (1999).
- Carpenter, J. F., Pikal, M. J., Chang, B. S., Randolph, T. W. Rational design of stable lyophilized protein formulations: some practical advice. Pharm. Res. 14 (8), 969-975 (1997).
- Carpenter, J. F., Chang, B. S., Garzon-Rodriguez, W., Randolph, T. W. Rational design of stable lyophilized protein formulations: theory and practice. Pharm. Biotechnol. 13, 109-133 (2002).
- Wüthrich, K. Protein structure determination in solution by NMR spectroscopy. J. Biol. Chem. 265 (36), 22059-22062 (1990).
- Ilari, A., Savino, C. Protein structure determination by x-ray crystallography. Methods. Mol. Biol. 452, 63-87 (2008).
- Brunger, A. T. X-ray crystallography and NMR reveal complementary views of structure and dynamics. Nat. Struct. Biol. 4, 862-865 (1997).
- Yu, L. Amorphous pharmaceutical solids: preparation, characterization and stabilization. Adv Drug. Deliv. Rev. 48 (1), 27-42 (2001).
- Manning, M. C. Use of infrared spectroscopy to monitor protein structure and stability. Expert. Rev. Proteomics. 2 (5), 731-743 (2005).
- Grohganz, H., Gildemyn, D., Skibsted, E., Flink, J. M., Rantanen, J. Rapid solid-state analysis of freeze-dried protein formulations using NIR and Raman spectroscopies. J. Pharm. Sci. 100 (7), 2871-2875 (2011).
- Bai, S., Nayar, R., Carpenter, J. F., Manning, M. C. Noninvasive determination of protein conformation in the solid state using near infrared (NIR) spectroscopy. J. Pharm. Sci. 94 (9), 2030-2038 (2005).
- Pikal, M. J., et al. Solid state chemistry of proteins: II. The correlation of storage stability of freeze-dried human growth hormone (hGH) with structure and dynamics in the glassy solid. J. Pharm. Sci. 97 (12), 5106-5121 (2008).
- Wang, B., Tchessalov, S., Cicerone, M. T., Warne, N. W., Pikal, M. J. Impact of sucrose level on storage stability of proteins in freeze-dried solids: II. Correlation of aggregation rate with protein structure and molecular mobility. J. Pharm. Sci. 98 (9), 3145-3166 (2009).
- Schule, S., Friess, W., Bechtold-Peters, K., Garidel, P. Conformational analysis of protein secondary structure during spray-drying of antibody/mannitol formulations. Eur. J. Pharm. Biopharm. 65 (1), 1-9 (2007).
- Baerga-Ortiz, A., Hughes, C. A., Mandell, J. G., Komives, E. A. Epitope mapping of a monoclonal antibody against human thrombin by H/D-exchange mass spectrometry reveals selection of a diverse sequence in a highly conserved protein. Protein. Sci. 11 (6), 1300-1308 (2002).
- Coales, S. J., Tuske, S. J., Tomasso, J. C., Hamuro, Y. Epitope mapping by amide hydrogen/deuterium exchange coupled with immobilization of antibody, on-line proteolysis, liquid chromatography and mass spectrometry. Rapid. Commun. Mass. Spectrom. 23 (5), 639-647 (2009).
- Pacholarz, K. J., Garlish, R. A., Taylor, R. J., Barran, P. E. Mass spectrometry based tools to investigate protein-ligand interactions for drug discovery. Chem. Soc. Rev. 41 (11), 4335-4355 (2012).
- Houde, D., Peng, Y., Berkowitz, S. A., Engen, J. R. Post-translational modifications differentially affect IgG1 conformation and receptor binding. Mol. Cell. Proteomics. 9 (8), 1716-1728 (2010).
- Houde, D., Berkowitz, S. A., Engen, J. R. The utility of hydrogen/deuterium exchange mass spectrometry in biopharmaceutical comparability studies. J. Pharm. Sci. 100 (6), 2071-2086 (2011).
- Dorman, G., Prestwich, G. D. Using photolabile ligands in drug discovery and development. Trends. Biotechnol. 18 (2), 64-77 (2000).
- Robinette, D., Neamati, N., Tomer, K. B., Borchers, C. H. Photoaffinity labeling combined with mass spectrometric approaches as a tool for structural proteomics. Expert. Rev. Proteomics. 3 (4), 399-408 (2006).
- Greenspan, L. Humidity fixed points of binary saturated aqueous solutions. Journal of Research of the National Bureau of Standards. 81A (1), 8 (1977).
- Sophocleous, A. M., Zhang, J., Topp, E. M. Localized hydration in lyophilized myoglobin by hydrogen-deuterium exchange mass spectrometry. 1. Exchange mapping. Mol. Pharm. 9 (4), 718-726 (2012).
- Keppel, T. R., Jacques, M. E., Young, R. W., Ratzlaff, K. L., Weis, D. D. An efficient and inexpensive refrigerated LC system for H/D exchange mass spectrometry. J. Am. Soc. Mass. Spectrom. 22 (8), 1472-1476 (2011).
- Gasteiger, E., et al. ExPASy: The proteomics server for in-depth protein knowledge and analysis. Nucleic. Acids. Res. 31 (13), 3784-3788 (2003).
- Sophocleous, A. M., Topp, E. M. Localized hydration in lyophilized myoglobin by hydrogen-deuterium exchange mass spectrometry. 2. Exchange kinetics. Mol. Pharm. 9 (4), 727-733 (2012).
- Moorthy, B. S., Schultz, S. G., Kim, S. G., Topp, E. M. Predicting Protein Aggregation during Storage in Lyophilized Solids Using Solid State Amide Hydrogen/Deuterium Exchange with Mass Spectrometric Analysis (ssHDX-MS). Mol. Pharm. 11 (6), 1869-1879 (2014).
- Wang, W. Lyophilization and development of solid protein pharmaceuticals. Int. J. Pharm. 203 (1-2), 1-60 (2000).
- Sarciaux, J. M., Mansour, S., Hageman, M. J., Nail, S. L. Effects of buffer composition and processing conditions on aggregation of bovine IgG during freeze-drying. J. Pharm. Sci. 88 (12), 1354-1361 (1999).
- Li, Y., Williams, T. D., Schowen, R. L., Topp, E. M. Characterizing protein structure in amorphous solids using hydrogen/deuterium exchange with mass spectrometry. Anal. Biochem. 366 (1), 18-28 (2007).
- Sinha, S., Li, Y., Williams, T. D., Topp, E. M. Protein conformation in amorphous solids by FTIR and by hydrogen/deuterium exchange with mass spectrometry. Biophys. J. 95 (12), 5951-5961 (2008).
- Iyer, L. K., Moorthy, B. S., Topp, E. M. Photolytic labeling to probe molecular interactions in lyophilized powders. Mol. Pharm. 10 (12), 4629-4639 (2013).
- Hentze, N., Mayer, M. P. Analyzing protein dynamics using hydrogen exchange mass spectrometry. J. Vis. Exp. (81), e50839 (2013).
- Kaltashov, I. A., Bobst, C. E., Abzalimov, R. R. H/D exchange and mass spectrometry in the studies of protein conformation and dynamics: is there a need for a top-down approach. Anal. Chem. 81 (19), 7892-7899 (2009).
- Jumper, C. C., Schriemer, D. C. Mass spectrometry of laser-initiated carbene reactions for protein topographic analysis. Anal. Chem. 83 (8), 2913-2920 (2011).
- Li, Y., Williams, T. D., Topp, E. M. Effects of excipients on protein conformation in lyophilized solids by hydrogen/deuterium exchange mass spectrometry. Pharm. Res. 25 (2), 259-267 (2008).
- Li, Y., Williams, T. D., Schowen, R. L., Topp, E. M. Trehalose and calcium exert site-specific effects on calmodulin conformation in amorphous solids. Biotechnol. Bioeng. 97 (6), 1650-1653 (2007).

