कार्यात्मक गैर-कोडिंग आनुवंशिक वेरिएंट के लिए स्क्रीनिंग का उपयोग electrophoretic गतिशीलता शिफ्ट परख (EMSA) और डीएनए आत्मीयता वर्षा परख (DAPA)
Summary
We present a strategic plan and protocol for identifying non-coding genetic variants affecting transcription factor (TF) DNA binding. A detailed experimental protocol is provided for electrophoretic mobility shift assay (EMSA) and DNA affinity precipitation assay (DAPA) analysis of genotype-dependent TF DNA binding.
Abstract
Population and family-based genetic studies typically result in the identification of genetic variants that are statistically associated with a clinical disease or phenotype. For many diseases and traits, most variants are non-coding, and are thus likely to act by impacting subtle, comparatively hard to predict mechanisms controlling gene expression. Here, we describe a general strategic approach to prioritize non-coding variants, and screen them for their function. This approach involves computational prioritization using functional genomic databases followed by experimental analysis of differential binding of transcription factors (TFs) to risk and non-risk alleles. For both electrophoretic mobility shift assay (EMSA) and DNA affinity precipitation assay (DAPA) analysis of genetic variants, a synthetic DNA oligonucleotide (oligo) is used to identify factors in the nuclear lysate of disease or phenotype-relevant cells. For EMSA, the oligonucleotides with or without bound nuclear factors (often TFs) are analyzed by non-denaturing electrophoresis on a tris-borate-EDTA (TBE) polyacrylamide gel. For DAPA, the oligonucleotides are bound to a magnetic column and the nuclear factors that specifically bind the DNA sequence are eluted and analyzed through mass spectrometry or with a reducing sodium dodecyl sulfate polyacrylamide gel electrophoresis (SDS-PAGE) followed by Western blot analysis. This general approach can be widely used to study the function of non-coding genetic variants associated with any disease, trait, or phenotype.
Introduction
अनुक्रमण और जीनोम चौड़ा संघ स्टडीज (GWAS), उम्मीदवार ठिकाना अध्ययन सहित जीनोटाइपिंग आधारित अध्ययन, और गहरी अनुक्रमण अध्ययन, कई आनुवंशिक वेरिएंट कि सांख्यिकीय एक बीमारी, लक्षण, या phenotype के साथ जुड़े रहे हैं की पहचान की है। जल्दी भविष्यवाणियों के विपरीत, इन वेरिएंट (85-93%) की सबसे अधिक गैर-कोडिंग क्षेत्रों में स्थित हैं और प्रोटीन 1,2 के अमीनो एसिड अनुक्रम बदल नहीं है। इन गैर-कोडिंग वेरिएंट के समारोह की व्याख्या करना और उन्हें जुड़े रोग से जोड़ने के जैविक तंत्र का निर्धारण करने, विशेषता, या phenotype चुनौतीपूर्ण 3-6 साबित कर दी है। जीन अभिव्यक्ति – हम एक सामान्य रणनीति आणविक तंत्र है कि एक महत्वपूर्ण मध्यवर्ती phenotype के लिए वेरिएंट लिंक की पहचान करने के लिए विकसित किया है। इस पाइप लाइन के लिए विशेष रूप से टीएफ आनुवंशिक वेरिएंट द्वारा बाध्यकारी के मॉडुलन की पहचान करने के लिए बनाया गया है। इस रणनीति के कम्प्यूटेशनल दृष्टिकोण और भविष्यवाणी करने के उद्देश्य से आणविक जीव विज्ञान तकनीक को जोड़ती हैसिलिको में उम्मीदवार वेरिएंट की जैविक प्रभाव, और इन भविष्यवाणियों को सत्यापित अनुभव से (चित्रा 1)।
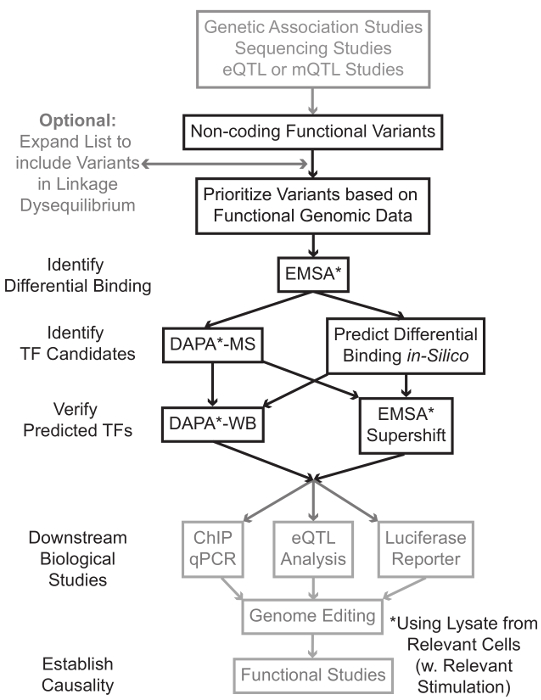
चित्रा 1:।। कि इस पांडुलिपि में विस्तृत ग्रे में छायांकित हैं के साथ जुड़े प्रोटोकॉल में शामिल नहीं हैं गैर-कोडिंग आनुवंशिक वेरिएंट कदम के विश्लेषण के लिए सामरिक दृष्टिकोण यह आंकड़ा का एक बड़ा संस्करण देखने के लिए यहां क्लिक करें।
कई मामलों में, यह वेरिएंट की सूची का विस्तार प्रत्येक सांख्यिकीय रूप से जुड़े संस्करण के साथ उच्च लिंकेज-असंतुलन (एलडी) में उन सभी को शामिल करने से शुरू करने के लिए महत्वपूर्ण है। एलडी दो अलग गुणसूत्र पदों पर alleles की गैर यादृच्छिक एसोसिएशन, जो आर 2 आंकड़ा 7 से मापा जा सकता का एक उपाय है। आर 2 लिन का एक उपाय हैKage दो वेरिएंट के बीच एक आर 2 = 1 denoting सही लिंकेज के साथ दो वेरिएंट के बीच असंतुलन। उच्च एलडी में alleles पैतृक आबादी भर में गुणसूत्र पर सह-अलग पाए जाते हैं। वर्तमान जीनोटाइपिंग सरणियों मानव जीनोम में सभी ज्ञात वेरिएंट में शामिल नहीं है। इसके बजाय, वे मानव जीनोम के भीतर एलडी शोषण और ज्ञात वेरिएंट कि एलडी 8 के एक विशेष क्षेत्र के भीतर अन्य वेरिएंट के लिए परदे के पीछे के रूप में कार्य की एक सबसेट शामिल हैं। इस प्रकार, किसी भी जैविक परिणाम के बिना एक संस्करण एक विशेष रोग के साथ जुड़ा हो सकता है, क्योंकि यह कारण संस्करण-एक सार्थक जैविक प्रभाव के साथ संस्करण के साथ एलडी में है। Procedurally, इसे बदलने के लिए 1,000 जीनोम की नवीनतम रिलीज plink 10,11, पूरे जीनोम एसोसिएशन के विश्लेषण के लिए एक खुला स्रोत उपकरण के साथ संगत द्विआधारी फाइलों में 9 संस्करण कॉल फ़ाइलें (वीसीएफ) परियोजना की सिफारिश की है। बाद में, एलडी आर 2> 0.8 के साथ अन्य सभी आनुवंशिक वेरिएंट प्रत्येक इनपुट आनुवंशिक VA के साथरियांत उम्मीदवार के रूप में पहचाना जा सकता है। यह इस कदम उदाहरण के लिए उचित संदर्भ आबादी का उपयोग करने के लिए महत्वपूर्ण है अगर एक संस्करण यूरोपीय वंश के विषयों, इसी वंश के विषयों से डेटा एलडी विस्तार के लिए इस्तेमाल किया जाना चाहिए में पहचान की थी।
एलडी विस्तार अक्सर उम्मीदवार वेरिएंट के दर्जनों में परिणाम है, और यह संभावना है कि केवल इन में से एक छोटा सा अंश रोग तंत्र के लिए योगदान करते हैं। अक्सर, यह प्रयोगात्मक व्यक्तिगत रूप से इन वेरिएंट के प्रत्येक जांच करने के लिए अव्यवहार्य है। इसलिए यह वेरिएंट को प्राथमिकता के लिए एक फिल्टर के रूप में सार्वजनिक रूप से उपलब्ध कार्यात्मक जीनोमिक डेटासेट के हजारों लाभ उठाने के लिए उपयोगी है। उदाहरण के लिए, सांकेतिक शब्दों में संघ के 12 चिप seq प्रयोगों TFS के बंधन का वर्णन है और सह कारकों, और हिस्टोन के निशान के हजारों संदर्भों की एक विस्तृत श्रृंखला में, क्रोमेटिन पहुंच डेटा के साथ प्रौद्योगिकियों से इस तरह के DNase-सेक 13, ATAC के रूप में किया गया है साथ -seq 14, और न आने-सेक 15। databases और ऐसे UCSC जीनोम ब्राउज़र 16, रोडमैप Epigenomics 17 खाका epigenome 18, Cistrome 19, और 20 REMAP के रूप में वेब सर्वर प्रकार की कोशिकाओं और स्थितियों की एक विस्तृत रेंज भर में इन और अन्य प्रयोगात्मक तकनीक द्वारा उत्पादित डेटा के लिए स्वतंत्र पहुँच प्रदान करते हैं। प्रयोगात्मक जांच करने के लिए भी कई वेरिएंट कर रहे हैं, इन आंकड़ों प्रासंगिक सेल और प्रकार के ऊतकों में होने की संभावना विनियामक क्षेत्रों के भीतर स्थित उन प्राथमिकता करने के लिए इस्तेमाल किया जा सकता है। इसके अलावा, उन मामलों में जहां एक संस्करण एक विशेष प्रोटीन के लिए एक चिप seq चोटी के भीतर है, इन आंकड़ों के संभावित सुराग विशिष्ट टीएफ (s) या सह कारकों जिसका बाध्यकारी को प्रभावित किया जा सकता है के रूप प्रदान कर सकते हैं।
अगले, जिसके परिणामस्वरूप प्राथमिकता के आधार पर वेरिएंट प्रयोगात्मक भविष्यवाणी जीनोटाइप निर्भर प्रोटीन को मान्य करने के EMSA 21,22 का उपयोग कर बाध्यकारी जांच कर रहे हैं। EMSA एक गैर कम करने TBE जेल पर oligo के प्रवास में परिवर्तन के उपाय। Fluorescently लेबल oligo साथ incubated हैपरमाणु lysate, और परमाणु कारकों के बंधन जेल पर oligo के आंदोलन को धीमा होगा। इस तरह से, oligo कि अधिक परमाणु कारकों बाध्य किया गया है स्कैनिंग पर एक मजबूत फ्लोरोसेंट संकेत के रूप में पेश होगा। विशेष रूप से, EMSA विशिष्ट प्रोटीन जिसका बाध्यकारी प्रभावित हो जाएगा के बारे में भविष्यवाणी की आवश्यकता नहीं है।
एक बार जब वेरिएंट की पहचान कर रहे भविष्यवाणी की नियामक क्षेत्रों के भीतर स्थित है और विभिन्न बाध्यकारी परमाणु कारकों में सक्षम हैं कि, कम्प्यूटेशनल विधियों विशिष्ट टीएफ (s) जिसका बाध्यकारी वे प्रभावित कर सकता है भविष्यवाणी करने के लिए कार्यरत हैं। हम सीआईएस-बीपी 23,24, RegulomeDB 25, UniProbe 26, और 27 JASPAR का उपयोग करने के लिए पसंद करते हैं। एक बार उम्मीदवार TFS पहचान कर रहे हैं, इन भविष्यवाणियों विशेष रूप से इन TFS (EMSA-supershifts और DAPA-पाश्चात्य) के खिलाफ एंटीबॉडी का उपयोग कर परीक्षण किया जा सकता है। एक EMSA-supershift परमाणु lysate और oligo के लिए एक टीएफ विशिष्ट एंटीबॉडी के अलावा शामिल है। एक EMSA-supershift में एक सकारात्मक परिणाम रेपर है(संदर्भ 28 में समीक्षा) EMSA बैंड में एक और पारी, या बैंड का एक नुकसान के रूप में esented। पूरक DAPA में, एक 5'-biotinylated oligo संस्करण और 20 आधार जोड़ी न्यूक्लियोटाइड flanking युक्त द्वैध किसी भी परमाणु कारकों विशेष रूप से बाध्यकारी ओलिगोस पर कब्जा करने के लिए प्रासंगिक सेल प्रकार (ओं) से परमाणु lysate साथ incubated हैं। oligo द्वैध परमाणु कारक परिसर में एक चुंबकीय स्तंभ में microbeads streptavidin से स्थिर है। बाध्य परमाणु कारकों क्षालन 29,48 के माध्यम से सीधे एकत्र कर रहे हैं। बंधन भविष्यवाणियों तो एक पश्चिमी धब्बा प्रोटीन के लिए विशिष्ट एंटीबॉडी का उपयोग द्वारा मूल्यांकन किया जा सकता है। मामलों में जहां कोई स्पष्ट भविष्यवाणियों, या बहुत अधिक भविष्यवाणियों, DAPA प्रयोगों के संस्करण पुल-चढ़ाव से elutions बड़े पैमाने पर स्पेक्ट्रोमेट्री का उपयोग उम्मीदवार TFS की पहचान करने के लिए एक प्रोटिओमिक्स कोर करने के लिए भेजा जा सकता है देखते हैं, जो बाद में उपयोग करते हुए मान्य किया जा सकता में ये पहले से वर्णित तरीकों।
articl के शेष मेंई, आनुवंशिक वेरिएंट की EMSA और DAPA विश्लेषण के लिए विस्तृत प्रोटोकॉल प्रदान की जाती है।
Protocol
Representative Results
Discussion
हालांकि अनुक्रमण और जीनोटाइपिंग प्रौद्योगिकियों के क्षेत्र में प्रगति बहुत हमारी क्षमता रोग के साथ जुड़े आनुवंशिक वेरिएंट की पहचान करने के लिए बढ़ाया है, हमारे इन वेरिएंट से प्रभावित कार्यात्मक ?…
Divulgazioni
The authors have nothing to disclose.
Acknowledgements
We thank Erin Zoller, Jessica Bene, and Lindsey Hays for input and direction in protocol development. MTW was supported in part by NIH R21 HG008186 and a Trustee Award grant from the Cincinnati Children’s Hospital Research Foundation. ZHP was supported in part by T32 GM063483-13.
Materials
| Custom DNA Oligonucleotides | Integrated DNA Technologies | http://www.idtdna.com/site/order/oligoentry | |
| Potassium Chloride | Fisher Scientific | BP366-500 | KCl, for CE buffer |
| HEPES (1M) | Fisher Scientific | 15630-080 | For CE and NE buffer |
| EDTA (0.5M), pH 8.0 | Life Technologies | R1021 | For CE, NE, and annealing buffer |
| Sodium Chloride | Fisher Scientific | BP358-1 | NaCl, for NE buffer |
| Tris-HCl (1M), pH 8.0 | Invitrogen | BP1756-100 | For annealing buffer |
| Phosphate Buffered Saline (1X) | Fisher Scientific | MT21040CM | PBS, for cell wash |
| DL-Dithiothreitol solution (1M) | Sigma | 646563 | Reducing agent |
| PMSF | Thermo Scientific | 36978 | Protease Inhibitor |
| Phosphatase Inhibitor Cocktail | Thermo Scientific | 78420 | Prevents dephosphorylation of TFs |
| Nonidet P-40 Substitute | IBI Scientific | IB01140 | NP-40, for nuclear extraction |
| BCA Protein Assay Kit | Thermo Scientific | 23225 | For measuring protein concentration |
| Odyssey EMSA Buffer Kit | Licor | 829-07910 | Contains all necessary EMSA buffers |
| TBE Gels, 6%, 12 Wells | Invitrogen | EC6265BOX | For EMSA |
| TBE Buffer (10X) | Thermo Scientific | B52 | For EMSA |
| FactorFinder Starting Kit | Miltenyi Biotec | 130-092-318 | Contains all necessary DAPA buffers |
| Licor Odyssey CLx | Licor | Recommended scanner for DAPA/EMSA | |
| Antibiotic-Antimycotic | Gibco | 15240-062 | Contains 10,000 units/mL of penicillin, 10,000 µg/mL of streptomycin, and 25 µg/mL of Fungizone® Antimycotic |
| Fetal Bovine Serum | Gibco | 26140-079 | FBS, for culture media |
| RPMI 1640 Medium | Gibco | 22400-071 | Contains L-glutamine and 25mM HEPES |
Riferimenti
- Hindorff, L. A., et al. Potential etiologic and functional implications of genome-wide association loci for human diseases and traits. Proc Natl Acad Sci U S A. 106 (23), 9362-9367 (2009).
- Maurano, M. T., et al. Systematic localization of common disease-associated variation in regulatory DNA. Science. 337 (6099), 1190-1195 (2012).
- Ward, L. D., Kellis, M. Interpreting noncoding genetic variation in complex traits and human disease. Nat Biotechnol. 30 (11), 1095-1106 (2012).
- Paul, D. S., Soranzo, N., Beck, S. Functional interpretation of non-coding sequence variation: concepts and challenges. Bioessays. 36 (2), 191-199 (2014).
- Zhang, F., Lupski, J. R. Non-coding genetic variants in human disease. Hum Mol Genet. , (2015).
- Lee, T. I., Young, R. A. Transcriptional regulation and its misregulation in disease. Cell. 152 (6), 1237-1251 (2013).
- Slatkin, M. Linkage disequilibrium–understanding the evolutionary past and mapping the medical future. Nat Rev Genet. 9 (6), 477-485 (2008).
- Bush, W. S., Moore, J. H. Chapter 11: Genome-wide association studies. PLoS Comput Biol. 8 (12), e1002822 (2012).
- 1000 Genomes Project Consortium. An integrated map of genetic variation from 1,092 human genomes. Nature. 491 (7422), 56-65 (2012).
- Chang, C. C., et al. Second-generation PLINK: rising to the challenge of larger and richer datasets. Gigascience. 4, 7 (2015).
- Purcell, S., et al. PLINK: a tool set for whole-genome association and population-based linkage analyses. Am J Hum Genet. 81 (3), 559-575 (2007).
- ENCODE Project Consortium. An integrated encyclopedia of DNA elements in the human genome. Nature. 489 (7414), 57-74 (2012).
- Crawford, G. E., et al. Genome-wide mapping of DNase hypersensitive sites using massively parallel signature sequencing (MPSS). Genome Res. 16 (1), 123-131 (2006).
- Buenrostro, J. D., Giresi, P. G., Zaba, L. C., Chang, H. Y., Greenleaf, W. J. Transposition of native chromatin for fast and sensitive epigenomic profiling of open chromatin, DNA-binding proteins and nucleosome position. Nat Methods. 10 (12), 1213-1218 (2013).
- Giresi, P. G., Kim, J., McDaniell, R. M., Iyer, V. R., Lieb, J. D. FAIRE Formaldehyde-Assisted Isolation of Regulatory Elements) isolates active regulatory elements from human chromatin. Genome Res. 17 (6), 877-885 (2007).
- Kent, W. J., et al. The human genome browser at UCSC. Genome Res. 12 (6), 996-1006 (2002).
- Roadmap Epigenomics Consortium. Integrative analysis of 111 reference human epigenomes. Nature. 518 (7539), 317-330 (2015).
- Martens, J. H., Stunnenberg, H. G. BLUEPRINT: mapping human blood cell epigenomes. Haematologica. 98 (10), 1487-1489 (2013).
- Liu, T., et al. Cistrome: an integrative platform for transcriptional regulation studies. Genome Biol. 12 (8), R83 (2011).
- Griffon, A., et al. Integrative analysis of public ChIP-seq experiments reveals a complex multi-cell regulatory landscape. Nucleic Acids Res. 43 (4), e27 (2015).
- Staudt, L. M., et al. A lymphoid-specific protein binding to the octamer motif of immunoglobulin genes. Nature. 323 (6089), 640-643 (1986).
- Singh, H., Sen, R., Baltimore, D., Sharp, P. A. A nuclear factor that binds to a conserved sequence motif in transcriptional control elements of immunoglobulin genes. Nature. 319 (6049), 154-158 (1986).
- Weirauch, M. T., et al. Determination and inference of eukaryotic transcription factor sequence specificity. Cell. 158 (6), 1431-1443 (2014).
- Ward, L. D., Kellis, M. HaploReg: a resource for exploring chromatin states, conservation, and regulatory motif alterations within sets of genetically linked variants. Nucleic Acids Res. 40 (Database issue), D930-D934 (2012).
- Boyle, A. P., et al. Annotation of functional variation in personal genomes using RegulomeDB. Genome Res. 22 (9), 1790-1797 (2012).
- Hume, M. A., Barrera, L. A., Gisselbrecht, S. S., Bulyk, M. L. UniPROBE, update 2015: new tools and content for the online database of protein-binding microarray data on protein-DNA interactions. Nucleic Acids Res. 43 (Database issue), D117-D122 (2015).
- Mathelier, A., et al. JASPAR 2014: an extensively expanded and updated open-access database of transcription factor binding profiles. Nucleic Acids Res. 42 (Database issue), 142-147 (2014).
- Smith, M. F., Delbary-Gossart, S. Electrophoretic Mobility Shift Assay (EMSA). Methods Mol Med. 50, 249-257 (2001).
- Franza, B. R., Josephs, S. F., Gilman, M. Z., Ryan, W., Clarkson, B. Characterization of cellular proteins recognizing the HIV enhancer using a microscale DNA-affinity precipitation assay. Nature. 330 (6146), 391-395 (1987).
- . BCA Protein Assay Kit: User Guide Available from: https://tools.thermofisher.com/content/sfs/manuals/MAN0011430_Pierce_BCA_Protein_Asy_UG.pdf (2014)
- Wijeratne, A. B., et al. Phosphopeptide separation using radially aligned titania nanotubes on titanium wire. ACS Appl Mater Interfaces. 7 (21), 11155-11164 (2015).
- Silva, J. M., McMahon, M. The Fastest Western in Town: A Contemporary Twist on the Classic Western Blot Analysis. J. Vis. Exp. (84), (2014).
- Lu, X., et al. Lupus Risk Variant Increases pSTAT1 Binding and Decreases ETS1 Expression. Am J Hum Genet. 96 (5), 731-739 (2015).
- Ramana, C. V., Chatterjee-Kishore, M., Nguyen, H., Stark, G. R. Complex roles of Stat1 in regulating gene expression. Oncogene. 19 (21), 2619-2627 (2000).
- Fillebeen, C., Wilkinson, N., Pantopoulos, K. Electrophoretic Mobility Shift Assay (EMSA) for the Study of RNA-Protein Interactions: The IRE/IRP Example. J. Vis. Exp. (94), e52230 (2014).
- Heng, T. S., Painter, M. W. Immunological Genome Project, C. The Immunological Genome Project: networks of gene expression in immune cells. Nat Immunol. 9 (10), 1091-1094 (2008).
- Wu, C., et al. BioGPS: an extensible and customizable portal for querying and organizing gene annotation resources. Genome Biol. 10 (11), R130 (2009).
- Wu, C., Macleod, I., Su, A. I. BioGPS and MyGene.info: organizing online, gene-centric information. Nucleic Acids Res. 41 (Database issue), D561-D565 (2013).
- Wang, J., et al. Sequence features and chromatin structure around the genomic regions bound by 119 human transcription factors. Genome Res. 22 (9), 1798-1812 (2012).
- Holden, N. S., Tacon, C. E. Principles and problems of the electrophoretic mobility shift assay. J Pharmacol Toxicol Methods. 63 (1), 7-14 (2011).
- Xu, J., Liu, H., Park, J. S., Lan, Y., Jiang, R. Osr1 acts downstream of and interacts synergistically with Six2 to maintain nephron progenitor cells during kidney organogenesis. Development. 141 (7), 1442-1452 (2014).
- Yang, T. -. P., et al. Genevar: a database and Java application for the analysis and visualization of SNP-gene associations in eQTL studies. Bioinformatics. 26 (19), 2474-2476 (2010).
- Fort, A., et al. A liver enhancer in the fibrinogen gene cluster. Blood. 117 (1), 276-282 (2011).
- Solberg, N., Krauss, S. Luciferase assay to study the activity of a cloned promoter DNA fragment. Methods Mol Biol. 977, 65-78 (2013).
- Rahman, M., et al. A repressor element in the 5′-untranslated region of human Pax5 exon 1A. Gene. 263 (1-2), 59-66 (2001).
- Mali, P., et al. RNA-Guided Human Genome Engineering via Cas9. Science. 339 (6121), 823-826 (2013).

