Aufbau von Stoffwechselnetzwerken außerhalb des Gleichgewichts in nano- und mikrometergroßen Vesikeln
Summary
Wir stellen ein Protokoll zur Rekonstitution von Membranproteinen und zur Verkapselung von Enzymen und anderen wasserlöslichen Komponenten in Lipidvesikeln von Submikrometer- und Mikrometergröße vor.
Abstract
Wir stellen eine Methode vor, um komplexe Proteinnetzwerke in Vesikel einzubauen, an denen integrale Membranproteine, Enzyme und fluoreszenzbasierte Sensoren unter Verwendung gereinigter Komponenten beteiligt sind. Diese Methode ist relevant für das Design und den Bau von Bioreaktoren und die Untersuchung komplexer metabolischer Reaktionsnetzwerke außerhalb des Gleichgewichts. Wir beginnen mit der Rekonstitution von (mehreren) Membranproteinen zu großen unilamellären Vesikeln (LUVs) nach einem zuvor entwickelten Protokoll. Anschließend verkapseln wir ein Gemisch aus gereinigten Enzymen, Metaboliten und fluoreszenzbasierten Sensoren (fluoreszierende Proteine oder Farbstoffe) mittels Gefrier-Auftau-Extrusion und entfernen nicht eingebaute Komponenten durch Zentrifugation und/oder Größenausschlusschromatographie. Die Leistung der Stoffwechselnetzwerke wird in Echtzeit gemessen, indem das ATP/ADP-Verhältnis, die Metabolitenkonzentration, der interne pH-Wert oder andere Parameter durch Fluoreszenzauslesung überwacht werden. Unsere Membranprotein-haltigen Vesikel mit einem Durchmesser von 100-400 nm können mit bestehenden, aber optimierten Verfahren in riesig-unilamelläre Vesikel (GUVs) umgewandelt werden. Der Ansatz ermöglicht den Einbau löslicher Komponenten (Enzyme, Metaboliten, Sensoren) in mikrometergroße Vesikel, wodurch das Volumen der Bioreaktoren um Größenordnungen vergrößert wird. Das metabolische Netzwerk, das GUVs enthält, wird in mikrofluidischen Geräten gefangen, um sie mit optischer Mikroskopie zu analysieren.
Introduction
Der Bereich der synthetischen Biologie von unten konzentriert sich auf die Konstruktion von (minimalen) Zellen 1,2 und metabolischen Bioreaktoren für biotechnologische 3,4 oder biomedizinische Zwecke 5,6,7,8. Die Konstruktion synthetischer Zellen bietet eine einzigartige Plattform, die es Forschern ermöglicht, (Membran-)Proteine unter genau definierten Bedingungen zu untersuchen, die denen der natürlichen Umgebung nachahmen, und ermöglicht so die Entdeckung von emergenten Eigenschaften und verborgenen biochemischen Funktionen von Proteinen und Reaktionsnetzwerken9. Als Zwischenschritt hin zu einer autonom funktionierenden synthetischen Zelle werden Module entwickelt, die wesentliche Merkmale lebender Zellen wie metabolische Energieerhaltung, Protein- und Lipidsynthese sowie Homöostase erfassen. Solche Module erweitern nicht nur unser Verständnis des Lebens, sondern haben auch Anwendungsmöglichkeiten in den Bereichen Medizin8 und Biotechnologie10.
Transmembranproteine sind das Herzstück praktisch jedes Stoffwechselnetzwerks, da sie Moleküle in oder aus der Zelle transportieren, Signale senden und auf die Qualität der Umwelt reagieren und zahlreiche biosynthetische Rollen spielen. Daher erfordert das Engineering von Stoffwechselmodulen in synthetischen Zellen in den meisten Fällen die Rekonstitution von integralen und/oder peripheren Membranproteinen zu einer Membrandoppelschicht, die aus spezifischen Lipiden besteht und eine hohe Integrität (geringe Permeabilität) aufweist. Der Umgang mit diesen Membranproteinen ist anspruchsvoll und erfordert spezifisches Wissen und experimentelle Fähigkeiten.
Es wurden mehrere Methoden entwickelt, um Membranproteine in Phospholipid-Vesikeln zu rekonstituieren, meist mit dem Ziel, die Funktion11,12, die Regulation13, die kinetischen Eigenschaften14,15, die Lipidabhängigkeit15,16 und/oder die Stabilität17 eines spezifischen Proteins zu untersuchen. Diese Verfahren umfassen die rasche Verdünnung von durch Detergenzien gelöstem Protein in wässrigen Medien in Gegenwart von Lipiden18, die Entfernung von Detergenzien durch Inkubation von durch Detergenzien gelöstes Protein mit detergenzient destabilisierten Lipidvesikeln und die Absorption des Detergens bzw. der Detergenzien auf Polystyrolkügelchen19 oder das Entfernen von Detergenzien durch Dialyse oder Größenausschlusschromatographie20. Organische Lösungsmittel wurden verwendet, um Lipidvesikel zu bilden, z. B. durch die Bildung von Öl-Wasser-Interphasen21, aber die Mehrzahl der integralen Membranproteine wird inaktiviert, wenn sie solchen Lösungsmitteln ausgesetzt werden.
In unserem Labor rekonstituieren wir hauptsächlich Membranproteine mit der Detergenz-Absorptionsmethode zu großen unilamellären Vesikeln (LUVs)19. Dieses Verfahren ermöglicht die Co-Rekonstitution mehrerer Membranproteine und die Verkapselung von Enzymen, Metaboliten und Sonden im Vesikellumen22,23. Die Membranprotein-haltigen LUVs können in riesen-unilamelläre Vesikel (GUVs) mit/ohne Verkapselung wasserlöslicher Komponenten umgewandelt werden, wobei entweder die Elektroformation24 oder die gelgestützte Quellung25 und spezifische Bedingungen zur Erhaltung der Integrität der Membranproteine26 verwendet werden.
In dieser Arbeit wird ein Protokoll für die Rekonstitution eines außerhalb des Gleichgewichts befindlichen metabolischen Netzwerks in LUVs vorgestellt, das ATP durch den Abbau von L-Arginin in L-Ornithin regeneriert27. Die Bildung von ATP ist an die Produktion von Glycerin-3-phosphat (G3P) gekoppelt, einem wichtigen Baustein für die Phospholipidsynthese22,28. Der Stoffwechselweg besteht aus zwei integralen Membranproteinen, einem Arginin/Ornithin (ArcD) und einem G3P/Pi-Antiporter (GlpT). Darüber hinaus werden drei lösliche Enzyme (ArcA, ArcB, ArcC) für das Recycling von ATP benötigt, und GlpK wird verwendet, um Glycerin in Glycerin-3-phosphat umzuwandeln, wobei das ATP aus dem Abbau von L-Arginin verwendet wird, siehe Abbildung 1 für einen schematischen Überblick über den Weg. Dieses Protokoll stellt einen guten Ausgangspunkt für den zukünftigen Aufbau noch komplexerer Reaktionsnetzwerke dar – für die Synthese von Lipiden oder Proteinen oder die Teilung von Zellen. Die Lipidzusammensetzung der Vesikel unterstützt die Aktivität einer Vielzahl von integralen Membranproteinen und wurde für den Transport verschiedener Moleküle in oder aus den Vesikeln optimiert 27,29,30.
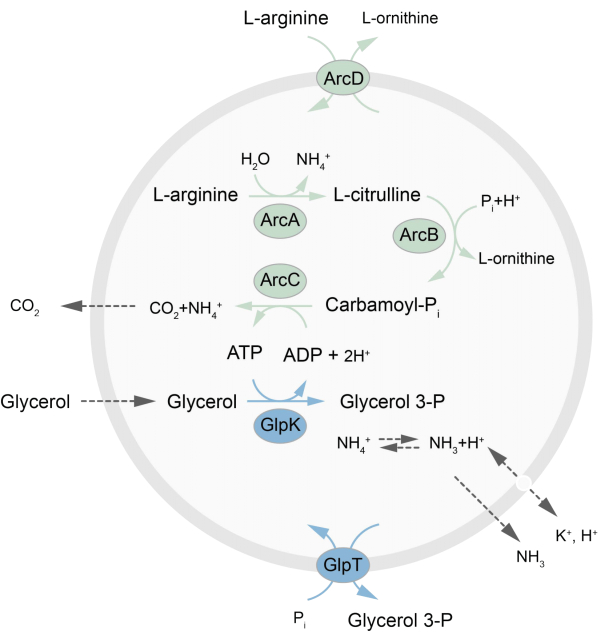
Abbildung 1: Überblick über den Weg der ATP-Produktion und der Glycerin-3-phosphat-Synthese und -Ausscheidung. Bitte klicken Sie hier, um eine größere Version dieser Abbildung anzuzeigen.
Kurz gesagt, gereinigte Membranproteine (solubilisiert in Dodecyl-β-D-Maltosid, DDM) werden zu vorgeformten Lipidvesikeln hinzugefügt, die mit Triton X-100 destabilisiert wurden, was die Insertion der Proteine in die Membran ermöglicht. Die Detergensmoleküle werden anschließend (langsam) durch die Zugabe von aktivierten Polystyrolkügelchen entfernt, was zur Bildung von gut verschlossenen Proteoliposomen führt. Lösliche Bestandteile können dann zu den Vesikeln hinzugefügt und über Gefrier-Tau-Zyklen verkapselt werden, wodurch die Moleküle im Prozess der Membranfusion eingefangen werden. Die gewonnenen Vesikel sind sehr heterogen und viele sind multilamell. Sie werden dann durch einen Polycarbonatfilter mit einer Porengröße von 400, 200 oder 100 nm extrudiert, was zu gleichmäßiger großen Vesikeln führt; Je kleiner die Porengröße, desto homogener und unilamellär sind die Vesikel, jedoch zum Preis eines kleineren inneren Volumens. Nicht eingebaute Proteine und kleine Moleküle werden durch Größenausschlusschromatographie aus der externen Lösung entfernt. Die proteoLUVs können durch gelgestütztes Aufquellen in mikrometergroße Vesikel umgewandelt werden, und diese proteoGUVs werden dann gesammelt und in einem mikrofluidischen Chip zur mikroskopischen Charakterisierung und Manipulation gefangen. Abbildung 2 zeigt einen schematischen Überblick über das gesamte Protokoll.
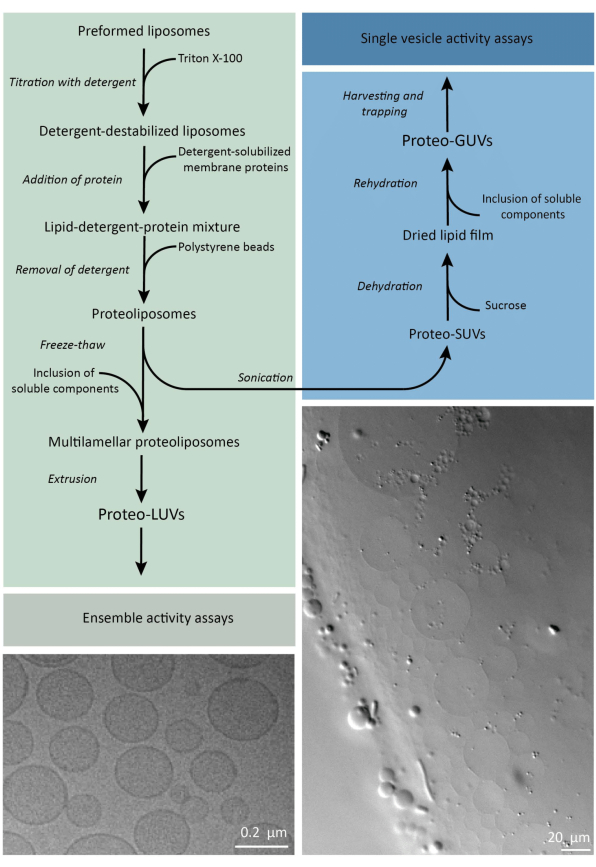
Abbildung 2: Überblick über das Protokoll zur Rekonstitution von Membranproteinen und zur Verkapselung von Enzymen und wasserlöslichen Komponenten in Lipidvesikeln mit Submikrometer- (LUVs) und Mikrometergröße (GUVs). Bitte klicken Sie hier, um eine größere Version dieser Abbildung anzuzeigen.
Die Rekonstitutions- und Verkapselungsprotokolle funktionieren gut und die Funktionalität der Proteine bleibt erhalten, aber die proteoLUVs und proteoGUVs sind heterogen groß. Mikrofluidische Ansätze 31,32 ermöglichen die Bildung von mikrometergroßen Vesikel, die in ihrer Größe homogener sind, aber eine funktionelle Rekonstitution von Membranproteinen ist im Allgemeinen nicht möglich, da das restliche Lösungsmittel in der Doppelschicht die Proteine inaktiviert. Die ProteoLUVs haben eine Größe von 100 bis 400 nm, und bei niedrigen Enzymkonzentrationen kann die Verkapselung zu Vesikeln mit unvollständigen Stoffwechselwegen führen (stochastische Effekte; siehe Abbildung 3). LUVs sind ideal für den Aufbau spezifischer Stoffwechselmodule, wie hier gezeigt, für die Produktion von ATP und Bausteinen wie G3P. Solche proteoLUVs können möglicherweise in GUVs eingekapselt werden und als organellenähnliche Kompartimente für die Wirtsvesikel dienen.
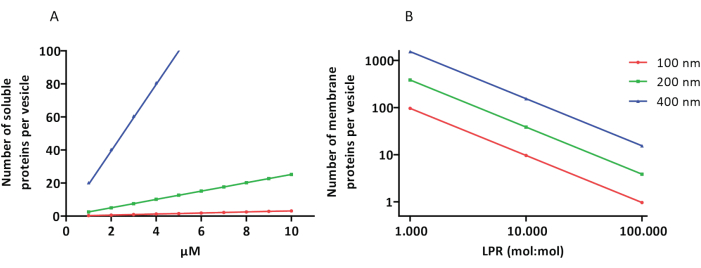
Abbildung 3: Anzahl der Moleküle pro Vesikel mit einem Durchmesser von 100, 200 oder 400 nm. (A) Wenn die verkapselten Proteine (Enzyme, Sonden) im Bereich von 1-10 μM liegen. (B) Die Rekonstitution erfolgt bei 1 bis 1.000, 1 bis 10.000 und 1 bis 100.000 Membranproteinen pro Lipid (mol/mol). Wir gehen davon aus, dass Moleküle in den angegebenen Konzentrationen verkapselt und bei diesen Protein-Lipid-Verhältnissen in die Membran eingebaut werden. Bei einigen Enzymen haben wir gesehen, dass sie an Membranen binden, was ihre scheinbare Konzentration in den Vesikeln erhöhen kann. Abkürzung: LPR = Lipid-Protein-Ratio Bitte klicken Sie hier, um eine größere Version dieser Abbildung anzuzeigen.
Protocol
Representative Results
Discussion
Wir stellen ein Protokoll für die Synthese von (Membran-)Proteinen vor, die submikrometergroße Lipidvesikel (proteoLUVs) enthalten, und die Umwandlung von proteoLUVs in riesen-unilamelläre Vesikel (proteoGUVs). Das Protokoll sollte anwendbar sein für die Rekonstitution anderer Membranproteine13, 19, 30, 40 und die Verkapselung anderer Stoffwechselnetzwerke als der hier vorgestellten L-Argin…
Divulgazioni
The authors have nothing to disclose.
Acknowledgements
Die Autoren danken Aditya Iyer für die Klonierung des pBAD-PercevalHR-Gens und Gea Schuurman-Wolters für die Unterstützung bei der Proteinproduktion und -reinigung. Die Forschung wurde durch das NWO-Gravitationsprogramm “Building a Synthetic Cell” (BaSyC) gefördert.
Materials
| Agarose | Sigma Aldrich | A9414-25g | |
| Amicon cut-off filter | Sigma Aldrich | Milipore centrifugal filter units Amicon Ultra | |
| BioBeads | BioRad | 152-3920 | |
| CHCl3 | Macron Fine Chemicals | MFCD00000826 | |
| D(+)-Glucose | Formedium | – | |
| D(+)-Sucrose | Formedium | – | |
| DDM | Glycon | D97002 -C | |
| Diethyl Ether | Biosolve | 52805 | |
| DMSO | Sigma-Aldrich | 276855-100ml | |
| DOPC | Avanti | 850375P-1g | |
| DOPE | Avanti | 850725P-1g | |
| DOPG | Avanti | 840475P-1g | |
| DTT | Formedium | DTT005 | |
| EtOH | J.T.Baker Avantor | MFCD00003568 | |
| Extruder | Avestin Inc | LF-1 | |
| Fluorimeter | Jasco | Spectrofluorometer FP-8300 | |
| Glycerol | BOOM | 51171608 | |
| Gravity flow column | Bio-Rad | 732-1010 | |
| Hamilton syringe 100 µL | Hamilton | 7656-01 | |
| Hamilton syringe 1000 µL | Hamilton | 81320 | |
| Handheld LCP dispenser | Art Robbins Instruments | 620-411-00 | |
| Handheld Sonicator | Hielscher Ultrasound Technology | UP50H | |
| HCl | BOOM | x76021889.1000 | |
| Imidazole | Roth | X998.4-250g | |
| K2HPO4 | Supelco | 1.05099.1000 | |
| KCl | BOOM | 76028270.1 | |
| KH2PO4 | Supelco | 1.04873.1000 | |
| Kimwipe | Kimtech Science | 7552 | |
| Large Falcon tube centrifuge | Eppendorf | Centrifuge 5810 R | |
| L-Arginine | Sigma-Aldrich | A5006-100G | |
| Light microscope | Leica | DM LS2 | |
| L-Ornithine | Roth | T204.1 | |
| LSM Laser Scanning Confocal Microscope | Zeiss | LSM 710 ConfoCor 3 | |
| MgCl2 | Sigma-Aldrich | M2670-1KG | |
| Microfluidic chip | Homemade | PDMS based | DOI: https://doi.org/10.1039/C8LC01275J |
| Na-ADP | Sigma-Aldrich | A2754-1G | |
| NaCl | Supelco | 1.06404.1000 | |
| Nanodrop Spectrometer | Isogen Life Science | ND-1000 spectrophotometer NanoDrop | |
| NaOH | Supelco | 1.06498.1000 | |
| Needles for GUVs | Henke-Ject | 14-14575 | 27 G x 3/4'' 0.4 x 20 mm |
| Needles for microfluidics | Henke-Ject | 14-15538 | 18 G x 1 1/2'' 1.2 x 40 mm |
| Ni2+ Sepharose | Cytiva | 17526802 | |
| Nigericin | Sigma-Aldrich | N7143-5MG | |
| Nutator | VWR | 83007-210 | |
| Osmolality meter | Gonotec Salmenkipp | Osmomat 3000 basic freezing point osmometer | |
| Plasmacleaner | Plasma Etch | PE-Avenger | |
| Polycarbonate filter | Cytiva Whatman | Nuclepor Track-Etch Membrane Product: 10417104 | 0.4 µm |
| Polycarbonate ultracentrifuge tube | Beckman Coulter | 355647 | |
| Pyranine | Acros Organics | H1529-1G | |
| Quartz cuvette (black) | Hellma Analytics | 108B-10-40 | |
| Sephadex G-75 resin | GE Healthcare | 17-0050-01 | |
| Sonicator | Sonics Sonics & Materials INC | Sonics vibra cell | |
| Syringe filter | Sarstedt | Filtropur S plus 0.2 | 0.2 µm |
| Syringe pump | Harvard Apparatus | A-42467 | |
| Tabletop centrifuge | Eppendorf | centrifuge 5418 | |
| Teflon spacer | Homemade | Teflon based | 45 x 26 x 1.5 or 45 x 26 x 3 or 20 x 20 x 3 mm |
| Tris | PanReac AppliChem | A1086.1000 | |
| Triton X-100 | Sigma Aldrich | T8787-100 ml | |
| Ultracentrifuge | Beckman Coulter | Optima Max-E | |
| UV lamp | Spectroline | ENB-280C/FE | |
| UV/VIS Spectrometer | Jasco | V730 spectrophotometer | |
| Valinomycin | Sigma-Aldrich | V0627-10MG | |
| Widefield fluorescence microscope | Zeiss | AxioObserver | |
| β-Casein | Sigma Aldrich | C5890-500g |
Riferimenti
- Hirschi, S., Ward, T. R., Meier, W. P., Müller, D. J., Fotiadis, D. Synthetic biology: bottom-up assembly of molecular systems. Chem Rev. 122 (21), 16294-16328 (2022).
- Ivanov, I., et al. Bottom-up synthesis of artificial cells: recent highlights and future challenges. Annu Rev Chem Biomol. Eng. 12 (1), 287-308 (2021).
- Clomburg, J. M., Crumbley, A. M., Gonzalez, R. Industrial biomanufacturing: The future of chemical production. Science. 355 (6320), (2017).
- Shi, T., Han, P., You, C., Zhang, Y. -. H. P. J. An in vitro synthetic biology platform for emerging industrial biomanufacturing: Bottom-up pathway design. Synth Syst Biotechnol. 3 (3), 186-195 (2018).
- Wang, A., et al. Liver-target and glucose-responsive polymersomes toward mimicking endogenous insulin secretion with improved hepatic glucose utilization. Adv Funct Mater. 30 (13), 1910168 (2020).
- Kanter, G., et al. Cell-free production of scFv fusion proteins: an efficient approach for personalized lymphoma vaccines. Blood. 109 (8), 3393-3399 (2007).
- Zeltins, A. Construction and characterization of virus-like particles: a review. Mol Biotechnol. 53 (1), 92-107 (2013).
- Jain, K. K. Synthetic biology and personalized medicine. Med Princ Pract. 22 (3), 209-219 (2013).
- Schwille, P., Frohn, B. P. Hidden protein functions and what they may teach us. Trends Cell Biol. 32 (2), 102-109 (2022).
- Sachsenmeier, P. Industry 5.0-The relevance and implications of bionics and synthetic biology. Ingegneria. 2 (2), 225-229 (2016).
- Schmidt, D., Jiang, Q. -. X., MacKinnon, R. Phospholipids and the origin of cationic gating charges in voltage sensors. Nature. 444 (7120), 775-779 (2006).
- Godoy-Hernandez, A., et al. Rapid and highly stable membrane reconstitution by LAiR enables the study of physiological integral membrane protein functions. ACS Cent Sci. 9 (3), 494-507 (2023).
- Sikkema, H. R., et al. Gating by ionic strength and safety check by cyclic-di-AMP in the ABC transporter OpuA. Sci Adv. 6 (47), 7697 (2020).
- Foucaud, C., Poolman, B. Lactose transport system of Streptococcus thermophilus. Functional reconstitution of the protein and characterization of the kinetic mechanism of transport. J Biol Chem. 267 (31), 22087-22094 (1992).
- Yoneda, J. S., Sebinelli, H. G., Itri, R., Ciancaglini, P. Overview on solubilization and lipid reconstitution of Na,K-ATPase: enzyme kinetic and biophysical characterization. Biophys Rev. 12 (1), 49-64 (2020).
- Simidjiev, I., et al. Self-assembly of large, ordered lamellae from non-bilayer lipids and integral membrane proteins in vitro. Proc Natl Acad Sci. 97 (4), 1473-1476 (2000).
- Harris, N. J., Booth, P. J. Folding and stability of membrane transport proteins in vitro. Biochim Biophys Acta BBA – Biomembr. 1818 (4), 1055-1066 (2012).
- Jackson, M. L., Litman, B. J. Rhodopsin-egg phosphatidylcholine reconstitution by an octyl glucoside dilution procedure. Biochim Biophys Acta BBA – Biomembr. 812 (2), 369-376 (1985).
- Geertsma, E. R., Nik Mahmood, N. A. B., Schuurman-Wolters, G. K., Poolman, B. Membrane reconstitution of ABC transporters and assays of translocator function. Nat Protoc. 3 (2), 256-266 (2008).
- Rigaud, J. -. L., Pitard, B., Levy, D. Reconstitution of membrane proteins into liposomes: application to energy-transducing membrane proteins. Biochim Biophys Acta BBA – Bioenerg. 1231 (3), 223-246 (1995).
- Szoka, F., Papahadjopoulos, D. Procedure for preparation of liposomes with large internal aqueous space and high capture by reverse-phase evaporation. Proc Natl Acad Sci. 75 (9), 4194-4198 (1978).
- . Synthetic Organelles for Energy Conservation and Delivery of Building Blocks for Lipid Biosynthesis Available from: https://www.researchsquare.com/article/rs-3385355/v1 (2023)
- Lee, K. Y., et al. Photosynthetic artificial organelles sustain and control ATP-dependent reactions in a protocellular system. Nat Biotechnol. 36 (6), 530-535 (2018).
- Méléard, P., Bagatolli, L. A., Pott, T. Giant unilamellar vesicle electroformation. Methods in Enzymology. , 161-176 (2009).
- Garten, M., Aimon, S., Bassereau, P., Toombes, G. E. S. Reconstitution of a transmembrane protein, the voltage-gated ion channel, KvAP, into giant unilamellar vesicles for microscopy and patch clamp studies. J. Vis. Exp. (95), e52281 (2015).
- Doeven, M. K., et al. lateral mobility and function of membrane proteins incorporated into giant unilamellar vesicles. Biophys J. 88 (2), 1134-1142 (2005).
- Pols, T., et al. A synthetic metabolic network for physicochemical homeostasis. Nat Commun. 10 (1), 4239 (2019).
- Bailoni, E., Poolman, B. ATP recycling fuels sustainable glycerol 3-phosphate formation in synthetic cells fed by dynamic dialysis. ACS Synth Biol. 11 (7), 2348-2360 (2022).
- Van Der Heide, T. On the osmotic signal and osmosensing mechanism of an ABC transport system for glycine betaine. EMBO J. 20 (24), 7022-7032 (2001).
- Van’T Klooster, J. S., et al. Membrane lipid requirements of the lysine transporter Lyp1 from Saccharomyces cerevisiae. J Mol Biol. 432 (14), 4023-4031 (2020).
- Lou, G., Anderluzzi, G., Woods, S., Roberts, C. W., Perrie, Y. A novel microfluidic-based approach to formulate size-tuneable large unilamellar cationic liposomes: Formulation, cellular uptake and biodistribution investigations. Eur J Pharm Biopharm. 143, 51-60 (2019).
- Weiss, M., et al. Sequential bottom-up assembly of mechanically stabilized synthetic cells by microfluidics. Nat Mater. 17 (1), 89-96 (2018).
- Pols, T., Singh, S., Deelman-Driessen, C., Gaastra, B. F., Poolman, B. Enzymology of the pathway for ATP production by arginine breakdown. FEBS J. 288 (1), 293-309 (2021).
- Yandrapalli, N., Robinson, T. Ultra-high capacity microfluidic trapping of giant vesicles for high-throughput membrane studies. Lab Chip. 19 (4), 626-633 (2019).
- Elias, M., et al. Microfluidic characterization of biomimetic membrane mechanics with an on-chip micropipette. Micro Nano Eng. 8, 100064 (2020).
- Robinson, T., Kuhn, P., Eyer, K., Dittrich, P. S. Microfluidic trapping of giant unilamellar vesicles to study transport through a membrane pore. Biomicrofluidics. 7 (4), 044105 (2013).
- Cooper, A., Girish, V., Subramaniam, A. B. Osmotic Pressure Enables High-Yield Assembly of Giant Vesicles in Solutions of Physiological Ionic Strengths. Langmuir. 39 (15), 5579-5590 (2023).
- Tantama, M., Martínez-François, J. R., Mongeon, R., Yellen, G. Imaging energy status in live cells with a fluorescent biosensor of the intracellular ATP-to-ADP ratio. Nat Commun. 4 (1), 2550 (2013).
- Setyawati, I., et al. In vitro reconstitution of dynamically interacting integral membrane subunits of energy-coupling factor transporters. eLife. 9, e64389 (2020).
- Oropeza-Guzman, E., Ríos-Ramírez, M., Ruiz-Suárez, J. C. Leveraging the coffee ring effect for a defect-free electroformation of giant unilamellar vesicles. Langmuir. 35 (50), 16528-16535 (2019).
- Estes, D. J., Mayer, M. Electroformation of giant liposomes from spin-coated films of lipids. Colloids Surf B Biointerfaces. 42 (2), 115-123 (2005).

