多量ホモ測定器と無料、フリー、オープン ソースの明るさ解析ソフトウェアを使用しての体外校正無料定量化
Summary
このプロトコルでは、蛋白質ホモ重合体外に基づく商業光走査顕微鏡を用いた蛍光揺らぎを定量化するための校正無料のアプローチについて説明します。正しい取得の設定と解析方法が表示されます。
Abstract
数と明るさは、ホモ多量を検出するため校正無料蛍光揺らぎ分光 (FFS) 手法です。デジタル検出器を搭載した従来の共焦点顕微鏡を使用して用いることができます。数と明るさを正確に AP20187 の dimerizing の薬剤の添加の前後に mVenus ラベル FKBP12F36V のオリゴマーの状態を定量化する、見ることができるユースケースによる培養技術の使用のためのプロトコルが表示されます。アクイジション ・ パラメーターは正しい顕微鏡と正しいデータの前処理と分析方法を使用しての重要性を説明します。特に、退色補正の選択の重要性が強調されています。この安価な方法は多くの生物学的文脈でのタンパク質間相互作用の研究に用いることができます。
Introduction
蛋白質-蛋白質の相互作用は私体外
伝統的に、結晶構造解析と核磁気共鳴実験クライオ電子顕微鏡法 (低) と組み合わせて、分野正確に蛋白質の三次元のアーキテクチャを記述してその機能を推測する技術高分解能構造詳細を吟味します。蛋白質、しかし、静的な構造ではない、時間と空間で様々 な構造変化や振動を受けることができます。これはなぜ構造結晶構造からの情報または低データは他の技術 (例えば、分子動力学シミュレーションと単一分子技術) を補完する必要があります: 蛋白質の機能はその立体構造に関連して変化と相互作用、およびこの情報は静的構造で存在しません。内分子動力学を調査するためにフォースター共鳴エネルギーの移動 (smFRET) 単一の分子に基づく手法が非常に効果的な1であります。これらのアプローチが複雑なメディアにおける分子の異なる集団を評価することができます。これは非常に重要なは、これらの変更は急速なありのデータ (つまり、 2 番目の範囲にナノ秒) の取得中に発生します。
2 つの主要なアプローチが採用して検出し、これらの変更を定量化する: ソリューションおよび表面固定化タンパク質。リガンドによって誘導される二量体化のプロセス、特に、分子間相互作用の検出のため smFRET は常に最高のツールではありません。確かに、フレット依存 (≈10 nm) の距離だけでなく (ドナーとアクセプター、χ2) の 2 双極子の向きにも、受容体の吸収スペクトル2がおそらくこの最後の条件を持つドナーの発光の重なりが小さい重要な験者できる提供される右のフレットのカップルを選んだ。SmFRET ホモ二量体化をプロービングのための特定の不利な興味の蛋白質のラベルから来る: ヘテロ smFRET 二量体化することができますのみ最大 50% を検出 (すなわち、ヘテロ フレットだけドナー ・ アクセプターを検出できるようになりますとアクセプター ドナー ホモ二量体がないドナー ドナーやアクセプター ・ アクセプター、ダイマーの他の 50% である)。蛍光相関分光法 (FCS) の誘導体 (FCCS、等3) タンパク質拡散定数と結合定数体外を確認するために使用は、別の方法です。これらのアプローチは完全にどちらかホモ二量体化を定量化することができない、拡散粒子の FCS 1 対策濃度と拡散、半径と拡散係数のように、非常に悪い; 分子量に依存分子の重量の 10 倍増加はたとえば、拡散係数4で 2.15 倍変更だけ意味になります。2 色 FCS や FCCS の場合、上記と同じ理由では、ホモ二量体の 50% だけが見られます。ホモ二量体化の in vitroとin vivoを検出する最も実用的と定量的な手法、ホモ フレット5と番号と明るさ (N & B)6です。という事実を考えるヒト フレットが異方性値 (すなわち、光の要素/アナライザー平行および垂直偏波を回復する) の固有のインストルメンテーション回復を必要とする、N & B を提示ここでは有利な方法としてタンパク質ホモ二量体化と集約を検出します。それは、体外と体内の商業設定の両方を採用します。
数と明るさ
N & B は、最近見直し7をされています。そのレビューは、生きた細胞技術の応用に焦点を当てた。それは価値がある再現これらの方程式としてここで、数学的な定式化は、データに適用されますが体外を収集しました。最初に、いくつかの用語や数学的な量を定義する必要があります。
- エンティティは、一緒にバインドされている分子のセットです。
- エンティティの明るさε は、それを発する (フレーム) ごとの単位時間当たりのフォトンの数です。
- nは、エンティティの現在の数です。
- イメージ シリーズにわたって、指定されたピクセルのは、その平均の強さと σ2はその強度の差異です。
フォトンカウンティング検出器と移動体と背景なしと仮定すると、その後、
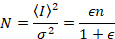
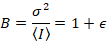
NはBの明白な数と明白な明るさです。これは、結果、
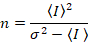
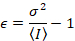
Dalal さんら8アナログ機器で 1 つは 3 つの補正項を必要とした: S ファクター背景のオフセット、および読み出しノイズσ02。その後、再び移動体と仮定してください。
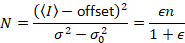
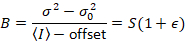
与える
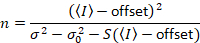
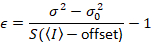
上記の式が異なることに注意してください dalal さんらで与えられています。8その後レビュー。7は、タイプミスなど dalal さんでら S分母が省略され、このエラーがレビューで再現しました。上の方程式はしいものです。指示 dalal さんらによって与えられるオフセットと σ02 – その意味 – の説明と共にSの測定、8
明るさ ε は拡散のエンティティのオリゴマーの状態に比例している: ε スチレンダイマーなどなどはモノマー、hexamers の倍の大きをモノマー、スチレンダイマーの 3 倍の大きさだと二量体の大きさ 2 倍になります。これで、明るさ ε を測定 1 つは多量体形成の任意の型を定量化できます。
現在、数オリゴマー状態の混合物があり、明るさは現在個々 のオリゴマーの状態を回復することができるではないです。これ技術の制限です。
Detrend アルゴリズムと nandb ソフトウェア
退色がされている補正の重要性は以前9を強調しました。退色が必然的にタイムラプス モードで光学顕微鏡の実験中に発生します。生きた細胞と体外の両方。多くのアプローチは、7を漂白を補正するため文献に記載されています。トレンド除去パラメーター Tの自動選択と指数のフィルタ リング技術は、現在最高です。それは、フリーでオープン ソース ソフトウェア nandb9に統合されます。確かに、彼らの detrending のパラメーターを手動で選択するユーザーを必要とするソフトウェアは、このパラメーターの選択に恣意的で不適切ななる可能性が高いため誤った結果を可能性があります。自動のアルゴリズムは、データを検査し、9ユーザーの介入を必要とせずに、適切なパラメーターを指定します。平滑化パラメーターの最良の選択でもトレンド除去はその制限があり退色率 25% 未満でのみうまく動作するシミュレーション9で示すように。興味深いことに、自動の detrending ルーチンを使用して、その精度はその 1 つは低輝度の値を扱うことができます (さらにB < 1.01)、それゆえ低強度、およびまだホモ二量体化を定量化する十分に正確であります。
退色はまた別の問題を引き起こす: 複雑な多量体で photobleached fluorophores の存在。これは例えば、三量体は、三量体の 3 つのユニットの 1 つが非蛍光性二量体のような表示になります。ミューラー10これを修正する方法を示し、この補正もその後レビュー7で強調されました。Nandb ソフトウェアには、この補正9が含まれています。
FKBP12F36Vシステム
FKBP12F36V 自然 oligomerize はないが、AP20187 (配位子を二量化する BB として通俗の言葉で知られている) 薬11,12の添加によって dimerize に知られている蛋白質であります。これにより、数と明るさのための理想的なテスト _ ケース: ラベル付き FKBP12F36V とオリゴマーの状態の倍増を守らなければなりません BB の追加。
Protocol
Representative Results
Discussion
N & B は、商業の光走査共焦点顕微鏡デジタル探知機装備を使用して多量体形成を検出する手法です。このアプローチは、FCS、FCCS、および smFRET 校正無料と明るさ計算だが簡単な単一ポイントと濃度独立6に比べて非常に魅力的です。それは明るさの計算9; を実行する前に漂白と長期強度の変動を補正するためしかし、主要な重要性の漂白のための明るさとそ…
Disclosures
The authors have nothing to disclose.
Acknowledgements
この作品は、Wellcome の信頼に支えられてきた r. n. に 105278/Z/14/2 を付与人類遺伝学のウェルカム トラスト ・ センターで Wellcome の信頼コア賞 203852/Z/16/2 資金を供給されます。C. s. のグループでの作業をサポートするには、癌研究イギリス (C20724/A14414) と欧州連合のホライゾン 2020年研究および革新プログラム助成金 647278 の下で欧州研究評議会。
Materials
| RosettaTM (DE3) pLysS cells | Novagen | 70956-3 | |
| Ampicillin | Sigma Aldrich | PubChem Substance ID 329824407 | |
| Chloramphenicol | Sigma Aldrich | PubChem Substance ID: 24892250 | |
| LB starter culture | QIAGEN | ||
| LB medium | QIAGEN | https://www.sigmaaldrich.com/content/dam/sigma-aldrich/head/search/external-link-icon.gif | |
| IPTG | Sigma Aldrich | PubChem Substance ID 329815691 | |
| IMAC buffer | Medicago | 09-1010-10 | |
| EDTA-free protease inhibitors | Sigma Aldrich | 11873580001 | |
| TALON resin | Clonetech | ||
| Nickel sepharose | GE Healthcare | ||
| S200 16/60 column | GE Healthcare | ||
| Glass bottom 8 well observation dish | Ibidi | 80827 |
References
- Voith von Voithenberg, L., Lamb, D. C. Single pair forster resonance energy transfer: A versatile tool to investigate protein conformational dynamics. BioEssays. 40, (2018).
- Padilla-Parra, S., Auduge, N., Coppey-Moisan, M., Tramier, M. Quantitative FRET analysis by fast acquisition time domain FLIM at high spatial resolution in living cells. Biophysical Journal. 95, 2976-2988 (2008).
- Padilla-Parra, S., Auduge, N., Coppey-Moisan, M., Tramier, M. Dual-color fluorescence lifetime correlation spectroscopy to quantify protein-protein interactions in live cell. Microscopy Research and Technique. 74, 788-793 (2011).
- Muller, J. D., Chen, Y., Gratton, E. Fluorescence correlation spectroscopy. Methods in Enzymology. 361, 69-92 (2003).
- Tramier, M., Coppey-Moisan, M. Fluorescence anisotropy imaging microscopy for homo-FRET in living cells. Methods in Cell Biology. 85, 395-414 (2008).
- Digman, M. A., Dalal, R., Horwitz, A. F., Gratton, E. Mapping the number of molecules and brightness in the laser scanning microscope. Biophysical Journal. 94, 2320-2332 (2008).
- Nolan, R., Iliopoulou, M., Alvarez, L., Padilla-Parra, S. Detecting protein aggregation and interaction in live cells: A guide to number and brightness. Methods. , (2017).
- Dalal, R. B., Digman, M. A., Horwitz, A. F., Vetri, V., Gratton, E. Determination of particle number and brightness using a laser scanning confocal microscope operating in the analog mode. Microscopy Research and Technique. 71, 69-81 (2008).
- Nolan, R., et al. nandb-number and brightness in R with a novel automatic detrending algorithm. Bioinformatics. , (2017).
- Hur, K. H., et al. Quantitative Measurement of Brightness from Living Cells in the Presence of Photodepletion. PLoS One. 9, (2014).
- Amara, J. F., et al. A versatile synthetic dimerizer for the regulation of protein-protein interactions. Proceedings of the National Academy of Sciences of the United States of America. 94, 10618-10623 (1997).
- Clackson, T., et al. Redesigning an FKBP-ligand interface to generate chemical dimerizers with novel specificity. Proceedings of the National Academy of Sciences of the United States of America. 95, 10437-10442 (1998).
- Rollins, C. T., et al. A ligand-reversible dimerization system for controlling protein-protein interactions. Proceedings of the National Academy of Sciences of the United States of America. 97, 7096-7101 (2000).
- Schindelin, J., Rueden, C. T., Hiner, M. C., Eliceiri, K. W. The ImageJ ecosystem: An open platform for biomedical image analysis. Molecular Reproduction and Development. 82, 518-529 (2015).
- . R: A Language and Environment for Statistical Computing. R Core. , (2017).
- . RStudio: Integrated Development Environment for R. R Team. , (2016).
- . nandb R package Available from: https://CRAN.R-project.org/package=nandb (2017)
- Jung, G., Wiehler, J., Zumbusch, A. The photophysics of green fluorescent protein: influence of the key amino acids at positions 65, 203, and 222. Biophysical Journal. 88, 1932-1947 (2005).
- Shaner, N. C., Steinbach, P. A., Tsien, R. Y. A guide to choosing fluorescent proteins. Nature Methods. 2, 905-909 (2005).
- Butkevich, A. N., et al. Hydroxylated fluorescent dyes for live-cell labeling: synthesis, spectra and super-resolution STED. Chemistry: A European Journal. 23, 12114-12119 (2017).

