ठोस और तरल ट्यूमर में कार्रवाई म्यूटेशन की जांच के लिए अगली पीढ़ी के अनुक्रमण
Summary
This manuscript describes clinical protocols for two next-generation sequencing panels. One panel interrogates hematologic malignancies while the other panel targets genes commonly mutated in solid tumors. Molecular classification of driver mutations in human malignancies offers valuable prognostic and predictive information.
Abstract
As our understanding of the driver mutations necessary for initiation and progression of cancers improves, we gain critical information on how specific molecular profiles of a tumor may predict responsiveness to therapeutic agents or provide knowledge about prognosis. At our institution a tumor genotyping program was established as part of routine clinical care, screening both hematologic and solid tumors for a wide spectrum of mutations using two next-generation sequencing (NGS) panels: a custom, 33 gene hematological malignancies panel for use with peripheral blood and bone marrow, and a commercially produced solid tumor panel for use with formalin-fixed paraffin-embedded tissue that targets 47 genes commonly mutated in cancer. Our workflow includes a pathologist review of the biopsy to ensure there is adequate amount of tumor for the assay followed by customized DNA extraction is performed on the specimen. Quality control of the specimen includes steps for quantity, quality and integrity and only after the extracted DNA passes these metrics an amplicon library is generated and sequenced. The resulting data is analyzed through an in-house bioinformatics pipeline and the variants are reviewed and interpreted for pathogenicity. Here we provide a snapshot of the utility of each panel using two clinical cases to provide insight into how a well-designed NGS workflow can contribute to optimizing clinical outcomes.
Introduction
नैदानिक ऑन्कोलॉजी नमूनों की अगली पीढ़ी के अनुक्रमण (NGS) लक्षित की आनुवंशिक परिवर्तन और भविष्य कहनेवाला / शकुन आणविक मार्कर की पहचान करने के महत्व को वैज्ञानिक साहित्य अंक बढ़ के रूप में पिछले कई वर्षों से अधिक व्यापक रूप से उपलब्ध हो गया है। मल्टी जीन पैनल का विश्लेषण करती है और दोनों उपकला 1,2 और 3 hematologic दुर्दमताओं में पूरे exome अनुक्रमण के अध्ययन ट्यूमर विविधता की अवधारणा और प्रतिरूप विकास जम चुके इस रोग की प्रगति और relapses के रूप में। इसके अतिरिक्त, इस तरह के पोलीमरेज़ चेन रिएक्शन (पीसीआर) या सेंगर अनुक्रमण के रूप में प्रतिस्पर्धा प्रौद्योगिकियों के विपरीत, NGS सभी चिकित्सकीय प्रासंगिक कैंसर के जीन में सबसे जीनोमिक परिवर्तन एक भी परख 4 में पता लगा सकते हैं।
शुरू में दो नैदानिक NGS पैनल, एक कस्टम hematological पैनल (हीम-NGS पैनल) और एक मुस्तैद FFPE नमूनों के लिए कैंसर पैनल (ठोस NGS पैनल) के साथ शुरू की निजीकृत निदान के लिए केंद्र (देखें <strong> चित्रा 1)। इन पैनलों चयनित जीन की चिकित्सकीय प्रासंगिक या उच्च ब्याज क्षेत्रों को कवर; सभी जीनों या एक्सॉनों पूरी तरह से कवर नहीं कर रहे हैं। Amplicons जांच संकरण विस्तार और बंधाव के बाद से उत्पन्न कर रहे हैं। लक्षित क्षेत्रों आगे 96 नमूने अनुक्रमण के लिए जमा किया जा करने के लिए अनुमति सार्वभौमिक दोहरे अनुक्रमित प्राइमरों के साथ पीसीआर का उपयोग परिलक्षित कर रहे हैं।
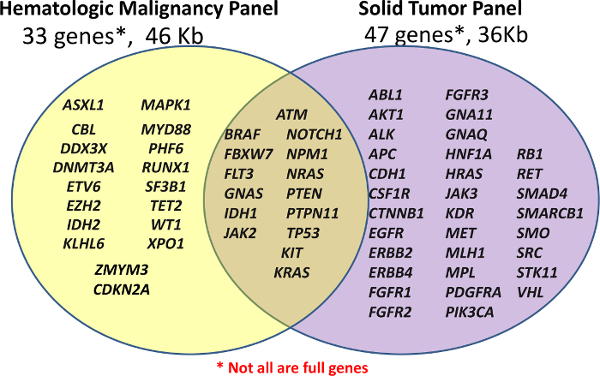
चित्रा 1:। पैनलों में जिन जीन की सूची पुस्तकालय तैयारी का उपयोग किया जाता है या तो कस्टम hematological पैनल 33 जीन या मुस्तैद Amplicon कर्क पैनल 47 जीनों की (ठोस NGS) के (हीम-NGS पैनल)। नहीं जीन या एक्सॉनों के सभी पूर्ण में शामिल किया जाता है, जैसा कि कुछ amplicons केवल कुछ आकर्षण के केंद्र कवर कर सकते हैं। यह आंकड़ा का एक बड़ा संस्करण देखने के लिए यहां क्लिक करें। </ A>
हीम-NGS पैनल के लिए सामग्री विभिन्न स्त्रोतों से प्राप्त होता है, लेकिन तीव्र माइलॉयड ल्यूकेमिया (एएमएल) पहले से नैदानिक उपयोगिता 5 के एक उच्च स्तर का प्रदर्शन के रूप में वर्णित में उत्परिवर्तित जीन 16 के आसपास केंद्रित किया गया था। ठोस NGS पैनल व्यावसायिक रूप से कैंसर में आमतौर पर उत्परिवर्तित जीन पर आधारित लक्षित क्षेत्रों के रूप में कैंसर (लौकिक) डेटाबेस 6 में दैहिक म्यूटेशन की सूची में रिपोर्ट के साथ उत्पादन किया जाता है।
कई महत्वपूर्ण कदम नैदानिक NGS के लिए समग्र कार्यप्रवाह विशेषताएँ। बाद चिकित्सक परीक्षण के आदेश, एक पैथोलॉजिस्ट निम्नलिखित ट्यूमर प्रतिशत और नमूना मात्रा के लिए नमूना विश्लेषण की पर्याप्तता निर्धारित करता है। हमारी संस्था में, हम प्रौद्योगिकी की पृष्ठभूमि अनुक्रमण त्रुटि दर ( "शोर") और लक्षित दृष्टिकोण की क्षमता के कारण कम से कम 10% ट्यूमर की आवश्यकता होती है। अगर ऊतक परीक्षण के लिए पर्याप्त है, जीनोमिक डीएनए निकाला जाता है। यह डीएनए तो कई गुणवत्ता नियंत्रण के अधीन है (क्यूसी) कदम। डीएनए से गुजरता है तो क्यूसी, एक amplicon पुस्तकालय उत्पन्न होता है और अनुक्रम है। परिणामी डेटा एक घर में जैव सूचना विज्ञान पाइपलाइन के माध्यम से विश्लेषण किया है। जैव सूचना विज्ञान विश्लेषण के बाद, वेरिएंट मैन्युअल की समीक्षा की और एक चिकित्सीय रिपोर्ट में शामिल करने से पहले pathogenicity के लिए व्याख्या कर रहे हैं। नीचे हम वर्णन दो मामलों है कि इस कठोर कार्यप्रवाह के माध्यम से चला गया और अंततः नैदानिक प्रबंधन में बदलाव के लिए नेतृत्व किया।
केस 1 – एक्यूट माइलॉयड लेकिमिया
मरीज को एक से एक अस्थि मज्जा बायोप्सी एएमएल के लिए नैदानिक था, परिपक्वता के बिना। Cytogenetic अध्ययनों अस्थि मज्जा नमूना पर भेजा और एक सामान्य महिला कुपोषण प्रदर्शन किया गया। 95% घूम वर्तमान विस्फोटों रहे थे, तो एक परिधीय रक्त नमूना हीम-NGS पैनल पर व्यक्तिगत नैदानिक परीक्षण के लिए भेजा गया था।
तीव्र माइलॉयड ल्यूकेमिया (एएमएल) सफेद रक्त कोशिकाओं की माइलॉयड वंश के एक hematological द्रोह है। खोजएएमएल में जीन म्यूटेशन के रोग का निदान और उपचार के लिए तेजी से महत्वपूर्ण बन गया है, साथ आवर्तक जीन म्यूटेशन रोगजनन और रोग का निदान 7 में महत्वपूर्ण के रूप में मान्यता दी। NPM1 और CEBPA में उत्परिवर्तन, एक अनुकूल शकुन जोखिम के साथ संबद्ध किया गया है, जबकि आंतरिक मिलकर दोहराव (ITDs) FLT3 में एक कम अनुकूल परिणाम 8 के साथ संबद्ध किया गया है। सबूत के एक बढ़ती शरीर एएमएल 9 में इन और अन्य परिवर्तन के लिए एक रोगजनक भूमिका का समर्थन करता है।
केस 2 – फेफड़े Adenocarcinoma
रोगी बी से एक बाएं अक्षोत्तर द्रव्यमान का एक बायोप्सी फेफड़े ग्रंथिकर्कटता का प्रदर्शन किया। formalin तय आयल एम्बेडेड (FFPE) लिम्फ नोड जन से बायोप्सी सामग्री जीनोमिक परीक्षण (ठोस NGS कक्ष) के लिए भेजा गया था के रूप में रोल / 50% से अधिक ट्यूमर के साथ कर्ल, की पहचान करने के लिए है कि क्या एक उत्परिवर्तन लक्षित चिकित्सीय हस्तक्षेप के लिए उपस्थित थे।
फेफड़े CANCएर संयुक्त राज्य अमेरिका में कैंसर से संबंधित मृत्यु दर का प्रमुख कारण है और दो मुख्य प्रकार, गैर छोटे सेल फेफड़ों के कैंसर (NSCLC) और छोटे सेल फेफड़ों के कैंसर (SCLC) में बांटा गया है। NSCLC आगे घाव के ऊतक विज्ञान पर आधारित है, या तो ग्रंथिकर्कटता या स्क्वैमस सेल कार्सिनोमा के रूप में परिभाषित किया जा सकता है। फेफड़ों adenocarcinoma फेफड़ों के कैंसर का सबसे आम उप प्रकार, दोनों धूम्रपान करने वालों और गैर धूम्रपान करने वालों में देखा है, और गैर धूम्रपान करने वालों के लिए 10 फेफड़ों के कैंसर का सबसे आम रूप है। फेफड़ों adenocarcinomas की आणविक अध्ययन कई ओंकोजीन 11 में उत्परिवर्तन की पहचान की है। सबसे आम चालक धूम्रपान करने वालों में पहचान म्यूटेशन KRAS और BRAF में परिवर्तन कर रहे हैं। गैर धूम्रपान करने वालों में सबसे आम म्यूटेशन EGFR में परिवर्तन, और जीन ALK, रेत और ROS1 शामिल rearrangements हैं। फेफड़ों के ट्यूमर जीन ErbB2 में एक में फ्रेम एक्सॉन 20 प्रविष्टि (HER2 / neu) के साथ वर्णित किया गया है। उन्होंने कहा कि में सबसे आम विषमताआर 2 / neu जिसके लिए एक लक्षित थेरेपी (: HER2 / neu के खिलाफ एक humanized मोनोक्लोनल एंटीबॉडी त्रास्तुज़ुमाब) उपलब्ध है स्तन कैंसर में इस लोकस के एक प्रवर्धन है। HER2 / neu एक्सॉन 20 सम्मिलन है कि 2 में मनाया जाता है – फेफड़ों के 4% adenocarcimomas 12 HER2 / neu और mTOR अवरोधकों के साथ संयोजन चिकित्सा के लिए आंशिक प्रतिक्रिया (neratinib और temsirolimus, क्रमशः) 13 दिखाया गया है।
Protocol
Representative Results
Discussion
जैसा कि इस पांडुलिपि में वर्णित दो NGS परीक्षण चिकित्सकीय पेशकश कर रहे हैं, सबसे महत्वपूर्ण व्यावहारिक विचार गुणवत्ता नियंत्रण है। विशेष रूप से, बंद विचार गुणवत्ता और निकाले डीएनए की मात्रा करने के लिए भुगतान किया जाना चाहिए। इस FFPE नमूने जो अक्सर चर डीएनए उपज के साथ अत्यधिक अपमानित कर रहे हैं के लिए विशेष रूप से महत्वपूर्ण है। एक isopropanol वर्षा विधि आदेश FFPE नमूनों से डीएनए उपज को अधिकतम करने के रूप में स्तंभ आधारित विधियों कभी-कभी सीमित क्षालन संस्करणों के साथ डीएनए बाल काटना करने के लिए नेतृत्व करने के लिए पाए गए में विकसित किया गया था। इसलिए, समय था जब एक नमूना भी कम एकाग्रता पैदावार या परख के लिए भी अपमानित है की सबसे अधिक है, यह सबसे अधिक संभावना ऊतक आकार, प्रकार, या निर्धारण और न निकालने की प्रक्रिया के कारण है। रक्त / अस्थि मज्जा के नमूनों के लिए, अगर वहाँ एक निष्कर्षण विफलता है, यह आमतौर पर एक नमूना जा रहा है hemodilute की वजह से है (यानी, कि ड्रॉ में सफेद रक्त या ट्यूमर कोशिकाओं की पर्याप्त संख्या नहीं होने के) या केमो ablated।
। NT "> सत्यापन के दौरान, डीएनए की गुणवत्ता और मात्रा की स्वीकार्यता के लिए cutoffs स्थापित किया जाना चाहिए 100 की सिफारिश की इनपुट – 250 एनजी अक्सर परख में प्रयोग किया जाता है, लेकिन, अगर डीएनए की गुणवत्ता अच्छी है, तो कम इनपुट मात्रा में सफल हो सकते हैं। तो उच्च इनपुट मात्रा अनुक्रमण परिणामों की गुणवत्ता में सुधार कर सकते हैं (क्योंकि amplifiable डीएनए की मात्रा अनुशंसित इनपुट तक पहुंच जाएगा) – इसके अलावा, अगर डीएनए की गुणवत्ता खराब है (250 एनजी यानी, amplifiable डीएनए की मात्रा 100 से भी कम है) । डीएनए की गुणवत्ता और मात्रा के लिए मेट्रिक्स एक 'ग्रे जोन' (देखें चित्र 2) में पुस्तकालय तैयारी में डीएनए को आगे बढ़ाने से पहले प्रत्येक नमूने के लिए लागू किया जाना चाहिए। उन नमूनों को प्रयोगशाला के निदेशक या designee के विवेक पर चलाया जाना चाहिए। वर्तमान में सबसे अच्छा यदि डीएनए अनुक्रमण के दौरान अच्छा प्रदर्शन नहीं होगा भविष्यवाणी करने के लिए जिस तरह से एक qPCR आधारित परख है कि इनपुट डीएनए की मात्रा का ठहराव और गुणवत्ता के आकलन के लिए अनुमति देता प्रदर्शन करने के लिए है। यह दृष्टिकोण bioavailab के पतेनमूना में अलग अलग आकार के टुकड़े, विभिन्न आकार के टुकड़े (जैसे, 100 बीपी, 150 बीपी, 200 बीपी और 300 बीपी) और तुलना उपज के प्रवर्धन के माध्यम से की बड़प्पन।वर्तमान में, पुस्तकालय तैयारी जहां कई मौकों में से एक पर एक misstep पुस्तकालय के लिए या तो असफल हो या गरीब गुणवत्ता का होना पैदा कर सकता है मैनुअल के चरणों की एक बड़ी संख्या शामिल है। microfluidic जेल विश्लेषण अनुक्रमण से पहले एक पुस्तकालय प्रस्तुत करने का मुद्दा जाँच करने के लिए केवल क्यूसी कदम है। तदनुसार, वहाँ कई महत्वपूर्ण कदम है, जहां अतिरिक्त mindfulness एक सफल प्रतिक्रिया की संभावना को बढ़ा सकते हैं। यह गारंटी करने के लिए सही नमूना और oligonucleotide पूल प्रत्येक नमूना के लिए इस्तेमाल कर रहे हैं आवश्यक है। यह सुनिश्चित करने के लिए और ठीक रिकॉर्डिंग है कि प्रत्येक नमूना दोहरे अनुक्रमित पीसीआर प्राइमर जोड़े के 96 में से एक अनूठा संयोजन शामिल एक नमूना मिश्रण के लिए मौका कम कर देता है। इसके अलावा, यह सुनिश्चित करने के लिए फिल्टर प्लेट (एफपीयू) सही ढंग से नालियों महत्वपूर्ण है; यदि यह उचित नाली नहीं है इस exte पैदा कर सकता हैपुस्तकालय तैयारी की nsion-बंधाव कदम suboptimally प्रदर्शन और खराब गुणवत्ता अनुक्रमण डेटा के लिए नेतृत्व करने के लिए। पुस्तकालय क्यूसी के बाद, यह सुनिश्चित करने के लिए कि LNB1 मोती पूरी तरह से resuspended हैं महत्वपूर्ण है और LNB1 / LNA1 समाधान अच्छी तरह से नमूने के लिए इसे जोड़ने के रूप में इस मिश्रण की एकाग्रता पुस्तकालय के molarity निर्धारित करने के लिए प्रयोग किया जाता है पहले मिलाया है। अंत में, यदि मनका क्षालन कदम मोती बंद एल्यूटिंग पुस्तकालय का एक सबऑप्टिमल राशि के लिए होता है यह क्लस्टरिंग घनत्व कम हो जाएगा और संभवतः पुस्तकालय पर्याप्त मतलब कवरेज प्राप्त नहीं करने के लिए कारण। इसके विपरीत, पुस्तकालय की एक अतिरिक्त नेतृत्व करेंगे करने के लिए गरीब गुणवत्ता पढ़ता है। इसलिए, यह इष्टतम पूलिंग और sequencer पर लाइब्रेरी के क्लस्टरिंग सुनिश्चित करने के लिए मनका-आधारित सामान्य बनाने के कदम पर लगातार हो महत्वपूर्ण है।
पुस्तकालय तैयारी के अलावा, यह एक जैव सूचना विज्ञान पाइपलाइन है कि कच्चे, डे-मल्टिप्लेक्स fastq फाइलों से सटीक उत्परिवर्तन कॉल का उत्पादन होगा मान्य करने के लिए महत्वपूर्ण है। चयन एककस्टम समाधान समय लेने वाली हो सकता है के रूप में वहाँ कई खुला स्रोत और वाणिज्यिक रूप से उपलब्ध aligners, संस्करण कॉल करने, और NGS सॉफ्टवेयर संकुल है कि एक के माध्यम से झारना के लिए होता है। कस्टम एल्गोरिदम, आवश्यक प्रदर्शन आंकड़ों निकालने अद्वितीय आवर्ती म्यूटेशन कि सबसे खुला स्रोत उपकरण नहीं मिल पाई पहचान है, और लोकी में से प्रत्येक पर नकल संख्या स्थिति का निर्धारण करने के लिए तैयार करने की आवश्यकता होगी। एक जैव सूचना विज्ञान पाइपलाइन की सत्यापन प्रक्रिया के दौरान, यह वेरिएंट है कि मिलने या गुणवत्ता को छानने के बाद कवरेज के दोनों एक न्यूनतम गहराई (जैसे, 250 की एक न्यूनतम पढ़ता है) और एक न्यूनतम एलील आवृत्ति से अधिक के लिए reportable cutoffs निर्धारित करने के लिए महत्वपूर्ण है (उदाहरण के लिए, 4 %)। यह एक मल्टिप्लेक्स amplicon आधारित परख के बाद से, यह निर्धारित करने के लिए कम से कम कवरेज की गहराई मतलब महत्वपूर्ण है (जैसे, 1,000x) पुस्तकालय न्यूनतम गहराई से पढ़ता के लिए सबसे कम प्रदर्शन amplicon प्राप्त करने में सक्षम होना करने के लिए प्राप्त करने की जरूरत है। इसके अलावा, परख की मल्टिप्लेक्स प्रकृति ग करता हैause बंद लक्ष्य प्रभाव और 'इन कलाकृतियों' की खोज की जा करने के लिए और पूरी तरह से शुरू होने से पहले पुनरीक्षित की आवश्यकता होगी। वर्णित परख के लिए एक और महत्वपूर्ण सीमा आदेश मान्य न्यूनतम एलील आवृत्ति प्राप्त करने के लिए 10% से अधिक ट्यूमर को रोकने के लिए नमूने के लिए एक की जरूरत है।
कम आवृत्ति, 1%, FLT3 सम्मिलन का पता लगाने के सबूत अभी भी इस प्रक्रिया में वांछनीय है कि मैनुअल समीक्षा की है। 5% की एक एलील आवृत्ति कट ऑफ के साथ भी, कुछ महत्वपूर्ण म्यूटेशन शायद याद किया और इस प्रकार मैन्युअल समीक्षा इन वेरिएंट पता लगाने के लिए आवश्यक हो जाएगा। FLT3-ITDs के लिए, एक्सॉन 14 के दृश्य निरीक्षण एक निम्न स्तर या बड़े सम्मिलन / दोहराव सुनिश्चित करने के लिए किसी का ध्यान नहीं जाना है सब एएमएल रोगियों के लिए किया जाता है। इसके अलावा, HER2 एक्सॉन 20 सम्मिलन है कि आमतौर पर प्राइमर अनुक्रम के बगल में हैं, मैनुअल हस्तक्षेप की जरूरत है। एक मजबूत जैव सूचना विज्ञान पाइप लाइन होने के बावजूद, कुछ वेरिएंट अनदेखी की जा सकते हैं जो सिर्फ एक कठिन कटौती होने का स्वभाव हैबंद सबसे आँकड़े के लिए ऊपर उल्लेख किया है। बेहतर जैव सूचना विज्ञान, इस मुद्दे को कम करने में मदद की जरूरत होगी के रूप में बेहतर होगा पुस्तकालय तैयारी और / या अनुक्रमण के तरीके में, क्योंकि यह भी कम cutoffs कि कम कलाकृतियों और झूठी सकारात्मक शामिल पर अच्छी गुणवत्ता वाले डेटा के लिए अधिक फायदेमंद है।
का पता लगाने और एलील आवृत्तियों की व्याख्या ट्यूमर प्रतिशत दृढ़ संकल्प और जीनोम के कुछ क्षेत्रों के प्रवर्धन पूर्वाग्रह में कठिनाई के कारण मुश्किल हो सकता है। इसके अलावा, 50% से अधिक एलील आवृत्तियों, पता लगाया जा सकता है, क्योंकि इस मामले में मनाया 2. इस Heterozygosity (LOH) घटना की हानि के रूप में व्याख्या की है, या तो सामान्य एलील की कमी के कारण, उत्परिवर्ती की स्पष्ट वृद्धि के लिए अग्रणी, एक पढ़ता उत्परिवर्ती एलील (जैसे, 2 उत्परिवर्ती और एक सामान्य प्रतिलिपि) या अन्य तंत्र का लाभ। ये तंत्र सरणी तुलनात्मक जीनोमिक संकरण (aCGH 19) और / या एक एसएनपी जीनोटाइपिंग सरणी का उपयोग करके स्पष्ट किया जा सकता है। 20।
वर्तमान लक्ष्य संवर्धन के तरीके या तो अक्षम संकर कब्जा या मल्टिप्लेक्स पीसीआर तकनीक का पूरा दिन प्रक्रियाओं है कि एक भी नमूना के अधिक अनुक्रमण कवरेज और बंद अधिक लक्ष्य अनुक्रमण पढ़ता के लिए की जरूरत में परिणाम पर निर्भर हैं। NGS आणविक ऑन्कोलॉजी के लिए अतिरिक्त अनुप्रयोगों निकट भविष्य में होने की उम्मीद आसान पुस्तकालय तैयारी के तरीकों कि पूरी तरह से automatable हो सकता है और इनपुट डीएनए की बहुत कम मात्रा के साथ नमूनों को प्रोसेस करने में सक्षम हो सकते हैं शामिल होंगे (यानी, 1 एनजी से कम) के साथ ही नमूने अत्यधिक अपमानित साथ डीएनए। इन चुनौतियों का सामना करने के लिए, सबसे तरीकों शायद पीसीआर आधारित होगा, या तो एक multistep पीसीआर दृष्टिकोण या एक व्यापक समानांतर singleplex पीसीआर दृष्टिकोण जा रहा है। इसके अलावा, व्यक्तिगत amplicons की आणविक बारकोडिंग नाटकीय रूप से पृष्ठभूमि अनुक्रमण शोर को कम करने के लिए दिखाया गया है और निचले एलील आवृत्तियों को प्राप्त करने और circulat पर कब्जा करने की दिशा में कदम ट्यूमर कोशिकाओं के कम अनुपात के साथ नमूनों की जांच में सक्षम होगाट्यूमर कोशिकाओं हैैं।
कैंसर के नमूनों में इस रोग से जुड़े म्यूटेशन की जांच के लिए दशकों से देखभाल के मानक किया गया है। ऐतिहासिक, जीन अक्सर क्रमिक रूप से, एक जीन / एक्सॉन एक समय में एक उत्परिवर्तन परीक्षण दृश्य के अंत करने के लिए अग्रणी की पहचान के साथ परीक्षण किया गया। NGS के आगमन कि रसौली के साथ जुड़े रहे कई उत्परिवर्तन की पहचान करने के लिए अग्रणी समानांतर में कई तरह के कैंसर के साथ जुड़े कई जीन अनुक्रमण के लिए एक कम पक्षपातपूर्ण दृष्टिकोण के लिए अनुमति दी गई है। कैंसर में दैहिक उत्परिवर्तन का पता लगाने के लिए NGS के नैदानिक उपयोगिता तेजी से स्पष्ट है। दरअसल, ट्यूमर के नमूनों की NGS-आधारित विश्लेषण एक नया प्रतिमान है कि पारंपरिक, एकल जीन परीक्षण को चुनौती दी प्रतिनिधित्व करता है, लेकिन नैदानिक उपयोगिता बहुत स्पष्ट है। नैदानिक प्रयोगशालाओं आज इस शक्तिशाली प्रौद्योगिकी के अनुप्रयोग के साथ सावधान विधि सत्यापन और परीक्षण व्याख्या से शादी करने के लिए रोमांचक अवसर है।
Declarações
The authors have nothing to disclose.
Acknowledgements
लेखकों पांडुलिपि और उत्पादन में सहायता के पढ़ने के लिए डैनियल जंगली की सहायता को स्वीकार करना होगा।
Materials
| Genomic DNA ScreenTape | Agilent Technology | 5067-5365 | |
| Genomic DNA Reagents | Agilent Technology | 5067-5366 | |
| High Sensitivity D1000 ScreenTape | Agilent Technology | 5067-5584 | |
| High Sensitivity D1000 Reagents | Agilent Technology | 5067-5585 | |
| TapeStation 2200 | Agilent Technology | G2965A | |
| TapeStation Analysis Software | Agilent Technology | A.01.04 or higher | |
| 96-well Tube Storage Racks | Any Vendor | ||
| 15/50 ml Tube Rack | Any Vendor | ||
| 96-well Plate Rack | Any Vendor | ||
| Pipette, single-channel, 0.5–2.5 μL | Any Vendor | ||
| Pipette, single-channel, 1–10 μL | Any Vendor | ||
| Pipette, single-channel, 2–20 μL | Any Vendor | ||
| Pipette, single-channel, 10–100 μL | Any Vendor | ||
| Pipette, single-channel, 20–200 μL | Any Vendor | ||
| Pipette, single-channel, 100–1000 μL | Any Vendor | ||
| Serological Pipettor | Any Vendor | ||
| Vortexer | Any Vendor | ||
| Ice bucket | Any Vendor | ||
| Microcentrifuge (for tubes and strip tubes) | Any Vendor | ||
| Freezer, -20 °C | Any Vendor | ||
| 4 °C Refrigerator | Any Vendor | ||
| Water or Bead Bath | Any Vendor | ||
| Incubator (37 oC) | Any Vendor | ||
| Serological Pipettes, 1 mL | Any Vendor | ||
| Serological Pipettes, 5 mL | Any Vendor | ||
| Serological Pipettes, 10 mL | Any Vendor | ||
| Serological Pipettes, 25 mL | Any Vendor | ||
| Gloves | Any Vendor | ||
| Razor Blades/Scaples | Any Vendor | ||
| KimWipes | Any Vendor | ||
| 15 mL Conical Tube | Any Vendor | ||
| 50 mL Conical Tube | Any Vendor | ||
| Paper Towels | Any Vendor | ||
| 200 proof Ethanol | Any Vendor | Store in Flammable Cabinet | |
| 2-Propanol (Isopropanol) | Any Vendor | Store in Flammable Cabinet | |
| 25ml Reservoirs | Any Vendor | ||
| 10N NaOH | Any Vendor | ||
| Pipette, 8-channel, 1–10 μL | Any Vendor | ||
| Pipette, 8-channel, 10–100 μL | Any Vendor | ||
| Pipette, 8-channel, 20–300 μL | Any Vendor | ||
| Ice Bucket | Any Vendor | ||
| Water Squirt Bottle | Any Vendor | ||
| Alcohol Squirt Bottle | Any Vendor | ||
| Lens Cleaning Paper | Any Vendor | ||
| Plates, 96-well PCR, Semi-Skirted | Any Vendor | ||
| Tube strips, 8-well, 0.2 mL | Any Vendor | ||
| Agencourt AMPure XP Beads | Beckman Coulter | A63881 | |
| BioShake IQ or 3000-T elm | Bulldog Bio/Q.Instruments | 1808-0506/ 1808-0517 | |
| DropPlate96 S – LabChipDS | Caliper | 128876 | |
| DropPlate96 D – LabChipDS | Caliper | 132848 | |
| DropSense96 | Caliper (Trinean) | ||
| DropQuant Software | Caliper (Trinean) | ||
| Plate Sealing Film | Denville | B1212-5S | |
| Aluminum Seal Foil | Denville | B1212-6S | |
| Nuclease-Free, Pure Water System | EMD Millipore | ||
| 5424 centrifuge | Eppendorf | 22621408 | |
| 5804R centrifuge | Eppendorf | 22623508 | Both 15 ml tube and plate rotators, preferably a centrifuge that can go up to 2,500 x g. |
| Safe-Lock Tube 1.5 mL, Natural | Eppendorf | 22431021 | |
| 5 mL Tube, DNA LoBind Tube | Eppendorf | 30108310 | |
| 5430R Centrifuge | Eppendorf | 022620645 | Any plate rotator centrifuge will work |
| Hybex Microsample Incubator | Fisher Scientific | 1057-30-0 | |
| Hybex 0.2 mL Tube Block | Fisher Scientific | 1057-31-0 | |
| TruSeq Amplicon – Cancer Panel | Illumina | FC-130-1008 | 96 reactions |
| TruSeq Custom Amplicon | Illumina | PE-940-1011 | 96 reactions |
| TruSeq Custom Amplicon Index Kit | Illumina | FC-130-1003 | 96 Indices, 384 Samples |
| MiSeq Reagent Kit v3, 500 Cycles | Illumina | MS-102-3003 | |
| MiSeq Reagent Kit v2, 300 Cycles | Illumina | MS-102-2002 | |
| MiSeq Reagent Kit v2, 500 Cycles | Illumina | MS-102-2003 | |
| Experiment Manager | Illumina | 1.3 or higher | |
| MiSeq Reporter | Illumina | 2.0 or higher | |
| Sequencing Analysis Viewer | Illumina | 1.8 or higher | |
| TruSeq Index Plate Fixture and Collar Kit | Illumina | FC-130-1007 | |
| MiSeq v2 | Illumina | SY-410-1003 | |
| TruSeq Custom Amplicon Filter Plate | Illumina | FC-130-1006 | |
| Index Adapter Replacement Caps | Illumina | 11294657 | |
| Qubit 2.0 | Invitrogen | Q32866 | |
| Qubit 0.5 ml Tubes | Invitrogen | Q32856 | |
| Qubit dsDNA Broad Range Assay Kit | Invitrogen | Q32853 | |
| DynaMa6-96 Magnetic Stand, Side Skirted | Invitrogen | 120.27 | |
| GeneAmp PCR System 9700 (gold/silver block) | Life Technologies | N8050200 | |
| Gentra Puregene Blood Kit | Qiagen | 158489 | |
| Deparaffinization Solution (16ml) | Qiagen | 19093 | |
| Buffer ATL (4x50ml) | Qiagen | 939011 | |
| Protein Precipitation Solution (50 ml) | Qiagen | 158910 | |
| DNA Hydration Solution (100ml) | Qiagen | 158914 | |
| Glycogen Solution (500 μl) | Qiagen | 158930 | |
| Qiagen Proteinase K | Qiagen | 19133 | |
| Rnase (5ml) | Qiagen | 158924 | |
| Nuclease-Free Water (10 x 50 ml) | Qiagen | 129114 | |
| Pestles | USA Scientific | 1415-5390 | |
| TipOne RPT 10 ul elongated filter pipet tips in sterilized racks, 10 racks of 96 tips (960 tips). | USA Scientific | 1180-3810 | |
| TipOne RPT 100 ul natural, beveled filter pipet tips in sterilized racks, 10 racks of 96 tips (960 tips) | USA Scientific | 1180-1840 | |
| TipOne RPT 200 μl natural, beveled filter pipet tips in racks, sterilized racks, 10 racks of 96 tips (960 tips) | USA Scientific | 1180-8810 | |
| TipOne RPT 20 μl natural, beveled filter pipet tips in racks, sterilized racks, 10 racks of 96 tips (960 tips) | USA Scientific | 1180-1810 | |
| TipOne RPT 1000 μl natural, graduated XL filter pipet tips in | USA Scientific | 1182-1830 |
Referências
- Gerlinger, M., et al. Intratumor heterogeneity and branched evolution revealed by multiregion sequencing. N Engl J Med. 366 (10), 883-892 (2012).
- Campbell, P. J., et al. The patterns and dynamics of genomic instability in metastatic pancreatic cancer. Nature. 467 (7319), 1109-1113 (2010).
- Ding, L., et al. Clonal evolution in relapsed acute myeloid leukaemia revealed by whole-genome sequencing. Nature. 481 (7382), 506-509 (2012).
- Frampton, G. M., et al. Development and validation of a clinical cancer genomic profiling test based on massively parallel DNA sequencing. Nature Biotechnol. 31 (11), 1023-1031 (2013).
- Patel, J. P., et al. Prognostic relevance of integrated genetic profiling in acute myeloid leukemia. N Engl J Med. 366 (12), 1079-1089 (2012).
- Forbes, S. A., et al. COSMIC (the Catalogue of Somatic Mutations in Cancer ): a resource to investigate acquired mutations in human cancer. Nucleic Acids Res. 38 (Database Issue), 652-657 (2010).
- Shih, A. H., Abdel-wahab, O., Patel, J. P., Levine, R. L. The role of mutations in epigenetic regulators in myeloid malignancies. Nat Rev Cancer. 12 (9), 599-612 (2012).
- Liersch, R., Müller-Tidow, C., Berdel, W. E., Krug, U. Prognostic factors for acute myeloid leukaemia in adults – biological significance and clinical use. Br J Haematol. 165 (1), 17-38 (2014).
- Bacher, U., Schnittger, S., Haferlach, T. Molecular genetics in acute myeloid leukemia. Curr Opin Oncol. 22 (6), 646-655 (2010).
- Subramanian, J., Govindan, R. Lung cancer in "Never-smokers": a unique entity. Oncology (Williston Park). 24 (1), 29-35 (2010).
- Sakashita, S., Sakashita, M., Tsao, M. S. Genes and pathology of non-small cell lung carcinoma. Semin Oncol. 41 (1), 28-39 (2014).
- Arcila, M. E., Chaft, J. E., Nafa, K. Prevalence clinicopathologic associations, and molecular spectrum of ERBB2 (HER2) tyrosine kinase mutations in lung adenocarcinomas. Clin Cancer Res. 18 (18), (2012).
- Gandhi, L., et al. Phase I study of neratinib in combination with temsirolimus in patients with human epidermal growth factor receptor 2-dependent and other solid tumors. J Clin Oncol. 32 (2), 68-75 (2014).
- Sheikhha, M. H., Awan, A., Tobal, K., Liu Yin, J. A. Prognostic significance of FLT3 ITD and D835 mutations in AML patients. Hematol J. 4 (1), 41-46 (2003).
- Mazières, J., et al. Lung cancer that harbors an HER2 mutation epidemiologic characteristics and therapeutic perspectives. J Clin Oncol. 31 (16), 1-8 (2014).
- Robinson, J. T., et al. Integrative Genomics Viewer. Nat Biotechnol. 29 (1), 495-500 (2011).
- Forbes, S. A., et al. COSMIC: exploring the world’s knowledge of somatic mutations in human cancer. Nucleic Acids Res. 43 (Database issue), D805-D811 (2014).
- Daber, R., Sukhadia, S., Morrissette, J. J. Understanding the limitations of next generation sequencing informatics, an approach to clinical pipeline validation using artificial data sets. Cancer Genetics. 206 (12), 441-448 (2013).
- Haraksingh, R. R., et al. Genome-Wide Mapping of Copy Number Variation in Humans: Comparative Analysis of High Resolution Array Platforms. PLoS ONE. 6 (11), e27859 (2011).
- de Leeuw, N., et al. SNP Array Analysis in Constitutional and Cancer Genome Diagnostics – Copy Number Variants, Genotyping and Quality Control. Cytogenet Genome Res. 135 (3-4), 212-221 (2011).

