qPCRTag विश्लेषण - एक उच्च Throughput, Sc2.0 जीनोटाइपिंग के लिए वास्तविक समय पीसीआर परख
Summary
Designer chromosomes of the Synthetic Yeast Genome project, Sc2.0, can be distinguished from their native counterparts using a PCR-based genotyping assay called PCRTagging, which has a presence/absence endpoint. Here we describe a high-throughput real time PCR detection method for PCRTag genotyping.
Abstract
सिंथेटिक खमीर जीनोम परियोजना (Sc2.0) 16 डिजाइनर खमीर गुणसूत्रों का निर्माण और एक एकल खमीर सेल में उनके गठबंधन को करना है। एक कृत्रिम गुणसूत्र, synIII 1, और एक कृत्रिम गुणसूत्र हाथ, synIXR 2 तारीख को, निर्माण और उनके vivo समारोह इसी जंगली प्रकार गुणसूत्रों के अभाव में मान्य किया गया है। Sc2.0 गुणसूत्रों का एक महत्वपूर्ण डिजाइन सुविधा उनके जंगली प्रकार समकक्षों से सिंथेटिक क्रोमोसोम के भेदभाव है कि सक्षम खुला पढ़ने फ्रेम (ORFs) के भीतर कम, फिर से कोडित दृश्य हैं जो PCRTags की शुरूआत है। PCRTag सिंथेटिक या जंगली प्रकार गुणसूत्रों और एक साधारण पीसीआर परख का उपयोग कर परीक्षण किया जा सकता डीएनए के प्रत्येक प्रकार की उपस्थिति / अनुपस्थिति या तो चुनिंदा पानी रखना प्राइमरों। PCRTag परख के मानक readout के agarose जेल वैद्युतकणसंचलन द्वारा amplicons की उपस्थिति / अनुपस्थिति का आकलन करना है। हालांकि, 1.5 केबी और एजी के प्रति एक के एक औसत PCRTag amplicon के घनत्व के साथ~ 12 एमबी की enome आकार, पूरा Sc2.0 जीनोम लगभग 8,000 PCRTags सांकेतिक शब्दों में बदलना होगा। थ्रूपुट में सुधार करने के लिए, हम हम qPCRTag विश्लेषण कहते हैं कि PCRTag जीनोटाइपिंग के लिए एक वास्तविक समय पीसीआर आधारित पता लगाने परख विकसित किया है। कार्यप्रवाह हमें एक ही प्रयोग में सिंथेटिक और जंगली प्रकार प्राइमर जोड़े दोनों के साथ 768 PCRTags अप करने के लिए परीक्षण करने के लिए अनुमति देता है, एक 1536 multiwell थाली में 500 nl प्रतिक्रियाओं निर्दिष्ट करता है।
Introduction
Sc2.0, या कृत्रिम खमीर जीनोम परियोजना ( www.syntheticyeast.org ), डिजाइन और एक पूरी तरह से सिंथेटिक यूकेरियोटिक जीनोम के निर्माण का लक्ष्य निर्धारित किया है। एक प्रारंभिक बिंदु के रूप Saccharomyces cerevisiae 3 की अत्यधिक क्यूरेट जीनोम अनुक्रम का उपयोग करना, सोलह रेखीय गुणसूत्रों में से प्रत्येक कोशिका फिटनेस बनाए रखने के जीनोम की स्थिरता में सुधार, और आनुवंशिक लचीलापन बढ़ रही द्वारा निर्दिष्ट डिजाइन सिद्धांतों का एक सेट को पूरा करने के लिए फिर से तैयार किया गया है। उदाहरण के लिए, ऐसे दोहराता के रूप में अस्थिर तत्व Sc2.0 गुणसूत्रों से नष्ट हो जाती हैं। टैग रोक codons के सभी उदाहरणों में एक गैर आनुवंशिक रूप से इनकोडिंग अमीनो एसिड की शुरूआत के लिए अंतिम तनाव में एक कोडोन 'मुक्त' करने के लिए TAA करने के लिए फिर से कोडित रहे हैं। इसके साथ ही रचनात्मक-Lox प्रणाली द्वारा सक्षम एक inducible विकास प्रणाली, हाथापाई, उपन्यास संरचनाओं 4 के साथ व्युत्पन्न जीनोम उत्पन्न करने के लिए अभूतपूर्व क्षमता परमिट।
<p class="Jove_content"> Sc2.0 जीनोम में एक अन्य प्रमुख डिजाइन तत्व सिंथेटिक और जंगली प्रकार डीएनए की ट्रैकिंग सक्षम करने के लिए डीएनए वॉटरमार्क के रूप में सेवा जो PCRTags की शुरूआत है। PCRTags सिंथेटिक क्रोमोसोम पर ORFs में कम, फिर से कोडित खंडों कर रहे हैं; PCRTag दृश्यों सिंथेटिक और जंगली प्रकार गुणसूत्रों के बीच डीएनए के स्तर पर भिन्न होते हैं, जबकि इनकोडिंग प्रोटीन अमीनो एसिड अनुक्रम और इस तरह, शायद, समारोह में समान हैं। PCRTag दृश्यों विशेष रूप से चयनात्मक प्रवर्धन (चित्रा 1 ए) की सुविधा के लिए प्राइमर बाध्यकारी साइटों के रूप में तैयार कर रहे हैं। PCRTag डिजाइन आम तौर पर 58 डिग्री सेल्सियस और 60 डिग्री सेल्सियस के बीच पिघलने तापमान के साथ देशी दृश्यों (न्यूनतम 33%) की तुलना में ~ 60% अलग हैं कि कृत्रिम दृश्यों recoded उपज GeneDesign 5,6 में 'सबसे अलग' कलन विधि का उपयोग किया जाता है amplicon 200-500 आधार जोड़े 2 के बीच लंबाई। इन क्षेत्रों के लिए जाना जाता है के रूप में recoding, प्रत्येक ओआरएफ के पहले 100 बीपी के भीतर की अनुमति नहीं हैकोडोन उपयोग 7 के मामले में विशेष पसन्द है। साथ में, इन डिजाइन नियम सिंथेटिक और जंगली प्रकार PCRTag प्राइमर जोड़े को विशेष रूप से सिंथेटिक और देशी डीएनए, क्रमशः (चित्रा 1 बी) बाँध और बढ़ाना जिससे पीसीआर स्थितियों का एक सेट के तहत लगभग सभी PCRTags के उच्च प्रदर्शन के पक्ष में।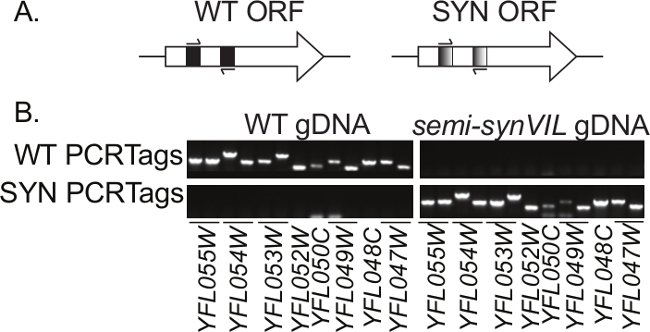
चित्रा 1:। PCRTag योजनाबद्ध (ए) PCRTags Sc2.0 गुणसूत्रों पर जीनों का खुला पढ़ने फ्रेम (ओआरएफ) के भीतर दृश्यों को फिर से कोडित रहे हैं। (बी) सिंथेटिक (SYN) और जंगली प्रकार (डब्ल्यूटी) PCRTag प्राइमरों विशेष रूप से क्रमशः, बाँध और (gDNA) सिंथेटिक और जंगली प्रकार जीनोमिक डीएनए बढ़ाना। टेम्पलेट के रूप में गुम्मट या अर्द्ध synVIL2 gDNA उपयोग कर या तो तेरह PCRTag प्राइमर जोड़े का परीक्षण गुणसूत्र छह की बाएं हाथ की एक ~ 30 केबी खंड के एक विश्लेषण, यहाँ दिखाया गया है। कई मामलों में एक भी ओआरएफ एक से अधिक पी encodesCRTag। PCRTag amplicons की उपस्थिति / अनुपस्थिति agarose जेल वैद्युतकणसंचलन के माध्यम से मूल्यांकन किया है। PCRTag amplicons के 200 बीपी से 500 बीपी को आकार में सीमा। पैनल के निचले भाग में तेजी से पलायन प्रजातियों प्राइमर dimers हैं।
PCRTag विश्लेषण Sc2.0 गुणसूत्रों की विधानसभा में एक महत्वपूर्ण उपकरण साबित हो गया है। 20-30 PCRTags एन्कोडिंग सिंथेटिक डीएनए के एक ठेठ प्रयोग 30-50 KB, में, इसी जंगली प्रकार डीएनए 1,2,8 को बदलने के लिए खमीर कोशिकाओं में तब्दील हो जाता है। PCRTag विश्लेषण तो डीएनए के उस खंड में फैले सिंथेटिक नहीं बल्कि जंगली प्रकार PCRTags सांकेतिक शब्दों में बदलना है कि transformants की पहचान के लिए प्रयोग किया जाता है, या '' विजेताओं तथाकथित। यह '' विजेताओं की पहचान है, इसलिए throughput और PCRTag विश्लेषण की लागत महत्वपूर्ण विचार कर रहे हैं करने के लिए कई transformants के परीक्षण करने के लिए आम तौर पर आवश्यक है। वर्तमान में दो Sc2.0 गुणसूत्रों Sc2.0 जीनोम का कम से कम 10% का प्रतिनिधित्व (synIII 1 और synIXR 2) पूरा हो चुका है, ऑल्टHough अधिक शेष गुणसूत्रों के आधे से अधिक वर्तमान में संश्लेषण और विधानसभा के दौर से गुजर रहे हैं। इस परियोजना के लिए आवश्यक PCRTag विश्लेषण के पैमाने तेजी से सिंथेटिक डीएनए और जंगली प्रकार डीएनए के अभाव की उपस्थिति जैल चलाने के लिए और मैन्युअल रूप में स्कोर करने की क्षमता outpacing है।
हम agarose जेल वैद्युतकणसंचलन का उपयोग नाकाम करने के लिए वास्तविक समय पीसीआर का उपयोग कर एक कार्यप्रवाह विकसित किया है PCRTag परख के throughput में सुधार करना। कार्यप्रवाह एक 1536 multiwell थाली, टेम्पलेट डीएनए और प्राइमरों स्थानांतरित करने के लिए एक nanoscale ध्वनिक तरल निकालने की मशीन के प्रत्येक कुएं में qPCR के mastermix वितरित करने के लिए एक थोक तरल निकालने की मशीन का उपयोग करता है, और एक 1536 qPCR के थर्मल cycler, हमें 500 nl करने के लिए प्रतिक्रियाओं miniaturize करने की इजाजत दी और throughput को अधिकतम। इसके अलावा विश्लेषण स्वचालित किया जा सकता है। उच्च throughput जीनोटाइपिंग प्रोटोकॉल के इस प्रकार के कई loci में कई क्लोन के विश्लेषण की आवश्यकता होती है किसी भी परियोजना के लिए generalizable होना चाहिए।
Protocol
Representative Results
Discussion
यह काफी उच्च throughput के लिए सक्षम बनाता है के रूप में PCRTag जीनोटाइपिंग परख में वास्तविक समय पीसीआर का पता लगाने के निगमन Sc2.0 परियोजना के लिए एक महत्वपूर्ण विकास है। पिछले कार्यप्रवाह 384 अच्छी तरह से पीसीआर प्लेट, 1.5 घंटा थर्मल साइकिल चलाते समय, agarose जेल वैद्युतकणसंचलन, और जेल के मार्गदर्शन एनोटेशन में 2.5 μl प्रतिक्रियाओं निर्दिष्ट।
qPCRTag विश्लेषण कहा जाता है यहाँ प्रस्तुत कार्यप्रवाह, कई प्रमुख बाधाओं पर काबू। सबसे पहले, एक qPCRTag चलाने के बारे में एक घंटे में खत्म (प्लेट की स्थापना के साथ साथ समय चलाने के लिए) के लिए शुरू, कार्रवाई की जा सकती है कि एक ही प्रयोग में 4 एक्स 384 अच्छी तरह प्लेटें संघनित। यह qPCRTag विश्लेषण के लिए अच्छी तरह से प्रति अभिकर्मक लागत कम throughput agarose जेल आधारित दृष्टिकोण के साथ बराबर है कि नोट करने के लिए महत्वपूर्ण है। हालांकि, जेल वैद्युतकणसंचलन और मैनुअल एनोटेशन circumventing द्वारा, qPCRTag कार्यप्रवाह प्रमुख लाभ कर रहे हैं, जो समय और श्रम में काफी बचत, परमिट। महत्वपूर्ण बात qPCRTag कार्यप्रवाह एन हैस्वचालन के साथ tirely संगत।
PCRTag परख के उत्पादन के रूप में वास्तविक समय का पता लगाने के उपयोग के साथ एक प्रमुख चिंता का विषय झूठी सकारात्मक और नकारात्मक झूठी की दर है। PCRTag प्राइमरों मूल रूप से वास्तविक समय पीसीआर में उपयोग के लिए तैयार नहीं थे के बाद से, यह नहीं है कि सभी प्राइमर जोड़े इस निर्गम के साथ प्रयोग के लिए उपयुक्त हो जाएगा कि उम्मीद है। यह अंत करने के लिए यह सामने तक वास्तविक समय आधारित परख में काम नहीं करते कि सबसेट बाहर करने के लिए सभी PCRTag प्राइमर जोड़े के समारोह और विशिष्टता को मान्य करने के लिए महत्वपूर्ण है। उदाहरण के लिए, गुणसूत्र 3 PCRTag झूठी सकारात्मक और नकारात्मक हैं दर-और-बड़े पीसीआर डेटा (आंकड़े 2 और 3) वास्तविक समय में प्रतिलिपि प्रस्तुत करने योग्य है और इन आगे के विश्लेषण से बाहर रखा जा सकता है। इसके अलावा, विफल करने के लिए जाना जाता है प्राइमर जोड़े (जेल वैद्युतकणसंचलन द्वारा मूल्यांकन और आंकड़े S6 और एट अल। 1 Annaluru की S7 में दिखाया गया है) भी बाहर रखा जा सकता है। यह आसानी से exclu बस पूरा किया हैडिंग ध्वनिक ट्रांसफर प्रोटोकॉल दोषपूर्ण प्राइमर जोड़े को स्थापित करते समय।
सबसे उच्च throughput assays के तरह, हम आगे बहाव के सत्यापन मिलने चाहिए transformants की पहचान करने के लिए एक प्राथमिक स्क्रीन के रूप में वास्तविक समय PCRTag पता लगाने का उपयोग करना चाहते हैं। बाद में, माध्यमिक स्क्रीनिंग के लिए स्वर्ण मानक readout के रूप में जेल वैद्युतकणसंचलन के साथ PCRTag विश्लेषण रहेगा। उच्च throughput वास्तविक समय पीसीआर तकनीक के साथ राज्य के-कला के nanoscale तरल प्रणाली से निपटने के संयोजन Sc2.0 के लिए PCRTag विश्लेषण के आवेदन, परे तेजी से और स्वचालित विश्लेषण में सक्षम बनाता है और कई क्षेत्रों को प्रभावित करने की क्षमता है। उदाहरण के लिए, इस कार्यप्रवाह उच्च throughput पुस्तकालय स्क्रीनिंग, संक्रामक रोग निदान, microbiome विश्लेषण, और अत्याधुनिक जीनोम संपादन करने के लिए लागू किया जा सकता है एक साथ कई स्थलों को संशोधित करने के लिए प्रयास दृष्टिकोण।
Declarações
The authors have nothing to disclose.
Acknowledgements
इस काम के द्वारा समर्थित किया गया था राष्ट्रीय विज्ञान फाउंडेशन अनुदान एमसीबी-0718846 और (JDB तक) रक्षा एडवांस्ड रिसर्च प्रोजेक्ट्स एजेंसी के अनुबंध N66001-12-सी-4020। लैम प्राकृतिक विज्ञान और कनाडा के इंजीनियरिंग रिसर्च काउंसिल से एक postdoctoral फैलोशिप द्वारा वित्त पोषित किया गया। इस लेख के प्रकाशन रॉश द्वारा प्रायोजित है।
Materials
| Yeast gDNA prep | |||
| yeast gDNA | custom | custom | template for real time PCR |
| Acid-washed glass beads (0.5mm) | Sigma | G8772 | yeast cell lysis |
| Ultrapure Phenol:Chloroform:Isoamyl Alcohol (25:24:1, v/v) | Invitrogen | 15593-031 | yeast cell lysis |
| 5432 Mixer | Eppendorf | 5432 | yeast cell lysis |
| Microcentrifuge 5417R | Eppendorf | 22621807 | yeast cell lysis |
| Qubit 3.0 Fluorometer | Life Technologies | Q33216 | gDNA quantification |
| Qubit dsDNA BR Assay Kit | Life Technologies | Q32850 | gDNA quantification |
| Labcyte 384PP plate | Labcyte | P-05525 | gDNA source plate |
| DNA Green Mastermix prep and dispensing | |||
| LightCycler 1536 DNA Green | Roche | 5573092001 | real time PCR mastermix |
| 1.5mL Microfuge Tube Holder | ARI | EST BD060314-1 | microfuge tube holder for deck of Cobra |
| LightCycler 1536 Multiwell Plate | Roche | 5358639001 | |
| Cobra liquid handling system | Art Robbins Instruments | 630-1000-10 | dispense qPCR master mix into 1536 plate |
| PCR Plate Spinner | VWR | 89184-608 | cenrifugation of 1536 plate |
| Template and primer dispensing | |||
| PCRTag primers | IDT | custom | premixed forward and reverse, [50uM] each |
| TempPlate pierceable sealing foil, sterile | USA Scientific | 2923-0110 | temporary seal for PCRTag primer plates |
| Labcyte LDV 384 well plate | Labcyte | LP-0200 | pre-mixed primer source plate |
| Echo 550 Liquid Handler | Labcyte | transfer 2.5nL drops of primer and template DNA into 1536 plate | |
| Plateloc Thermal Microplate Sealer | Agilent | G5402-90001 | heat seal for 1536 plate prior to LC1536 run |
| Clear Permanent Seal | Agilent | 24212-001 | optically clear heat seal for LC1536 multiwell plate |
| PlateLoc Roche/LightCycler 1536 Plate Stage | Agilent | G5402-20008 | can substitute ~2mm thick washers |
| Sorvall Legend XTR | Thermo Scientfic | 75-004-521 | centrifuge heat sealed 1536 plate |
| Industrial Air Compressor | Jun Air | 1795011 | to run the Echo and Heat Sealer |
| Real Time PCR | |||
| LightCycler 1536 | Roche | requires 220V outlet |
Referências
- Annaluru, N., et al. Total synthesis of a functional designer eukaryotic chromosome. Science. 344 (6179), 55-58 (2014).
- Dymond, J. S., et al. Synthetic chromosome arms function in yeast and generate phenotypic diversity by design. Nature. 477 (7365), 471-476 (2011).
- Goffeau, A., et al. Life with 6000 genes. Science. 274 (5287), 546-547 (1996).
- Dymond, J., Boeke, J. The Saccharomyces cerevisiae SCRaMbLE system and genome minimization. Bioeng Bugs. 3 (3), 168-171 (2012).
- Richardson, S. M., Nunley, P. W., Yarrington, R. M., Boeke, J. D., Bader, J. S. GeneDesign 3.0 is an updated synthetic biology toolkit. Nucleic Acids Res. 38 (8), 2603-2606 (2010).
- Richardson, S. M., Liu, S., Boeke, J. D., Bader, J. S. Design-A-Gene with GeneDesign. Methods Mol Biol. 852, 235-247 (2012).
- Lajoie, M. J., et al. Probing the limits of genetic recoding in essential genes. Science. 342 (6156), 361-363 (2013).
- Jovicevic, D., Blount, B. A., Ellis, T. Total synthesis of a eukaryotic chromosome: Redesigning and SCRaMbLE-ing yeast. Bioessays. 36 (9), 855-860 (2014).
- Dymond, J. S. Preparation of genomic DNA from Saccharomyces cerevisiae. Methods Enzymol. 529, 153-160 (2013).
- Brachmann, C. B., et al. Designer deletion strains derived from Saccharomyces cerevisiae S288C: a useful set of strains and plasmids for PCR-mediated gene disruption and other applications. Yeast. 14 (2), 115-132 (1998).

