डीएनए मिथाइलेशन के जैव सूचना विज्ञान विश्लेषण के लिए नमूना तैयारी: मोटापे और संबंधित विशेषता अध्ययन के लिए एसोसिएशन रणनीति
Summary
वर्तमान अध्ययन माइक्रोएरे प्रौद्योगिकियों द्वारा प्राप्त डीएनए मिथाइलेशन डेटा का प्रबंधन करने के लिए वर्कफ़्लो का वर्णन करता है। प्रोटोकॉल नमूना तैयारी से डेटा विश्लेषण तक के चरणों को प्रदर्शित करता है। सभी प्रक्रियाओं को विस्तार से वर्णित किया गया है, और वीडियो महत्वपूर्ण चरणों को दिखाता है।
Abstract
मोटापा सीधे जीवन शैली से जुड़ा हुआ है और डीएनए मिथाइलेशन परिवर्तनों से जुड़ा हुआ है जो रोग के विकास में योगदान देने वाली एडिपोजेनेसिस और लिपिड भंडारण प्रक्रियाओं में परिवर्तन का कारण बन सकता है। हम मोटापे के साथ और बिना रोगियों के एपिजेनेटिक डेटा विश्लेषण के लिए चयन से एक पूर्ण प्रोटोकॉल प्रदर्शित करते हैं। प्रोटोकॉल के सभी चरणों का परीक्षण किया गया था और एक पायलट अध्ययन में मान्य किया गया था। अध्ययन में 32 महिलाओं ने भाग लिया, जिसमें 15 व्यक्तियों को बॉडी मास इंडेक्स (बीएमआई) (45.1 ± 5.4 किलोग्राम / एम 2) के अनुसार मोटापे के साथ वर्गीकृत किया गया था; और 17 व्यक्तियों को बीएमआई (22.6 ± 1.8 किलोग्राम / एम 2) के अनुसार मोटापे के बिना वर्गीकृत किया गया था। मोटापे के साथ समूह में, वसा द्रव्यमान से संबंधित 564 सीपीजी साइटों को रैखिक प्रतिगमन विश्लेषण द्वारा पहचाना गया था। सीपीजी साइटें प्रमोटर क्षेत्रों में थीं। विभेदक विश्लेषण में मोटापे वाले व्यक्तियों में 470 सीपीजी हाइपोमेथिलेटेड और 94 हाइपरमेथिलेटेड साइटें पाई गईं। सबसे hypomethylated समृद्ध pathways RUNX, WNT सिग्नलिंग, और हाइपोक्सिया की प्रतिक्रिया में थे। हाइपरमेथिलेटेड मार्ग इंसुलिन स्राव, ग्लूकागन सिग्नलिंग और Ca2 + से संबंधित थे। हम निष्कर्ष निकालते हैं कि प्रोटोकॉल ने प्रभावी रूप से डीएनए मिथाइलेशन पैटर्न और विशेषता से संबंधित डीएनए मिथाइलेशन की पहचान की। इन पैटर्नों को परिवर्तित जीन अभिव्यक्ति के साथ जोड़ा जा सकता है, जो एडिपोजेनेसिस और लिपिड भंडारण को प्रभावित करता है। हमारे परिणामों ने पुष्टि की कि एक ओबेसोजेनिक जीवन शैली मानव डीएनए में एपिजेनेटिक परिवर्तनों को बढ़ावा दे सकती है।
Introduction
बड़े पैमाने पर ओमिक्स प्रौद्योगिकियों का उपयोग पुरानी बीमारियों के अध्ययन में तेजी से किया गया है। इन विधियों की एक दिलचस्प विशेषता वैज्ञानिक समुदाय के लिए बड़ी मात्रा में उत्पन्न डेटा की उपलब्धता है। इसलिए, अध्ययनों के बीच तकनीकी तुलना की अनुमति देने के लिए प्रोटोकॉल को मानकीकृत करने की मांग उत्पन्न हुई है। वर्तमान अध्ययन डीएनए मिथाइलेशन डेटा प्राप्त करने और विश्लेषण करने के लिए एक प्रोटोकॉल के मानकीकरण का सुझाव देता है, एक लागू उदाहरण के रूप में एक पायलट अध्ययन का उपयोग करता है।
नकारात्मक ऊर्जा व्यय आधुनिक मानव जीवन शैली में प्रबल होता है, जिससे वसा ऊतक का अत्यधिक संचय होता है और परिणामस्वरूप, मोटापे का विकास होता है। कई कारकों ने मोटापे की दर में वृद्धि की है, जैसे कि sedentarism, उच्च कैलोरी आहार, और तनावपूर्ण दिनचर्या। विश्व स्वास्थ्य संगठन (डब्ल्यूएचओ) का अनुमान है कि 2016 में 1.9 बिलियन वयस्क मोटापे से ग्रस्त थे, जिसका अर्थ है कि दुनिया की 20% से अधिक आबादी में 30 किलोग्राम / एम 2 बीएमआई 2 है। 2018 के सबसे हालिया अपडेट से पता चला कि संयुक्त राज्य अमेरिका (यूएसए) में मोटापे का प्रसार 42% 3 से अधिक था।
एपिजेनेटिक्स गुणसूत्र क्षेत्रों का संरचनात्मक अनुकूलन है जो परिवर्तित गतिविधि राज्यों को पंजीकृत करने, संकेत देने या बनाए रखने के लिए है। डीएनए मेथिलिकरण साइटोसिन-गुआनोसिन डाइन्यूक्लियोटाइड्स साइटों (सीपीजी साइटों) में एक प्रतिवर्ती रासायनिक परिवर्तन है, जो 5-मिथाइलसाइटोसिन-पीजी (5mCpG) बनाता है। यह डीएनए 5,6,7,8 के लिए प्रतिलेखन मशीनरी की पहुंच को विनियमित करके जीन अभिव्यक्ति को संशोधित कर सकता है। इस संदर्भ में, यह समझना आवश्यक है कि कौन सी सीपीजी साइटें मोटापे से संबंधित लक्षणों से जुड़ी हैं। कई कारक साइट-विशिष्ट डीएनए मिथाइलेशन का समर्थन या रोकथाम कर सकते हैं। इस प्रक्रिया के लिए आवश्यक एंजाइम, जैसे कि डीएनए मिथाइलट्रांसफरेज़ 10 (DNTMs) और दस-ग्यारह ट्रांसलोकेशन (TETs), पर्यावरणीय एक्सपोज़र 11 के तहत डीएनए मिथाइलेशन या डिमिथाइलेशन को बढ़ावा दे सकते हैं।
पिछले वर्षों में डीएनए मेथिलिकरण अध्ययनों में बढ़ती रुचि को ध्यान में रखते हुए, प्रत्येक प्रश्न का सटीक उत्तर देने के लिए सबसे उपयुक्त विश्लेषण रणनीति चुनना शोधकर्ताओं की एक आवश्यक चिंता का विषय रहा है12,13,14। 450K डीएनए मिथाइलेशन सरणी सबसे लोकप्रिय विधि है, जिसका उपयोग डीएनए मिथाइलेशन प्रोफ़ाइल को निर्धारित करने के लिए 360 से अधिक प्रकाशनों 14 में किया जाता है। यह ज्ञात जीन 15 के 99% में स्थित 485,000 सीपीजी तक के मिथाइलेशन को निर्धारित कर सकता है। हालांकि, इस सरणी को बंद कर दिया गया है और ईपीआईसी के साथ बदल दिया गया है, जिसमें 850,000 सीपीजी साइटों को शामिल किया गया है। वर्तमान प्रोटोकॉल को 450K और EPIC16,17,18 दोनों के लिए लागू किया जा सकता है।
प्रोटोकॉल को चित्रा 1 में चरण-दर-चरण प्रस्तुत किया गया है और इसमें निम्नलिखित चरण शामिल हैं: जनसंख्या चयन, नमूनाकरण, प्रयोग की तैयारी, डीएनए मिथाइलेशन पाइपलाइन, और जैव सूचना विज्ञान विश्लेषण। प्रस्तावित प्रोटोकॉल के चरणों को स्पष्ट करने के लिए हमारी प्रयोगशाला में किए गए एक पायलट अध्ययन को यहां प्रदर्शित किया गया है।
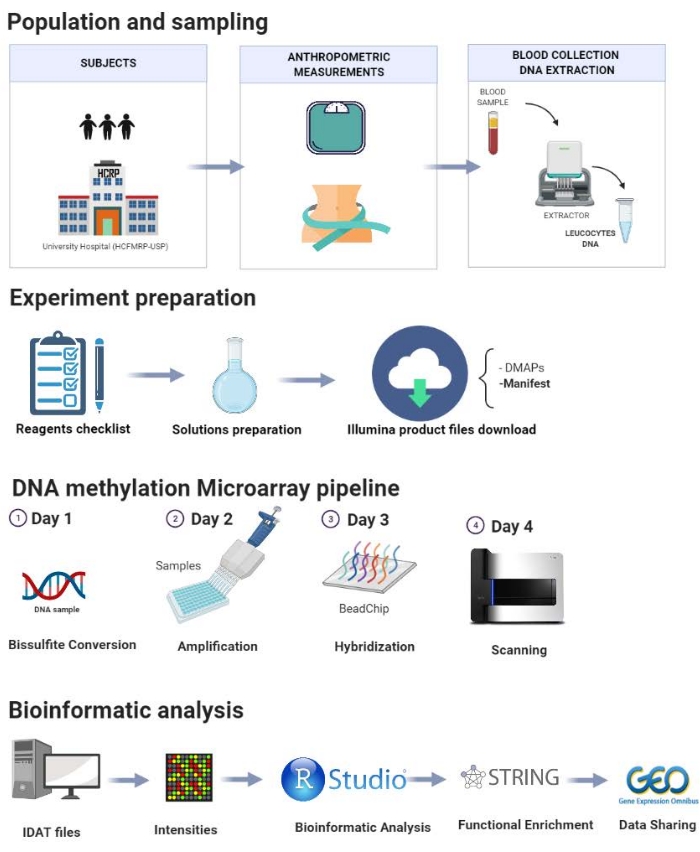
चित्र 1: प्रस्तुत प्रोटोकॉल की योजनाबद्ध. कृपया इस आकृति का एक बड़ा संस्करण देखने के लिए यहाँ क्लिक करें.
Protocol
Representative Results
Discussion
डीएनए मिथाइलेशन सरणियां उनकी लागत-लाभ अनुपात 14 के कारण डीएनए मिथाइलेशन तक पहुंचने के लिए सबसे अधिक उपयोग की जाने वाली विधियां हैं। वर्तमान अध्ययन ने ब्राजील के एक समूह में किए गए पायलट अध्ययन में डीएनए मिथाइलेशन का मूल्यांकन करने के लिए व्यावसायिक रूप से उपलब्ध माइक्रोएरे प्लेटफॉर्म का उपयोग करके एक विस्तृत प्रोटोकॉल का वर्णन किया। पायलट अध्ययन से प्राप्त परिणामों ने प्रोटोकॉल की प्रभावशीलता की पुष्टि की। चित्रा 3 नमूना तुलनात्मकता और पूर्ण bisulfite रूपांतरण 32 से पता चलता है.
एक गुणवत्ता नियंत्रण चरण के रूप में, CHAMP एल्गोरिथ्म फ़िल्टरिंग प्रक्रिया के दौरान CpGs साइटों के बहिष्करण की सिफारिश की। जांच को बाहर करने का उद्देश्य डेटा विश्लेषण में सुधार करना और पूर्वाग्रह को खत्म करना है। डेटासेट में प्रयोगात्मक शोर को खत्म करने के लिए कम गुणवत्ता वाले CpGs (0.05 से कम p-मान) को हटा दिया गया था। लक्ष्य घनत्व प्लॉट विश्लेषण में पारित रहे। Zhou33 ने बेमेल से बचने के लिए एसएनपी के पास सीपीजी को फ़िल्टर करने के महत्व का वर्णन किया, बहुरूपी साइटोसिन के मिथाइलेशन की गलत व्याख्या, और प्रकार के स्विच रंग का कारण बनता है मैं डिजाइन 34 की जांच करता हूं। इसके अलावा, जैसा कि XY गुणसूत्रों को छापने से अलग-अलग प्रभावित किया जाता है, Heiss और Just35 ने उन जांचों को फ़िल्टर करने के महत्व को मजबूत किया क्योंकि, महिलाओं में, संकरण के साथ समस्याएं भ्रमित कारक हो सकती हैं35।
DMAPs की समय सीमा समाप्ति तिथि, formamide खोलने की तारीख, पूर्ण इथेनॉल की विश्लेषणात्मक गुणवत्ता, और कुल ल्यूकोसाइट गिनती प्रोटोकॉल में महत्वपूर्ण कदम माना जाता है।
इसके अलावा, हमारी टिप्पणियों के अनुसार, जैव सूचना विज्ञान विश्लेषण करने में सेल-प्रकार का अनुमान आवश्यक है। हाउसमैन विधि सेल प्रकार का अनुमान लगाती है जैसा कि तियान के अध्ययन 30 में वर्णित है। यह विधि 473 विशिष्ट सीपीजी साइटों पर आधारित है जो सबसे महत्वपूर्ण सेल प्रकारों के प्रतिशत की भविष्यवाणी कर सकती हैं, जैसे कि ग्रैनुलोसाइट्स, मोनोसाइट्स, बी कोशिकाएं और टी सेल 36। हम ChAMP पैकेज से अनुशंसित फ़ंक्शन “myRefbase” का उपयोग किया। अनुमान के बाद, CHAMP एल्गोरिथ्म बीटा मूल्यों को समायोजित करता है और डेटासेट से इस पूर्वाग्रह को समाप्त करता है। यह कदम मोटापे पर केंद्रित अध्ययनों में महत्वपूर्ण है क्योंकि इस आबादी में उनकी पुरानी भड़काऊ स्थिति के कारण सफेद रक्त कोशिकाओं में काफी अंतर है।
हमने केवल विधि संशोधन और समस्या निवारण के बारे में सामान्य पीसीआर सील के लिए मूल कैप मानचित्र को बदल दिया है। प्रत्येक centrifugation प्रक्रिया के बाद, सील एक नए एक के लिए बदल दिया गया था। हम मानक गर्मी सील का उपयोग नहीं कर सका और प्लेट के चारों ओर एल्यूमीनियम पन्नी का उपयोग करके इसे अनुकूलित किया।
यद्यपि वाणिज्यिक assays epigenetic अध्ययन के लिए एक सोने का मानक माना जाता है, प्रोटोकॉल की एक सीमा एक अद्वितीय ब्रांड 37,38,39,40 से अभिकर्मकों और उपकरणों की विशिष्टता हो सकती है। एक और सीमा संकेतकों की कमी है जो प्रयोग 41 की सही प्रगति की पहचान की अनुमति देती है।
वर्तमान प्रोटोकॉल का मानकीकरण एपिजेनेटिक अनुसंधान के लिए एक महान मार्गदर्शिका का प्रतिनिधित्व करता है, प्रक्रिया के दौरान मानव त्रुटियों को कम करता है और विभिन्न अध्ययनों के बीच सफल डेटा विश्लेषण और तुलनात्मकता की अनुमति देता है।
हमारे परिणामों के अनुसार, डीएनए मेथिलिकरण प्रयोग मोटापे के साथ और बिना व्यक्तियों की तुलना करने वाले अध्ययनों के लिए उपयुक्त हैं43। इसके अलावा, प्रस्तावित जैव सूचना विज्ञान विश्लेषण ने उच्च गुणवत्ता वाले डेटा प्रदान किए और बड़े पैमाने पर अध्ययनों में विचार किया जा सकता है।
एसवीडी विश्लेषण का उपयोग करते हुए, हमने पहचान की कि मोटापे से संबंधित लक्षण (बीएमआई, डब्ल्यूसी और एफएम) ने डीएनए मिथाइलेशन डेटा में परिवर्तनशीलता को प्रभावित किया। एक महत्वपूर्ण परिणाम के रूप में, सेल-प्रकार का अनुमान इंगित करता है कि प्राकृतिक हत्यारा कोशिकाएं (एनके) और बी कोशिकाएं मोटापे के बिना महिलाओं की तुलना में मोटापे वाली महिलाओं में अधिक थीं (चित्रा 5)। उन कोशिकाओं की उच्च गिनती को इन व्यक्तियों की निम्न-श्रेणी की भड़काऊ स्थिति द्वारा समझाया जा सकता है44। हमने देखा कि मोटापे वाले रोगियों में वसा द्रव्यमान से जुड़े जीन के प्रमोटर क्षेत्रों में हाइपो- और हाइपरमेथिलेटेड सीपीजी होते हैं। अधिकांश साइटें हाइपोमेथिलेटेड थीं, जो इन व्यक्तियों में प्रतिक्रियाशील ऑक्सीजन प्रजातियों (आरओएस) के स्तर में प्राकृतिक वृद्धि से संबंधित हो सकती हैं। यह ऑक्सीडेटिव तनाव की स्थिति डाइन्यूक्लियोटाइड साइट पर गुआनिन बेचैनी को बढ़ावा दे सकती है, जिससे 8-hydroxy-2′-deoxyguanosine (8-OHdG) का निर्माण होता है, जिसके परिणामस्वरूप 5mCp-8-OHdG डाइन्यूक्लियोटाइड साइट होती है, और TET एंजाइमों की भर्ती होती है। ये सभी घटनाएं कार्रवाई के विभिन्न तंत्रों द्वारा डीएनए हाइपोमिथाइलेशन और हाइपरमिथाइलेशन को बढ़ावा देने के लिए जिम्मेदार हो सकती हैं45।
इसके अलावा, मोटापे वाले व्यक्तियों में एडिपोजेनेसिस की दर बढ़ जाती है, जिसमें पुरानी कोशिकाओं के लिए लगभग 10% नई कोशिकाएं होती हैं46,47। एपिजेनेटिक योगदान, ओबीजोजेनिक वातावरण पर जोर देते हुए, कोशिकाओं के प्रसार और भेदभाव दरों को बदल सकते हैं, वसा द्रव्यमान 48 के विकास के पक्ष में। एपिजेनेटिक परिवर्तन भी एडिपोजेनिक कार्यक्रमों को प्रभावित कर सकते हैं, उनके विकास को सुविधाजनक या प्रतिबंधित कर सकते हैं। प्राथमिक प्रतिलेखन कारक (पीपीएआर या सी / ईबीपीα) या मल्टीप्रोटीन कॉम्प्लेक्स की असेंबली, एपिजेनेटिक संशोधित एंजाइमों को शामिल करने या बाहर करने के द्वारा संचालित डाउनस्ट्रीम प्रमोटर क्षेत्रों में स्थित है, हाइपर- या हाइपोमिथाइलेशन 45 के माध्यम से जीन अभिव्यक्ति को विनियमित करती है। पीपीएआर मार्ग को पहले डब्ल्यूएनटी मार्ग को बदलने के लिए वर्णित किया गया है, जिसमें इस अध्ययन में जीन समृद्ध थे। हालांकि यह अभी भी अज्ञात है कि एडिपोजेनेसिस के दौरान डब्ल्यूएनटी सिग्नलिंग कैसे होती है, हाल के अध्ययनों ने बताया है कि यह एडिपोसाइट चयापचय में आवश्यक भूमिका निभा सकता है, विशेष रूप से ओबेसोजेनिक स्थितियों के तहत।
Disclosures
The authors have nothing to disclose.
Acknowledgements
हम युआन तियान, पीएचडी (tian.yuan@ucl.ac.uk) को CHAMP पैकेज के बारे में सभी संदेहों का जवाब देने के लिए उपलब्ध होने के लिए धन्यवाद देना चाहते हैं। हम इस पेपर से तकनीकी और वैज्ञानिक दोनों मुद्दों पर उनके योगदान के लिए Guilherme Telles, Msc. को भी धन्यवाद देते हैं; उन्होंने एपिजेनेटिक्स और वीडियो कैप्चरिंग और स्वरूपण तकनीकों (guilherme.telles@usp.br) के बारे में महत्वपूर्ण विचार किए। उपभोग्य वित्तपोषण: साओ पाउलो रिसर्च फाउंडेशन (FAPESP) (# 2018/24069-3) और वैज्ञानिक और तकनीकी विकास के लिए राष्ट्रीय परिषद (CNPq: #408292/ व्यक्तिगत वित्त पोषण: (FAPESP: # 2014/ 16740-6) और उच्च शिक्षा स्टाफ विकास के लिए समन्वय से अकादमिक उत्कृष्टता कार्यक्रम (CAPES: 88882.180020/ 2018-01)। डेटा को सार्वजनिक रूप से और स्वतंत्र रूप से बिना किसी प्रतिबंध के उपलब्ध कराया जाएगा। NYN (ई-मेल: nataliayumi@usp.br) या CBN (ई-मेल: carla@fmrp.usp.br) को पता पत्राचार.
Materials
| Absolute ethanol | J.T. Baker | B5924-03 | |
| Agarose gel | Kasvi | K9-9100 | |
| Electric bioimpedance | Quantum BIA 450 Q – RJL System | ||
| Ethylenediaminetetraacetic acid (EDTA) | Corning | 46-000-CI | |
| EZ DNA Methylation-Gold kit | ZymoResearch, Irvine, CA, USA | D5001 | |
| Formamide | Sigma | F9037 | |
| FMS—Fragmentation solution | Illumina | 11203428 | Supplied Reagents |
| HumanMethylation450 BeadChip | Illumina | ||
| Maxwell Instrument | Promega, Brazil | AS4500 | |
| MA1—Multi-Sample Amplification 1 Mix | Illumina | 11202880 | Supplied Reagents |
| MicroAmp Optical Adhesive Film | Thermo Fisher Scientific | 201703982 | |
| MSM—Multi-Sample Amplification Master Mix | Illumina | 11203410 | Supplied Reagents |
| NaOH | F. MAIA | 114700 | |
| PB1—Reagent used to prepare BeadChips for hybridization | Illumina | 11291245 | Supplied Reagents |
| PB2—Humidifying buffer used during hybridization | Illumina | 11191130 | Supplied Reagents |
| 2-propanol | Emsure | 10,96,34,01,000 | |
| RA1—Resuspension, hybridization, and wash solution | Illumina | 11292441 | Supplied Reagents |
| RPM—Random Primer Mix | Illumina | 15010230 | Supplied Reagents |
| STM—Superior Two-Color Master Mix | Illumina | 11288046 | Supplied Reagents |
| TEM—Two-Color Extension Master Mix | Illumina | 11208309 | Supplied Reagents |
| Ultrapure EDTA | Invitrogen | 155576-028 | |
| 96-Well Reaction Plate with Barcode (0.1mL) | ByoSystems | 4346906 | |
| 96-Well Reaction Plate with Barcode (0.8mL) | Thermo Fisher Scientific | AB-0859 | |
| XC1—XStain BeadChip solution 1 | Illumina | 11208288 | Supplied Reagents |
| XC2—XStain BeadChip solution 2 | Illumina | 11208296 | Supplied Reagents |
| XC3—XStain BeadChip solution 3 | Illumina | 11208392 | Supplied Reagents |
| XC4—XStain BeadChip solution 4 | Illumina | 11208430 | Supplied Reagents |
References
- Manna, P., Jain, S. Obesity, oxidative stress, adipose tissue dysfunction, and the associated health risks: causes and therapeutic strategies. Metabolic Syndrome and Related Disorders. 13 (10), 423-444 (2015).
- . Obesity Available from: https://www.who.int/health-topics/obesity#tab=tab_1 (2017)
- Adult Obesity Facts. Center for Disease Control and Prevention Available from: https://www.cdc.gov/obesity/data/adult.html (2021)
- Bird, A. Perceptions of epigenetics. Nature. 396, (2007).
- Kouzarides, T. Chromatin modifications, and their function. Cell. 128 (4), 693-705 (2007).
- Berger, F. The strictest usage of the term epigenetic. Seminars in Cell & Developmental Biology. 19 (6), 525-526 (2008).
- Henikoff, S., Greally, J. M. Epigenetics, cellular memory, and gene regulation. Current Biology. 26 (14), 644-648 (2016).
- Laker, R. C., et al. Transcriptomic and epigenetic responses to short-term nutrient-exercise stress in humans. Scientific Reports. 7 (1), 1-12 (2017).
- Wahl, S., et al. Epigenome-wide association study of body mass index, and the adverse outcomes of adiposity. Nature. 541, 81-86 (2017).
- Jin, B., Robertson, K. D. DNA methyltransferases, DNA damage repair, and cancer. Epigenetic Alterations in Oncogenesis. 754, 3-29 (2013).
- Jang, H. S., Shin, W. J., Lee, J. E., Do, J. T. CpG and non-CpG methylation in epigenetic gene regulation and brain function. Genes. 8 (6), 148 (2017).
- Shen, L., Waterland, R. A. Methods of DNA methylation analysis. Current Opinion in Clinical Nutrition & Metabolic Care. 10 (5), 576-581 (2007).
- Olkhov-Mitsel, E., Bapat, B. Strategies for discovery and validation of methylated and hydroxymethylated DNA biomarkers. Cancer Medicine. 1, 237-260 (2012).
- Kurdyukov, S., Bullock, M. DNA methylation analysis: choosing the right method. Biology. 5 (1), 3 (2016).
- Yong, W. -. S., Hsu, F. -. M., Chen, P. -. Y. Profiling genome-wide DNA methylation. Epigenetics & Chromatin. 9 (1), 1-16 (2016).
- Dugué, P. A., et al. Alcohol consumption is associated with widespread changes in blood DNA methylation: Analysis of cross-sectional and longitudinal data. Addiction Biology. 1, 12855 (2021).
- Colicino, E., et al. Blood DNA methylation sites predict death risk in a longitudinal study of 12, 300 individuals. Aging. 14, 14092-14124 (2020).
- Karlsson, L., Barbaro, M., Ewing, E., Gomez-Cabrero, D., Lajic, S. Genome-wide investigation of DNA methylation in congenital adrenal hyperplasia. The Journal of Steroid Biochemistry and Molecular Biology. 201, 105699 (2020).
- Ribeiro, R. R., Guerra-Junior, G., de Azevedo Barros-Filho, A. Bone mass in schoolchildren in Brazil: the effect of racial miscegenation, pubertal stage, and socioeconomic differences. Journal of Bone and Mineral Metabolism. 27 (4), 494-501 (2009).
- Filozof, C., et al. Obesity prevalence and trends in Latin-American countries. Obesity Reviews. 2 (2), 99-106 (2001).
- Chadid, S., Kreger, B. E., Singer, M. R., Bradlee, M. L., Moore, L. L. Anthropometric measures of body fat and obesity-related cancer risk: sex-specific differences in Framingham Offspring Study adults. International Journal of Obesity. 44 (3), 601-608 (2020).
- Nicoletti, C. F., et al. DNA methylation pattern changes following a short-term hypocaloric diet in women with obesity. European Journal of Clinical Nutrition. 74 (9), 1345-1353 (2020).
- Assessing Your Weight. Centers for Disease Control and Prevention Available from: https://www.cdc.gov/healthyweight/assessing/index.html (2020)
- Giavarina, D., Lippi, G. Blood venous sample collection: Recommendations overview and a checklist to improve quality. Clinical Biochemistry. 50 (10-11), 568-573 (2017).
- Duijs, F. E., Sijen, T. A rapid and efficient method for DNA extraction from bone powder. Forensic Science International: Reports. 2, 100099 (2020).
- . Infinium HD Methylation Assay, Manual Protocol Available from: https://support.illumina.com/content/dam/illumina-support/documents/documentation/chemistry_documentation/infinium_assays/infinium_hd_methylation/infinium-hd-methylation-guide-15019519-01.pdf (2015)
- Serrano, J., Snuderl, M. Whole genome DNA methylation analysis of human glioblastoma using Illumina BeadArrays. Glioblastoma. , 31-51 (2018).
- Leti, F., Llaci, L., Malenica, I., DiStefano, J. K. Methods for CpG methylation array profiling via bisulfite conversion. Disease Gene Identification. 1706, 233-254 (2018).
- Noble, A. J., et al. A validation of Illumina EPIC array system with bisulfite-based amplicon sequencing. PeerJ. 9, 10762 (2021).
- Tian, Y., et al. ChAMP: updated methylation analysis pipeline for Illumina BeadChips. Bioinformatics. 33, 3982-3984 (2017).
- Turinsky, A. L., et al. EpigenCentral: Portal for DNA methylation data analysis and classification in rare diseases. Human Mutation. 41 (10), 1722-1733 (2020).
- . The Chip Analysis Methylation Pipeline Available from: https://www.bioconductor.org/packages/release/bioc/vignettes/ChAMP/inst/doc/ChAMP.html (2020)
- Zhou, W., Laird, P. W., Shen, H. Comprehensive characterization, annotation and innovative use of Infinium DNA methylation BeadChip probes. Nucleic Acids Research. 45 (4), 22 (2017).
- Wanding, Z., Triche, T. J., Laird, P. W., Hui, S. SeSAMe: reducing artifactual detection of DNA methylation by Infinium BeadChips in genomic deletions. Nucleic Acids Research. 46 (20), 123 (2018).
- Heiss, J. A., Just, A. C. Improved filtering of DNA methylation microarray data by detection p values and its impact on downstream analyses. Clinical Epigenetics. 11, 15 (2019).
- Houseman, E. A., et al. DNA methylation arrays as surrogate measures of cell mixture distribution. BMC Bioinformatics. 13, 86 (2012).
- Valavanis, I., Sifakis, E. G., Georgiadis, P., Kyrtopoulos, S., Chatziioannou, A. A. A composite framework for the statistical analysis of epidemiological DNA methylation data with the Infinium human Methylation 450K BeadChip. IEEE Journal of Biomedical and Health Informatics. 18 (3), 817-823 (2014).
- Sun, N., Zhang, J., Zhang, C., Shi, Y., Zhao, B., Jiao, A., Chen, B. Using Illumina Infinium HumanMethylation 450K BeadChip to explore genomewide DNA methylation profiles in a human hepatocellular carcinoma cell line. Molecular Medicine Reports. 18 (5), 4446-4456 (2018).
- Moran, S., Arribas, C., Esteller, M. Validation of a DNA methylation microarray for 850,000 CpG sites of the human genome enriched in enhancer sequences. Epigenomics. 8 (3), 389-399 (2016).
- Bibikova, M., et al. High density DNA methylation array with single CpG site resolution. Genomics. 98 (4), 288-295 (2011).
- Lehne, B., et al. A coherent approach for analysis of the Illumina HumanMethylation450 BeadChip improves data quality and performance in epigenome-wide association studies. Genome Biology. 16 (1), 1-12 (2015).
- Wang, J., Zhang, H., Rezwan, F. I., Relton, C., Arshad, S. H., Holloway, J. W. Pre-adolescence DNA methylation is associated with BMI status change from pre- to post-adolescence. Clinical Epigenetics. 25, 64 (2021).
- Maugeri, A. The effects of dietary interventions on DNA methylation: implications for obesity management. International Journal of Molecular Sciences. 21, 8670 (2020).
- DeFuria, J., et al. B cells promote inflammation in obesity and type 2 diabetes through regulation of T-cell function and an inflammatory cytokine profile. Proceedings of the National Academy of Sciences. 110 (13), 5133-5138 (2013).
- Kietzmann, T., Petry, A., Shvetsova, A., Gerhold, J. M., Görlach, A. The epigenetic landscape related to reactive oxygen species formation in the cardiovascular system. British Journal of Pharmacology. 174, 1533-1554 (2017).
- Chase, K., Sharma, R. P. Epigenetic developmental programs and adipogenesis: implications for psychotropic induced obesity. Epigenetics. 8 (11), 1133-1140 (2013).
- Spalding, K. L., et al. Dynamics of fat cell turnover in humans. Nature. 453, 783-787 (2008).
- Ross, S. E., et al. Inhibition of adipogenesis by Wnt signaling. Science. 289, 950-953 (2000).
- Bagchi, D. P., et al. Wnt/β-catenin signaling regulates adipose tissue lipogenesis and adipocyte-specific loss is rigorously defended by neighboring stromal-vascular cells. Molecular Metabolism. 42, 101078 (2020).

