השימוש יחיד מולקולה פלורסנט ב באתרו הכלאה (SM-דג) כדי mRNAs Quantify ו Localize ב Oocytes מאתר
Summary
Reproducibly לספור את המספרים של mRNAs ב oocytes בודדים, מולקולה בודדת RNA פלורסצנטיות באתרו הכלאה (RNA-דג) היה אופטימיזציה עבור תאים שאינם מחסידי. Oocytes נאספו, hybridized עם הגששים ספציפית התעתיק, לכמת באמצעות תוכנה כימות של התמונה.
Abstract
שיטות בשימוש שגרתי לכמת mRNA oocytes, העוברים כוללים תגובת שרשרת של פולימראז הפוכה-תמלול דיגיטלי (dPCR), כמותיים, בזמן אמת RT-PCR (RT-qPCR), רצפי RNA. כאשר שיטות אלה נעשות באמצעות oocyte יחיד או העובר, נמוך-עותק mRNAs לא אמינה מזוהים. כדי להתגבר על בעיה זו, oocytes או עוברי יכול להיות איחדו יחד לניתוח; עם זאת, זה מוביל לעתים קרובות השתנות גבוהה בין הדגימות. ב פרוטוקול זה, אנו מתארים את השימוש זריחה בהכלאה באתרו (דגים) באמצעות הכימיה DNA מסועף. טכניקה זו מזהה התבנית המרחבי של mRNAs בתאים בודדים. כאשר הטכניקה זה משולב עם מציאת מקום ותוכנות מחשב מעקב, השפע של mRNAs בתא גם ניתן לכמת. בעזרת טכניקה זו, יש השתנות מופחתת בתוך קבוצת הניסוי, פחות oocytes, העוברים נדרשים לזהות הבדלים משמעותיים בין קבוצות הניסוי. SM-DNA זמינים מסחרית-דגים ערכות מוטבו לזהות mRNAs רקמות משרטוטי או תאים חסיד בשקופיות. עם זאת, oocytes אינן מתיישבות ביעילות על שקופיות, כמה ריאגנטים בערכה היו קשים מדי וכתוצאה מכך oocyte פירוק. כדי למנוע את פירוק, נעשו מספר שינויים לערכה דגים. באופן ספציפי, oocyte permeabilization ושטוף מאגרים המיועדים את immunofluorescence של oocytes, העוברים החליף את המאגרים קניינית. Permeabilization, שוטף, וכן incubations עם המחקרים וכל מגבר בוצעו ב- 6-ובכן צלחות, oocytes הונחו על שקופיות בסוף הפרוטוקול באמצעות מדיה הרכבה. שינויים אלה הצליחו להתגבר על המגבלות של ערכת זמינים מסחרית, בפרט, פירוק oocyte. כדי במדויק, reproducibly לספור את מספר mRNAs ב oocytes בודדים, שימש תוכנות מחשב. יחד, פרוטוקול זה מייצג חלופה PCR ורצף כדי להשוות את הביטוי של הפרוטוקולים ספציפי בתאים בודדים.
Introduction
רוורס טרנסקריפטאז תגובת שרשרת פולימראזית (PCR) כבר תקן זהב עבור כימות mRNA. שני מבחני, PCR (dPCR) דיגיטלי1 ו זמן אמיתי כמותיים PCR (qPCR)2 משמשים כיום. של שתי טכניקות PCR, dPCR יש רגישות רבה יותר מאשר qPCR רומז כי זה יכול לשמש כדי למדוד את שפע mRNA בתאים בודדים. עם זאת, בידיים שלנו, הפיק dPCR ניתוח של שפע נמוך mRNAs בבריכות של 5-10 oocytes לכל כל מדגם ניסיוני נתונים עם הפארמצבטית נמוך ווריאציה גבוהה3. . זה ככל הנראה בגלל השגיאה ניסיוני המשויך החילוץ-RNA ויעילות שעתוק במהופך. רצפי RNA גם בוצעה באמצעות עכבר אחת oocytes האנושי4,5. טכניקה זו דורשת cDNA הגברה השלבים הנדרשים עבור הדור ספריה אשר סביר להניח מגביר את השתנות בתוך קבוצת הניסוי. יתר על כן, שפע נמוך תעתיקים לא ניתן לזיהוי. למרות רצף המחירים ירדו בשנים האחרונות, הוא עדיין יכול להיות ושדורשת עקב העלות הגבוהה של ביואינפורמטיקה ניתוחים. לבסוף, mRNA לוקליזציה היא תהליך דינמי עם שינויים מרחביים התורמים חלבון פונקציה6. לכן, יצאנו לאמץ טכניקה היה לייצר אמצעי כמותית מדויקת לשחזור ולוקליזציה של הפרט mRNAs ב oocytes יחיד.
DNA מסועף מצמידים זריחה בהכלאה באתרו מגביר את האות זריחה במקום RNA/cDNA הגברה המאפשרת זיהוי mRNAs יחיד תאים בודדים- 7,–8,–9. הבדיקה מבוצעת דרך סדרה של הכלאה הגברה (באמצעות DNA קנים), קרינה פלואורסצנטית תיוג צעדים כדי להגביר את האות של קרינה פלואורסצנטית7. הטכניקה מתחילה עם קשירה של זוגות בדיקה oligonucleotide 18 – 25-לבסיס כי הם משלימים על ספציפיות mRNA3,8,10. 15-20 זוגות בדיקה מיועדים ירידה לפרטים הבטחת כל תורגם על-ידי היעד. הכלאה mRNA ספציפי ואחריו הגששים קדם מגבר, מגבר כי הטופס תצורה מסועף. כ, fluorophores תווית 400 לאגד כל מגבר, וכתוצאה מכך עלייה 8000-fold ב פלורסצנטיות המאפשר זיהוי של הפרט mRNAs (איור 1)11.
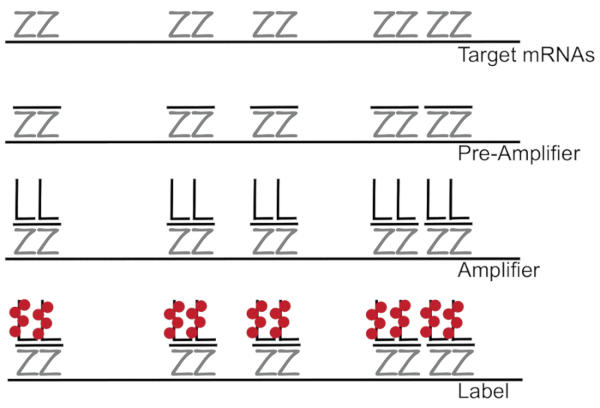
איור 1: סכימטי של פרוטוקול SM-דג- הכלאה רציפים של התעתיק בדיקה ספציפיים, כפועל DNA מגבר ו fluorophore ליעד mRNA מוצג. אנא לחץ כאן כדי להציג גירסה גדולה יותר של הדמות הזאת.
מחקרים קודמים באמצעות קרינה פלואורסצנטית מולקולה בודדת ב באתרו הכלאה (SM-דג) לשפות אחרות β-אקטין mRNAs נוירונים בודדים12 , וירוס הפפילומה האנושי DNA של סרטן צוואר הרחם תא קווים7. תוכנת מחשב במקום למצוא תוכנית מעקב אחר מזהה אות ניאון punctate בודדים, שימש בהצלחה כדי לכמת את מספר mRNAs כל3,תא13.
בהתבסס על התוצאות של גילוי mRNA נוירונים12, אנחנו שיערו כי SM-דג יוכיח כלי שימושי כדי quantitate רמות תורגם מאתר oocytes, העוברים כולל שפע נמוך mRNAs. עם זאת, הטכניקה ממוטבת לשימוש עם תאים קבוע חסיד, פורמלדהיד קבוע פרפין משובצים קטעי רקמה (FFPE). Oocytes לא יכולה לדבוק שקופית, גם כאשר הם מצופים פולי-L-ליזין. יתר על כן, הן שבירות יותר תאים סומטיים ומקטעים רקמות וכתוצאה מכך פירוק התא כאשר נתון של המאגרים קניינית ערכות זמינים מסחרית3. כדי להתגבר על האתגרים הללו, oocytes היו קבוע, מועברים באופן ידני בין טיפות של המאגרים. יתר על כן, מאגרי permeabilization ושטוף ערכות הוחלפו כדי להפחית את פירוק התא. שתגבש רגשים נרכשים לצד ערכת דגים או תעתיקים ספציפי ניתן לבקש. כל ערכת בדיקה קניינית זמין באחד בשלושה ערוצי קרינה פלואורסצנטית (C1, C2, C3) כדי לאפשר ריבוב. בניסוי הנוכחי, oocytes מאתר היו שהוכתמו כפול, כימות באמצעות בדיקה C2 Nanog ובדיקה C3 Pou5f1 . רגשים אלו נבחרו מבוסס על הביטוי המדווחת של Nanog , Pou5f1 oocytes, העוברים. בסיום השלבים הכלאה, oocytes היו ממוקמים בתוך טיפות אנטי-לדעוך הרכבה מדיה עבור יישום בשקופיות היסטולוגית. תמונות קונאפוקלית שימשו כדי לכמת את מספר punctate אותות פלואורסצנט אשר מייצגים mRNAs בודדים. בנוסף לכימות של mRNAs, ההדמיה הראתה גם את התפוצה המרחבית של ה-mRNA ספציפי בתא, אילו שיטות כימות אחרים של RNA הם הצליחו. להגיע להישגים. טכניקה זו הוכיח יש השתנות נמוך בתוך קבוצת הניסוי המאפשר שימוש מספר קטן יחסית של oocytes בכל קבוצה ניסיונית כדי לזהות הבדלים משמעותיים בין קבוצות הניסוי3.
Protocol
Representative Results
Discussion
סדרה של צעדים קלים במהלך הפרוטוקול יבטיח פלורסצנטיות מוצלחת וספירות מדויק של mRNAs. ראשית, הפרוטוקול חייב להתבצע מיד לאחר איסוף של קיבוע oocytes. שימו לב כי PVP נוסף למאגר קיבוע paraformaldehyde 4% כדי למנוע oocytes נצמדים אחד לשני. מצאנו כי יש צורך לבצע את הניסוי מיד אחרי אוסף קיבוע oocytes. כל עיכוב תוצאות הרבה נ…
Disclosures
The authors have nothing to disclose.
Acknowledgements
אנו מודים ד ר דניאל ר לארסון לעזרתו נדיב עם ההתקנה ואת השימוש מציאת נקודה, מעקב אחר תוכנית 13 ותמיכה טכנית של אוניברסיטת נברסקה לינקולן מיקרוסקופ הליבה עבור ההדמיה מיקרוסקופיה קונפוקלית. מחקר זה מייצג תרומה של האוניברסיטה של אגף המחקר החקלאי נבראסקה, לינקולן, נברסקה, נתמך על ידי קרנות הפתח UNL (נב-26-206/ההצטרפות-232435 ומספר נאב-26-231/ההצטרפות-1013511).
Materials
| (±)-α-Lipoic acid | Sigma-Aldrich | T1395 | Alpha Lipoic Acid |
| Albumin, Bovine Serum, Low Fatty Acid | MP Biomedicals, LLC | 199899 | FAF BSA |
| BD 10mL TB Syringe | Becton, Dickinson and Company | 309659 | 10 mL syringe |
| BD PrecisionGlide Needle | Becton, Dickinson and Company | 305109 | 27 1/2 gauge needle |
| Calcium chloride dihydrate | Sigma-Aldrich | C7902 | CaCl2-2H2O |
| Citric acid | Sigma-Aldrich | C2404 | Citrate |
| D-(+)-Glucose | Sigma-Aldrich | G6152 | Glucose |
| Disodium phosphate | Na2HPO4 | ||
| Easy Grip Petri Dish | Falcon Corning | 351008 | 35 mm dish |
| Edetate Disodium | Avantor | 8994-01 | EDTA |
| Extra Fine Bonn Scissors | Fine Science Tools | 14084-08 | Straight, Sharp/Sharp, non-serrated, 13mm cutting edge scissors |
| Fetal Bovine Serum | Atlanta biologicals | S10250 | FBS |
| Gentamicin Reagent Solution | gibco | 15710-064 | Gentamicin |
| GlutaMAX-I (100X) | gibco | 35050-061 | Glutamax |
| Gold Seal Micro Slides | Gold Seal | 3039 | 25 x 75mm slides |
| Gonadotropin, From Pregnant Mares' Serum | Sigma | G4877 | eCG |
| hCG recombinant | NHPP | AFP8456A | hCG |
| Hyaluronidase, Type IV-S: From Bovine Testes | Sigma-Aldrich | H3884 | Hyaluronidase |
| Jewelers Style Forceps | Integra | 17-305X | Forceps 4-3/8", Style 5F, Straight, Micro Fine Jaw |
| L-(+)-Lactic Acid, free acid | MP Biomedicals, LLC | 190228 | L-Lactate |
| Magnesium sulfate heptahydrate | Sigma-Aldrich | M2773 | MgSO4-7H2O |
| MEM Nonessential Amino Acids | Corning | 25-025-Cl | NEAA |
| Microscope Cover Glass | Fisher Scientific | 12-542-C | 25 x 25x 0.15 mm cover slips |
| Mm-Nanog-O2-C2 RNAscope Probe | Advanced Cell Diagnostics | 501891-C2 | Nanog Probe |
| Mm-Pou5f1-O1-C3 RNAscope Probe | Advanced Cell Diagnostics | 501611-C3 | Pou5f1 Probe |
| MOPS | Sigma-Aldrich | M3183 | |
| Paraformaldehyde | Sigma-Aldrich | P6148 | Paraformaldehyde |
| PES 0.22 um Membrane -sterile | Millex-GP | SLGP033RS | 0.22 um filters |
| Polyvinylpyrrolidone | Sigma-Aldrich | P0930 | PVP |
| Potassium chloride | Sigma-Aldrich | 60128 | KCl |
| Potassium phosphate monobasic | Sigma-Aldrich | 60218 | KH2PO4 |
| Prolong Gold antifade reagent | invitrogen | P36934 | Antifade reagent without DAPI |
| RNAscope DAPI | Advanced Cell Diagnostics | 320858 | DAPI |
| RNAscope FL AMP 1 | Advanced Cell Diagnostics | 320852 | Amplifier 1 |
| RNAscope FL AMP 2 | Advanced Cell Diagnostics | 320853 | Amplifier 2 |
| RNAscope FL AMP 3 | Advanced Cell Diagnostics | 320854 | Amplifier 3 |
| RNAscope FL AMP 4 ALT A | Advanced Cell Diagnostics | 320855 | Amplifier 4 ALT A |
| RNAscope FL AMP 4 ALT B | Advanced Cell Diagnostics | 320856 | Amplifier 4 ALT B |
| RNAscope FL AMP 4 ALT C | Advanced Cell Diagnostics | 320857 | Amplifier 4 ALT C |
| RNAscope Fluorescent Multiplex Detection Reagents Kit | Advanced Cell Diagnostics | 320851 | FISH Reagent Kit |
| RNAscope Probe 3-plex Negative Control Probe | Advanced Cell Diagnostics | 320871 | Negative Control |
| RNAscope Probe 3-plex Positive Control | Advanced Cell Diagnostics | 320881 | Positive Control |
| RNAscope Probe Diluent | Advanced Cell Diagnostics | 300041 | Probe Diluent |
| RNAscope Protease III | Advanced Cell Diagnositics | 322337 | Protease III |
| RNAscope Protease III & IV Reagent Kit | Advanced Cell Diagnostics | 322340 | FISH Protease Kit |
| RNAscope Protease IV | Advanced Cell Diagnostics | 322336 | Protease IV |
| S/S Needle with Luer Hub 30G | Component Supply Co. | NE-301PL-50 | blunt 30 gauge needle |
| Sodium bicarbonate | Sigma-Aldrich | S6297 | NaHCO3 |
| Sodium chloride | Sigma-Aldrich | S6191 | NaCl |
| Sodium hydroxide | Sigma-Aldrich | 306576 | NaOH |
| Sodium pyruvate, >= 99% | Sigma-Aldrich | P5280 | Pyruvate |
| Solution 6 Well Dish | Agtechinc | D18 | 6 well dish |
| Taurine | Sigma-Aldrich | T8691 | Taurine |
| Tissue Culture Dish | Falcon Corning | 353002 | 60 mm dish |
| Triton X-100 | Sigma-Aldrich | X100 | Triton X-100 |
References
- Vogelstein, B., Kinzler, K. W. Digital PCR. Proceedings of the National Academy of Sciences. 96 (16), 9236-9241 (1999).
- MacK, E. M., Smith, J. E., Kurz, S. G., Wood, J. R. CAMP-dependent regulation of ovulatory response genes is amplified by IGF1 due to synergistic effects on Akt phosphorylation and NF-kB transcription factors. Reproduction. 144 (5), 595-602 (2012).
- Xie, F., Timme, K. A., Wood, J. R. Using Single Molecule mRNA Fluorescent in Situ Hybridization (RNA-FISH) to Quantify mRNAs in Individual Murine Oocytes and Embryos. Scientific Reports. 8 (1), 7930 (2018).
- Ruebel, M. L., et al. Obesity modulates inflammation and lipidmetabolism oocyte gene expression: A single-cell transcriptome perspective. Journal of Clinical Endocrinology and Metabolism. 102 (6), 2029-2038 (2017).
- Borensztein, M., Syx, L., Servant, N., Heard, E. . Mouse Oocyte Development. 1818, 51-65 (2018).
- Jansova, D., Tetkova, A., Koncicka, M., Kubelka, M., Susor, A. Localization of RNA and translation in the mammalian oocyte and embryo. PLoS ONE. 13 (3), 1-25 (2018).
- Player, A. N., Shen, L. P., Kenny, D., Antao, V. P., Kolberg, J. A. Single-copy gene detection using branched DNA (bDNA) in situ hybridization. Journal of Histochemistry and Cytochemistry. 49 (5), 603-611 (2001).
- Wang, F., et al. RNAscope: A novel in situ RNA analysis platform for formalin-fixed, paraffin-embedded tissues. Journal of Molecular Diagnostics. 14 (1), 22-29 (2012).
- Itzkovitz, S., van Oudenaarden, A. Validating transcripts with probes and imaging technology. Nature Methods. 8 (4), S12-S19 (2011).
- Derti, A., et al. ProbeDesigner: for the design of probesets for branched DNA (bDNA) signal amplification assays. Bioinformatics. 15 (5), 348-355 (1999).
- Larson, B., Malayter, D., Shure, M. Multiplexed Detection of Cytokine Cancer Biomarkers using Fluorescence RNA In Situ Hybridization and Cellular Imaging. BioTek Application Notes. , 1-5 (2016).
- Buxbaum, A. R., Wu, B., Singer, R. H. Single β-Actin mRNA Detection in Neurons Reveals a Mechanism for Regulating Its Translatability. Science. 343 (6169), 419-422 (2014).
- Thompson, R. E., Larson, D. R., Webb, W. W. Precise nanometer localization analysis for individual fluorescent probes. Biophysical Journal. 82 (5), 2775-2783 (2002).
- Herrick, J. R., Paik, T., Strauss, K. J., Schoolcraft, W. B., Krisher, R. L. Building a better mouse embryo assay: effects of mouse strain and in vitro maturation on sensitivity to contaminants of the culture environment. Journal of Assisted Reproduction and Genetics. 33 (2), 237-245 (2016).
- Pohlmeier, W. E., Xie, F., Kurz, S. G., Lu, N., Wood, J. R. Progressive obesity alters the steroidogenic response to ovulatory stimulation and increases the abundance of mRNAs stored in the ovulated oocyte. Molecular Reproduction and Development. 81 (8), 735-747 (2014).
- Xie, F., Anderson, C. L., Timme, K. R., Kurz, S. G., Fernando, S. C., Wood, J. R. Obesity-dependent increases in oocyte mRNAs are associated with increases in proinflammatory signaling and gut microbial abundance of lachnospiraceae in female mice. Endocrinology. 157 (4), 1630-1643 (2016).
- Hirao, Y., Yanagimachi, R. Detrimental effect of visible light on meiosis of mammalian eggs in vitro. Journal of Experimental Zoology. , (1978).
- Takenaka, M., Horiuchi, T., Yanagimachi, R. Effects of light on development of mammalian zygotes. Proceedings of the National Academy of Sciences. 104 (36), 14293-14293 (2007).
- Komminoth, P., Werner, M. Target and signal amplification: Approaches to increase the sensitivity of in situ hybridization. Histochemistry and Cell Biology. 108 (4-5), 325-333 (1997).
- Hornick, J. E., Duncan, F. E., Shea, L. D., Woodruff, T. K. Multiple follicle culture supports primary follicle growth through paracrine-acting signals. Reproduction. 145 (1), 19-32 (2013).
- Vlasova-St. Louis, I., Bohjanen, P. Feedback Regulation of Kinase Signaling Pathways by AREs and GREs. Cells. 5 (1), 4 (2016).
- Gilbert, C., Svejstrup, J. Q. RNA Immunoprecipitation for Determining RNA-Protein Associations In Vivo. Current Protocols in Molecular Biology. 75 (1), 27.4.1-27.4.11 (2006).
- Kwon, S., Chin, K., Nederlof, M., Gray, J. W. Quantitative, in situ analysis of mRNAs and proteins with subcellular resolution. Scientific Reports. 7 (1), 16459 (2017).
- Voigt, F., et al. Single-Molecule Quantification of Translation-Dependent Association of mRNAs with the Endoplasmic Reticulum. Cell Reports. 21 (13), 3740-3753 (2017).
- Halstead, J. M., Wilbertz, J. H., Wippich, F., Lionnet, T., Ephrussi, A., Chao, J. A. TRICK: A Single-Molecule Method for Imaging the First Round of Translation in Living Cells and Animals. Methods in Enzymology. 572, (2016).
- Cookson, W., Liang, L., Abecasis, G., Moffatt, M., Lathrop, M. Mapping complex disease traits with global gene expression. Nature Reviews Genetics. 10 (3), 184-194 (2009).
- Houle, D., Govindaraju, D. R., Omholt, S. Phenomics: the next challenge. Nature Reviews Genetics. 11, 855 (2010).
- Freimer, N., Sabatti, C. The Human Phenome Project. Nature Genetics. 34, 15 (2003).

